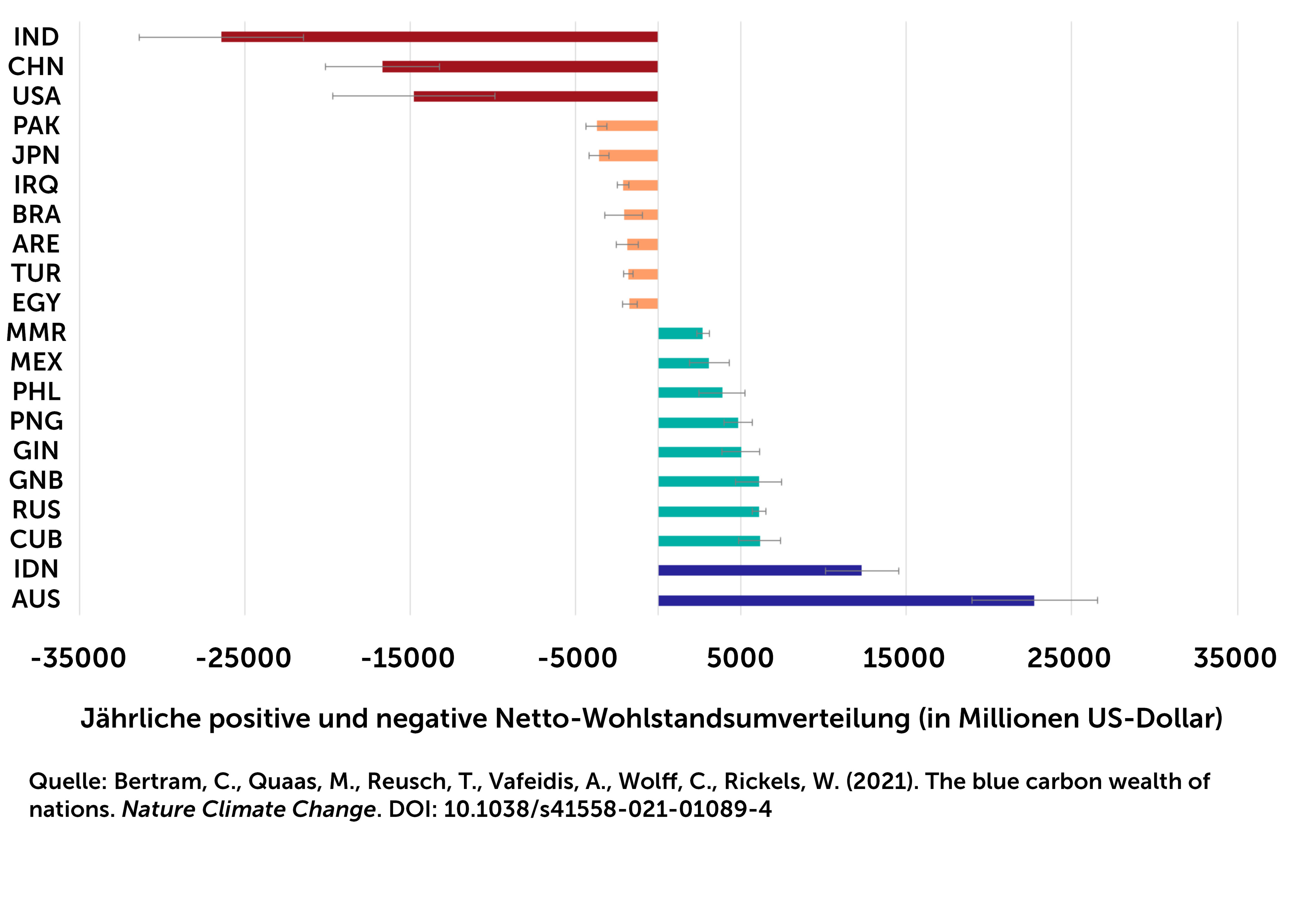
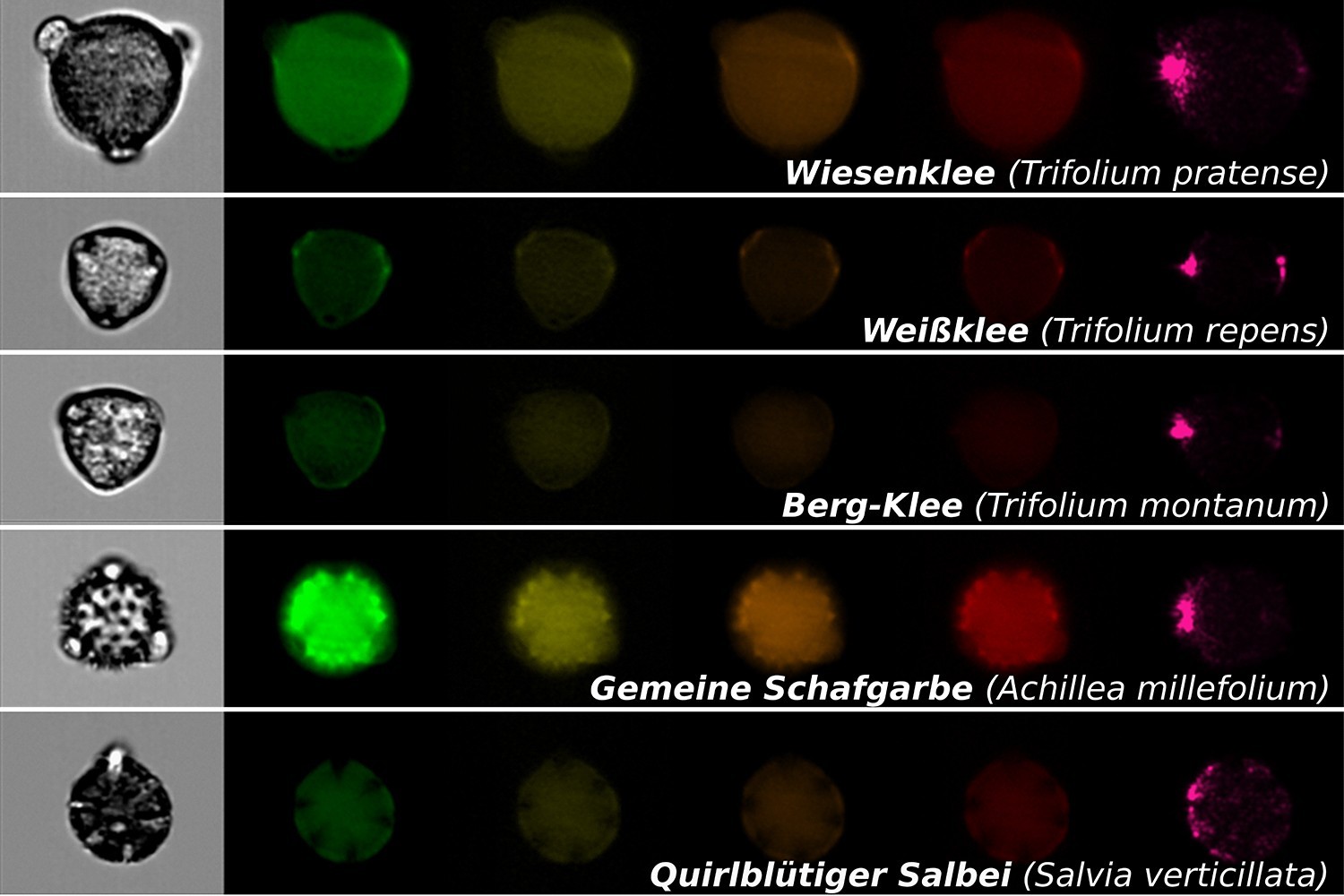
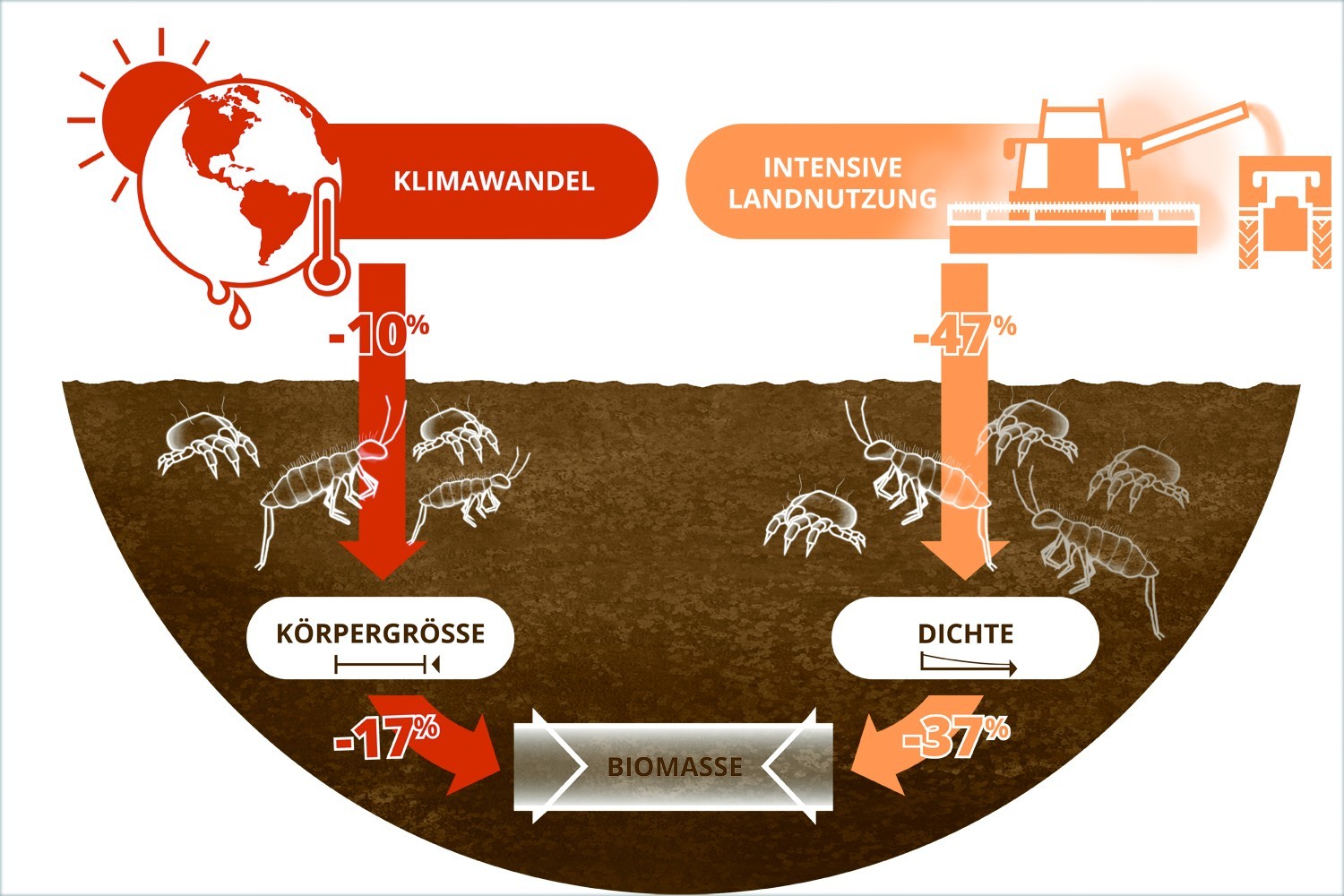
09.07.2025 | Biodiversitätstheorie, Experimentelle Interaktionsökologie, iDiv, Medienmitteilung
Die Mischung macht’s: Vielfältige Baumpflanzungen fördern Ökosystemleistungen im Wald
Mehr08.07.2025 | Biodiversität und Mensch, Forschung, iDiv, Medienmitteilung
Menschen können Biodiversität wahrnehmen
Mehr19.06.2025 | iDiv, Medienmitteilung, UFZ-News
Die Rolle von Forschenden in politischen Debatten
Mehr19.06.2025 | iDiv, iDiv, Medienmitteilung
Vererbung nach eigenen Regeln: Die scheinbar unmögliche Fortpflanzung der Hundsrosen
Mehr16.06.2025 | Biodiversität und Naturschutz, Medienmitteilung, Science-Policy
Rewilding auf landwirtschaftlich genutzten Flächen
Mehr10.06.2025 | Experimentelle Interaktionsökologie, iDiv, Medienmitteilung
iDiv-Forschungsgruppe Experimentelle Interaktionsökologie als „Bestes Forschungsumfeld“ ausgezeichnet
Mehr02.06.2025 | Biodiversität und Naturschutz, Forschung, iDiv, Medienmitteilung, Science-Policy
Kulturelles Erbe erhalten, Lebensräume schützen: Ehemalige Dorfstrukturen bieten Zufluchtsorte für Amphibien
Mehr26.05.2025 | iDiv, iDiv, Medienmitteilung, Medienmitteilung, MLU News, MLU News
Studie zum Wissenstransfer: Wie der „Gollum-Effekt“ Forschung und Karrieren behindert
Mehr19.05.2025 | iDiv, iDiv-Mitglieder, Medienmitteilung
Erstes bundesweites Bürgerwissenschaftsprojekt GartenDiv gestartet
Mehr15.05.2025 | iDiv, iDiv, Medienmitteilung
Sollten wir nicht-einheimische Arten schützen? Eine neue Studie sagt: vielleicht
Mehr
15.05.2025 | iDiv, Medienmitteilung
Cooper Award würdigt iDiv-Publikation zur taxonomischen Harmonisierung in der Biodiversitätsforschung
Mehr05.05.2025 | Biodiversität und Mensch, Medienmitteilung
Citizen-Science-Projekt FLOW startet in zweite Förderphase
Mehr30.04.2025 | Biodiversität und Naturschutz, Medienmitteilung
Vom Vorgarten zum Kontinent: Warum die Artenvielfalt von klein nach groß nicht gleichmäßig zunimmt
Mehr17.04.2025 | Forschung, iDiv, Medienmitteilung
Nährstoffe verändern die Wirkung von Niederschlägen auf das Pflanzenwachstum
Regen und Schnee erhöhen das Pflanzenwachstum. Diese Beziehung ist umso stärker je mehr Nährstoffe verfügbar sind.
Mehr11.04.2025 | Biodiversitätstheorie, Forschung, iDiv, Medienmitteilung
„Internet der Natur” – Einblicke in die verborgenen Netzwerke des Lebens
Mehr10.04.2025 | Blog Post
Auf dem Weg zu Gleichberechtigung in der Forschung: Erkenntnisse der iDiv Female Scientists-Initiative
Mehr03.04.2025 | iDiv, Medienmitteilung
Neuer Podcast “Inside Biodiversity”
Inside Biodiversity ist ein neuer iDiv-Podcast.
Mehr03.04.2025 | Arten-Interaktionsökologie, Forschung, iDiv, Medienmitteilung
Dark Diversity – die bislang unbekannte Seite der Pflanzenvielfalt
Nature-Studie befasst sich mit verborgenen Auswirkungen menschlicher Aktivitäten auf die Natur
Mehr27.03.2025 | Forschung, iDiv, Medienmitteilung, sDiv
Wie Samenpflanzen sich über Jahrmillionen verbreiten
Mehr24.03.2025 | Experimentelle Interaktionsökologie, iDiv-Mitglieder, Medienmitteilung
Hohe Baumarten-Vielfalt mindert Hitze in Wäldern
Mehr20.03.2025 | Experimentelle Interaktionsökologie, Forschung, Medienmitteilung
Ressourceneffiziente Baumarten wachsen schneller unter realen Bedingungen, laut neuer Studie
Mehr13.03.2025 | Biodiversitätssynthese, Biodiversitätssynthese, Forschung, iDiv, Medienmitteilung, Medienmitteilung, Forschung
Studie widerspricht umstrittener These zur Lebensraumfragmentierung
Mehr11.03.2025 | Blog Post, iDiv, sDiv
Der Artenvielfalt in der Ukraine auf der Spur
Wie eine sDiv-Kooperation dazu beitrug, ukrainische Wissenschaftlerinnen und Wissenschaftler wieder zusammenzubringen und ihnen ein Umfeld der Stabilität, der Fokussierung und des wissenschaftlichen Austauschs bot.
Mehr05.03.2025 | Forschung, iDiv, Medienmitteilung
Satellitenbilder liefern neue Erkenntnisse über Tropenwälder
New Nature paper: satellite images from space are allowing scientists to delve deeper into the individual functions of different tropical forest canopies.
Mehr05.03.2025 | Biodiversität und Naturschutz, iDiv, Medienmitteilung
Die Zukunft des Naturschutzes in Europa
Konzepte für ein widerstandsfähiges und zusammenhängendes transeuropäisches Naturnetz
Mehr27.02.2025 | Blog Post, Blog Post, sDiv, sDiv, TOP NEWS
50.000 sDiv-Zitationen – 12 Jahre Exzellenz in der Biodiversitätsforschung
Mehr19.02.2025 | Experimentelle Interaktionsökologie, iDiv, Medienmitteilung
Grüter-Preis für Translating Soil Biodiversity
Der Preis für Wissenschaftsvermittlung 2025 der Werner und Inge Grüter-Stiftung geht an das Projekt „Translating Soil Biodiversity“.
Mehr
29.01.2025 | Biodiversitätssynthese, Biodiversitätstheorie, Medienmitteilung
Der Klimawandel mischt die Arten neu wie ein Kartenspiel
Eine neue Studie zeigt, dass sich die Biodiversität dort schneller verändert hat, wo sich auch die Temperaturen schneller verändert haben.
Mehr
15.01.2025 | Forschung, iDiv-Mitglieder, Medienmitteilung
Unbekannte Verwandte aufspüren: Genetische Verbindungen in Tierpopulationen
Mehr13.01.2025 | Biodiversität und Mensch, iDiv, Medienmitteilung
Perspektive: Baumkulturen sind der Schlüssel zur Förderung der nachhaltigen Entwicklungsziele
Mehr09.01.2025 | Biodiversität und Naturschutz, iDiv-Mitglieder, Medienmitteilung
Schimpansen sind genetisch an Lebensräume und Infektionen angepasst
Mehr
18.12.2024 | Biodiversität und Funktionen des Bodens, iDiv-Mitglieder, Medienmitteilung
Anton Potapov erhält ERC Consolidator Grant
Mit dem Förderpreis wird das Forschungsprojekt des iDiv-Mitglieds mit rund zwei Millionen Euro finanziert
Mehr04.12.2024 | Experimentelle Interaktionsökologie, Medienmitteilung, TOP NEWS
Überlebensstrategien winziger Bodenlebewesen aufgedeckt
Neue Studie in Nature zeigt, wie Bodenmikroben durch extreme Wetterereignisse beeinflusst werden, und bietet neue Einblicke in die Gefahren des Klimawandels.
Mehr03.12.2024 | iDiv-Mitglieder, MLU News, TOP NEWS
Ökosysteme: Neue Studie hinterfragt gängige Annahme zur biologischen Vielfalt
Pflanzenarten können innerhalb eines Ökosystems ähnliche Funktionen erfüllen, unabhängig davon, wie eng verwandt sie miteinander sind.
Mehr19.11.2024 | Experimentelle Interaktionsökologie, Medienmitteilung, TOP NEWS, Unkategorisiert
Bodenökosystem ist bei extensiver Bewirtschaftung widerstandsfähiger
Forschende untersuchten Auswirkungen intensiver und extensiver Landnutzung auf Vielfalt der Bodenlebewesen in Acker- und Grünlandflächen
Mehr12.11.2024 | Medienmitteilung, TOP NEWS
Ressource Wald: Wie Wälder verschiedenen Anforderungen gerecht werden
Forschungsteam analysiert Folgen der Anreicherung von Buchenwäldern mit Nadelbäumen
Mehr10.10.2024 | iDiv-Mitglieder, Medienmitteilung, sDiv, TOP NEWS
Europäische Waldpflanzen wandern gen Westen, Stickstoffeinträge Hauptursache
Basierend auf einer Medienmitteilung der Universität Ghent
Mehr01.10.2024 | Forschung, Medienmitteilung, Science-Policy, TOP NEWS
Faktencheck Artenvielfalt zeigt, wie es um die biologische Vielfalt in Deutschland steht
Mehr als die Hälfte der Lebensraumtypen in Deutschland weist einen ökologisch ungünstigen Zustand auf
Mehr01.10.2024 | iDiv, Medienmitteilung, TOP NEWS
Neue iDiv-Phase: Biodiversitätsforschung in Mitteldeutschland verstetigt
Das Deutsche Zentrum für integrative Biodiversitätsforschung (iDiv) startet zum 1. Oktober in eine neue Phase mit neuer Grundfinanzierung, neuer Geschäftsführerin und einer neuen Forschungsgruppe.
Mehr17.09.2024 | iDiv-Mitglieder, Medienmitteilung, TOP NEWS
Pollen beeinflussen Wolkenbildung und Niederschlagsmuster
Neue Studie zeigt klimarelevante Effekte
Mehr
16.09.2024 | Medienmitteilung, MLU News, TOP NEWS
Pflanzen, Ökosysteme und der Klimawandel: 600 Forschende treffen sich an der Universität Halle
Deutschen Botanischen Gesellschaft tagt vom 15. bis 19. September
Mehr10.09.2024 | iDiv-Mitglieder, Medienmitteilung, TOP NEWS
Großflächige Waldrodung verringert Wolkenbildung
Forschende sprechen von gravierenden Auswirkungen auf das Klima
Mehr09.09.2024 | Biodiversitätssynthese, Medienmitteilung, MLU News, TOP NEWS
Inselleben lässt Tiere langsamer werden
Vögel und Säugetiere auf Inseln haben einen langsameren Stoffwechsel als ihre Verwandten auf dem Festland
Mehr06.09.2024 | Biodiversitätsökonomik, Medienmitteilung, TOP NEWS
Graduiertenkolleg ECO-N gestartet
Promovierende forschen zu nachhaltiger Entwicklung
Mehr27.08.2024 | Experimentelle Interaktionsökologie, Forschung, Medienmitteilung, TOP NEWS
Umweltstressoren schwächen die Widerstandsfähigkeit von Ökosystemen
Je höher der Umweltstress, desto geringer die Widerstandsfähigkeit gegenüber globalen Veränderungen
Mehr21.08.2024 | Forschung, iDiv-Mitglieder, Medienmitteilung, TOP NEWS
Studie: Honigbienen fliegen auf Biolandwirtschaft
A new study reveals how farming practices affect colony health.
Mehr07.08.2024 | iDiv, Medienmitteilung, TOP NEWS
Wie können wir Vielfalt, Gerechtigkeit und Integration in der Biodiversitätsforschung weltweit fördern?
Ganzheitlicher Ansatz bietet konkrete Strategien für Forschende, Forschungs- und Fördermitteleinrichtungen sowie Herausgeber
Mehr
22.07.2024 | Medienmitteilung, TOP NEWS, UFZ-News
Weniger produktiv, aber stabiler
Extensiv genutztes Grünland kommt besser mit den Folgen des Klimawandels zurecht
Mehr09.07.2024 | Forschung, iDiv-Mitglieder, Medienmitteilung, TOP NEWS
Mit Pflanzen-App die Folgen des Klimawandels verstehen
Leipzig. Ein Forschungsteam unter der Leitung des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) und der Universität Leipzig hat einen Algorithmus entwickelt, der Beobachtungsdaten der App Flora Incognita analysiert. Daraus lassen sich ökologische Muster ableiten, die Aufschluss über die Auswirkungen des Klimawandels auf die Pflanzenwelt geben. Die Studie wurde im Fachmagazin Methods in Ecology and Evolution veröffentlicht.
Mehr02.07.2024 | Biodiversität und Mensch, Biodiversität und Naturschutz, iDiv, Medienmitteilung, Science-Policy, TOP NEWS
Was braucht es für ein besseres Biodiversitäts-Monitoring in Europa?
Basiert auf einer Medienmitteilung von IIASA Wissenschaftlerinnen und Wissenschaftler des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) und des Internationalen Instituts für Angewandte Systemanalyse (IIASA) haben gemeinsam mit vielen weiteren Partnern untersucht, wie es um das Biodiversitätsmonitoring in Europa bestellt ist. In der Fachzeitschrift Conservation Letters geben sie wichtige Einblicke in politische Erfordernisse, Herausforderungen und zukünftige Lösungsansätze.
Mehr26.06.2024 | Biodiversität und Naturschutz, Medienmitteilung, TOP NEWS
Lückenhaftes Wissen zur Biodiversität in den tropischen Anden
Mehr25.06.2024 | iDiv, Medienmitteilung, Science-Policy, TOP NEWS
Deutschlands Führungsrolle in der Biodiversitäts-Forschung und -Politik
Mehr17.06.2024 | Experimentelle Interaktionsökologie, Medienmitteilung, TOP NEWS
Bodenfauna könnte die Kohlenstoffspeicherung im Boden grundlegend verändern
Mehr13.06.2024 | Biodiversitätsökonomik, Experimentelle Interaktionsökologie, iDiv-Mitglieder, Medienmitteilung, Physiologische Diversität, TOP NEWS
Flächenmanagement und Klimawandel beeinträchtigen mehrere Agrarland-Ökosystemleistungen gleichzeitig
Eine neue Studie, die in der Fachzeitschrift Nature Communications veröffentlicht wurde, zeigt, dass Grün- und Ackerland besser verschiedene Leistungen gleichzeitig erbringen könnten, wenn der Einsatz von Pflanzenschutzmitteln und mineralischen Düngemitteln verringert wird.
Mehr30.04.2024 | iDiv, Medienmitteilung, TOP NEWS
Extensive Beweidung: gut für die lokale Biodiversität, aber herausfordernd für Landnutzer
Ein Forschungsteam unter Leitung des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv), der Universität Leipzig (UL) und des Helmholtz-Zentrums für Umweltforschung (UFZ) hat untersucht, mit welcher Motivation Landnutzer in Europa eine extensive Beweidung betreiben und welchen Herausforderungen sie gegenüberstehen. Die Ergebnisse der Befragungen wurden im Fachmagazin Land Use Policy veröffentlicht. Sie zeigen, dass flexiblere Förderbedingungen zu einer Verbesserung beitragen könnten.
Mehr26.04.2024 | Biodiversität und Naturschutz, iDiv-Mitglieder, Medienmitteilung, TOP NEWS
Der Klimawandel könnte Hauptgrund für den Rückgang biologischer Vielfalt werden
Mehr23.04.2024 | Forschung, iDiv-Mitglieder, Medienmitteilung, TOP NEWS
Studie zeigt, wie Pflanzen das Klima in Europa beeinflussen
Basiert auf einer Medienmitteilung der Martin-Luther-Universität Halle-Wittenberg Das Klima reguliert das Pflanzenwachstum, aber das Klima wird auch von Pflanzen beeinflusst. Je nach Pflanzenmix haben Ökosysteme sogar einen starken Einfluss auf das Klima in Europa, wie eine Studie der Martin-Luther-Universität Halle-Wittenberg (MLU) und des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) im Journal Global Change Biology zeigt. Die Forschenden verknüpften Satellitendaten mit rund 50.000 Vegetationsaufnahmen aus ganz Europa. Gut fünf Prozent der regionalen Klimaregulation lassen sich durch die Pflanzenvielfalt vor Ort erklären. Die Analyse zeigt zudem, dass die Effekte von vielen weiteren Faktoren abhängen. Pflanzen beeinflussen das Klima, indem sie Sonnenlicht reflektieren oder durch Verdunstung ihre Umgebung abkühlen.
Mehr18.04.2024 | Experimentelle Interaktionsökologie, iDiv, Medienmitteilung, TOP NEWS
iDiv-Forschungsgruppenleiter Nico Eisenhauer neues Mitglied der Leopoldina
Mehr17.04.2024 | Biodiversität und Naturschutz, Medienmitteilung, TOP NEWS
„Rewilding“ Amphibien: Schutz von gefährdeten Arten für die ökologische Wiederherstellung
Mehr03.04.2024 | Biodiversität und Naturschutz, Forschung, iDiv, Medienmitteilung, TOP NEWS
Abbau kritischer Rohstoffe bedroht Menschenaffen in Afrika
Eine neue Studie unter Leitung von Wissenschaftlerinnen und Wissenschaftlern des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv), der Martin-Luther-Universität Halle-Wittenberg (MLU) und der Naturschutzorganisation Re:wild zeigt, dass die Bedrohung von Menschenaffen in Afrika durch den Bergbau bislang deutlich unterschätzt wurde. Die Ergebnisse der Untersuchung wurden im Fachjournal Science Advances veröffentlicht.
Mehr02.04.2024 | Medienmitteilung, TOP NEWS
iDiv trauert um Diana Wall
Diana Wall verstarb am 25. März 2024. Die international geachtete Umweltwissenschaftlerin und Bodenökologin war langjähriges Mitglied des Wissenschaftlichen Beirats von iDiv und an mehreren Forschungsprojekten zur Bodenbiodiversität beteiligt.
Mehr28.03.2024 | Medienmitteilung, TOP NEWS
Rangordnung hinterlässt genetische Spuren: Wie der soziale Status das Erbgut von Tüpfelhyänen beeinflusst
Basiert auf einer Medienmitteilung des Leibniz-Instituts für Zoo- und Wildtierforschung (Leibniz-IZW) Forschende des Deutschen Zentrums für Biodiversitätsforschung (iDiv) Halle-Jena-Leipzig und des Leibniz-Instituts für Zoo- und Wildtierforschung (Leibniz-IZW) weisen in einer Untersuchung an jungen und erwachsenen freilebenden Tüpfelhyänen nach, dass sich Sozialverhalten und sozialer Status durch epigenetische Mechanismen auf molekularer Ebene im Erbgut niederschlagen. Die in der Fachzeitschrift Communications Biology veröffentlichten Ergebnisse tragen dazu bei, die Rolle epigenetischer Mechanismen im Zusammenspiel von sozialen, ökologischen und physiologischen Faktoren im Leben eines sozialen Säugetiers besser zu verstehen.
Mehr26.03.2024 | Biodiversität und Naturschutz, Medienmitteilung, MLU News, TOP NEWS
Was haben Vögel und Flüsse mit Euroscheinen zu tun?
Basiert auf einem Beitrag in Campus Hallensis, dem Campus-Magazin der Martin-Luther-Universität Halle-Wittenberg (MLU) Wenn es nach Prof. Dr. Henrique Pereira geht, tragen die Menschen in Europa künftig ein Stück Biodiversität im Geldbeutel. Der Ökologe ist Teil der „Motifs Advisory Group“ der Europäischen Zentralbank (EZB). Ihre Aufgabe ist es, Motive vorzuschlagen, die auf der nächsten Generation der Euronoten zu sehen sind.
Mehr14.03.2024 | Forschung, Medienmitteilung, Science-Policy, TOP NEWS
Citizen Science-Projekt FLOW zeigt: Kleine Bäche in Deutschland sind in keinem guten ökologischen Zustand
Basiert auf einer Medienmitteilung des Helmholtz-Zentrums für Umweltforschung (UFZ) Pflanzenschutzmittel sichern Erträge in der Landwirtschaft, indem sie schädliche Insekten, Pilze und Unkräuter bekämpfen. Sie gelangen aber auch in benachbarte Bäche und schädigen dort Lebensgemeinschaften, die für den Erhalt der Artenvielfalt entscheidend sind, Teil des Nahrungsnetzes sind und die Selbstreinigung des Wassers unterstützen. Vor allem für kleine Fließgewässer fehlen jedoch bislang belastbare Daten, die Auskunft darüber geben, wie es um sie wirklich bestellt ist. Im Citizen Science-Projekt FLOW haben 900 Bürgerforschende über drei Jahre lang in ganz Deutschland kleine Fließgewässer auf ihren ökologischen Zustand untersucht. Das Projekt wurde vom Bund für Umwelt und Naturschutz Deutschland (BUND) gemeinsam mit dem Helmholtz-Zentrum für Umweltforschung (UFZ) und dem Deutschen Zentrum für integrative Biodiversitätsforschung (iDiv) Halle-Jena-Leipzig durchgeführt. Die Daten zeigen: In der Mehrheit der untersuchten Bäche, die durch eine landwirtschaftlich geprägte Landschaft fließen, ist die Wirbellosenfauna durch Pflanzenschutzmittel gestört, zudem weisen die Fließgewässer eine stark veränderte morphologische Struktur auf. Das Projekt bestätigt darüber hinaus, dass Bürgerforschung auch im Bereich der Gewässerökologie dringend benötigte Daten in hoher Qualität liefern kann.Auf Flüsse als wertvolle Lebensräume will auch der internationale Tag der Flüsse am 14. März 2024 aufmerksam machen und ruft zu deren Schutz auf.
Mehr27.02.2024 | Biodiversitätstheorie, Medienmitteilung, TOP NEWS
Fische könnten aussterben, wenn sie aufgrund steigender Temperaturen ihr Jagdverhalten ändern
Mehr23.02.2024 | Medienmitteilung, sDiv, TOP NEWS
Wie viel Natur steckt im internationalen Handel?
Forschende haben einen neuen Ansatz entwickelt, mit dem sich die Abhängigkeit des internationalen Handels von der Natur in Zahlen ausdrücken lässt. Der mehrschrittige Prozess, der im Fachmagazin People and Nature veröffentlicht wurde, soll helfen, die komplexe Beziehung zwischen Natur und internationalem Handel besser zu verstehen.
Mehr20.02.2024 | iDiv, Medienmitteilung, TOP NEWS
Vom Regenwald zur Plantage: Umwandlung prägt Nahrungsnetze und Biodiversität
Basiert auf einer Medienmitteilung der Universität Göttingen Mit der Umwandlung von Regenwald in Plantagen verändern sich die Nahrungsnetze in tropischen Ökosystemen grundlegend. Das zeigt eine neue Studie in der Fachzeitschrift Nature, die erstmals Aufschluss gibt über die Weitergabe von Energie zwischen den Tieren des Bodens und der Baumkronen in diesen besonders artenreichen Lebensräumen.
Mehr14.02.2024 | Forschung, iDiv, Medienmitteilung, TOP NEWS
Drei Viertel der Vegetationstypen in Amerika nicht ausreichend geschützt
Drei Viertel der verschiedenen Vegetationstypen in Nord-, Mittel- und Südamerika erfüllen nicht die Zielvorgabe der Globalen Biodiversitätskonvention, 30 % der weltweiten Land- und Meeresflächen unter Schutz zu stellen. Das hat eine Studie unter Leitung des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) und der Martin-Luther-Universität Halle-Wittenberg (MLU) ergeben, die in Global Ecology and Conservation veröffentlicht wurde. Sie zeigt außerdem, dass über 40 % der bedrohten Vogel- und Säugetierarten vor allem in einem einzigen Vegetationstyp vorkommen. Dadurch könnten sie vom Aussterben bedroht sein, wenn diese kritischen Lebensräume nicht ausreichend geschützt werden.
Mehr14.02.2024 | Biodiversität und Mensch, Medienmitteilung, TOP NEWS
Fische der oberen Donau könnten zukünftig genauso gefährdet sein wie in der Vergangenheit, nur der Grund ist ein anderer
Basiert auf einer Medienmitteilung des Leibniz-Instituts für Gewässerökologie und Binnenfischerei (IGB) Flüsse gehören zu den am stärksten gefährdeten Ökosystemen der Erde. Während einige Studien die Auswirkungen des Klimawandels auf die dort lebenden Tierarten prognostizieren, ist wenig darüber bekannt, wie gravierend diese im Vergleich zu historischen Veränderungen sein werden. Forschende unter der Leitung des Leibniz-Instituts für Gewässerökologie und Binnenfischerei (IGB) und des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) haben die Gefährdung von 48 heimischen Fischarten im oberen Donaueinzugsgebiet durch vergangene und mögliche zukünftige Umweltveränderungen untersucht. Sie zeigen, dass Fische in der Vergangenheit besonders empfindlich auf Veränderungen des Durchflusses durch Begradigung und Querbauwerke reagiert haben, während in Zukunft höhere Temperaturen die größte Bedrohung darstellen. Die Gefährdung wird auch in Zukunft mindestens gleich hoch bleiben. Sie könnte aber wahrscheinlich durch die Wiederanbindung ehemaliger Auen und eine verbesserte Durchgängigkeit abgepuffert werden.
Mehr09.02.2024 | Medienmitteilung, MLU News, TOP NEWS
US-Ökologe Brian McGill gewinnt Humboldt-Forschungspreis
Basiert auf einer Medienmitteilung der Martin-Luther-University Halle-Wittenberg Die Alexander von Humboldt-Stiftung zeichnet den US-Wissenschaftler Prof. Dr. Brian McGill von der University of Maine mit dem Humboldt-Forschungspreis aus. Nominiert wurde der Biodiversitätsforscher von Prof. Dr. Jonathan Chase, Leiter der Forschungsgruppe Biodiversitätssynthese am Deutschen Zentrum für integrative Biodiversitätsforschung Halle-Jena-Leipzig (iDiv) und an der Martin-Luther-Universität Halle-Wittenberg (MLU). Der Preis ist mit 60.000 Euro dotiert. Das Geld wird McGill für mehrere Forschungsaufenthalte am iDiv nutzen.
Mehr22.01.2024 | Biodiversität und Naturschutz, Forschung, iDiv, Medienmitteilung, TOP NEWS
Wolf und Elch – willkommen im Oderdelta?
Der Rückkehr großer Fleisch- und Pflanzenfresser wie Wolf und Elch in das Oderdelta stehen laut einer Online-Befragung viele Menschen in Deutschland und Polen offen gegenüber. Das zeigt eine Studie unter Leitung des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) Halle-Jena-Leipzig und der Martin-Luther-Universität Halle-Wittenberg (MLU), die in People and Nature veröffentlich wurde. Bei einer Auswahl zwischen verschiedenen Rewilding-Szenarien bevorzugte die Mehrheit der Befragten ein naturnahes Management. Vorbehalte gibt es hingegen bei den Menschen, die in der Nähe des Oderdeltas wohnen.
Mehr17.01.2024 | iDiv-Mitglieder, Medienmitteilung, TOP NEWS
Ehrung: Christian Wirth zum Auswärtigen Mitglied des Max-Planck-Instituts für Biogeochemie ernannt
Basiert auf einer Medienmitteilung des Max-Planck-Instituts für Biogeochemie Das Max-Planck-Institut für Biogeochemie (MPI-BGC) hat ein neues auswärtiges Mitglied gewonnen: Prof. Dr. Christian Wirth wurde vom Senat der Max-Planck-Gesellschaft auf Antrag des MPI-BGC zu dessen Auswärtigem Wissenschaftlichen Mitglied ernannt. Wirth ist Gründungsdirektor und Sprecher des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv), Professor der Universität Leipzig und Direktor des Botanischen Gartens Leipzig. Der Pflanzenökologe untersucht die Auswirkungen natürlicher und menschengemachter Änderungen der pflanzlichen Biodiversität auf Ökosystemprozesse, wie zu Beispiel die Kohlenstoffspeicherung, den Wasserverbrauch und den Energiehaushalt. Als ehemaliger Gruppenleiter und später Fellow am MPI-BGC hat Prof. Wirth den Aufbau der TRY Datenbank initiiert und unterstützt, die weltweit größte Datenbank zu Pflanzeneigenschaften. Seine Forschung zum Einfluss des Klimawandels auf Biodiversität und Ökosystemleistungen von Wäldern ergänzt in idealer Weise die Forschungsschwerpunkte des Max-Planck-Instituts in Jena.
Mehr09.01.2024 | Medienmitteilung, TOP NEWS
Globale Studie untersucht Auswirkungen extremer Dürre auf Grasland
Mehr08.01.2024 | Forschung, iDiv-Mitglieder, Medienmitteilung, TOP NEWS
Landwirtschaftliche Nutzung von natürlichen Lebensräumen gefährdet junge Primaten
Das regelmäßige Aufsuchen von Palmölplantagen führt zu einer deutlich erhöhten Sterblichkeitsrate unter jungen Südlichen Schweinsaffen (Macaca nemestrina) in freier Natur. Das zeigt eine neue Studie, die in Current Biology veröffentlicht wurde. Die Forscherinnen begründen dies mit einem höheren Risiko durch Raubtiere und den Menschen. Auch der Kontakt mit potentiell schädlichen Chemikalien, die in der Landwirtschaft zum Einsatz kommen, könnte die Entwicklung der jungen Primaten beeinträchtigen.
Mehr05.01.2024 | Biodiversitätsökonomik, Medienmitteilung, Science-Policy, TOP NEWS
Umweltökonom: „Die Subvention des Dieselverbrauchs in der Landwirtschaft lässt sich nicht mehr begründen“
Basiert auf einer Medienmitteilung der Universität Leipzig Traktoren blockieren Straßen, wütende Bauern hindern Wirtschaftsminister Robert Habeck am Verlassen einer Fähre, für die kommende Woche sind großflächige Proteste der Bauern geplant: Die Landwirte wollen damit gegen die Kürzung der Subventionen für Agrardiesel und gegen eine KfZ-Steuer für die Landwirtschaft demonstrieren. „Durch den Druck, im Bundeshaushalt sparen zu müssen, ist endlich Bewegung in die Bemühungen gekommen, umweltschädliche Subventionen zu streichen. Insbesondere die Abschaffung der Agrardiesel-Subventionen ist überfällig“, sagt Prof. Martin Quaas, Leiter der Forschungsgruppe Biodiversitätsökonomik am Deutschen Zentrum für integrative Biodiversitätsforschung (iDiv) und an der Universität Leipzig. Im Interview spricht er über die Proteste der Bauern, Lösungswege und seine eigene Forschung auf diesem Feld.
Mehr15.12.2023 | Medienmitteilung, TOP NEWS
Wie kann Europa seine Natur wiederherstellen?
Basiert auf einer Medienmitteilung der Universität Duisburg-Essen Anfang 2024 wird das Europäische Parlament endgültig über das „Gesetz zur Wiederherstellung der Natur“ (Nature Restoration Law, NRL) abstimmen. Die international einzigartige und heiß diskutierte Verordnung hat das Ziel, den Verlust der biologischen Vielfalt in Europa aufzuhalten und umzukehren. Ein internationales Forschungsteam, in dem auch zwei Forscher von iDiv und dem UFZ vertreten sind, hat untersucht, wie erfolgsversprechend dieses Gesetz ist. Der Artikel wird am 14. Dezember 2023 in der Fachzeitschrift Science veröffentlicht.
Mehr15.12.2023 | Biodiversität und Mensch, Biodiversitätssynthese, Medienmitteilung, TOP NEWS
Häufige Insektenarten am stärksten vom Rückgang betroffen
Leipzig. Der Rückgang der Insekten ist auf Verluste bei lokal häufigeren Arten zurückzuführen. Das zeigt eine neue Studie, die in der Fachzeitschrift Nature veröffentlicht worden ist. Geleitet von Forschern des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) und der Martin-Luther-Universität Halle-Wittenberg (MLU), stellt die Meta-Analyse von 923 Standorten weltweit zwei wichtige Tendenzen fest: 1) häufige Arten mit vielen Individuen (hohe Abundanzen) sind stärker zurückgegangen als seltene Arten, und 2) die Zunahmen mancher Insektenarten waren zu gering, um früher beobachtete Häufigkeiten zu erreichen. Dies erklärt wahrscheinlich die verbreitete Feststellung, dass es heute weniger Insekten gibt als vor zehn, zwanzig oder dreißig Jahren.
Mehr13.12.2023 | Experimentelle Interaktionsökologie, iDiv-Mitglieder, Medienmitteilung, TOP NEWS
Der Duft der Wälder – ein Risiko fürs Klima?
Basiert auf einer Medienmitteilung der Universität Leipzig Pflanzen geben Duftstoffe ab, um zum Beispiel miteinander zu kommunizieren, Fressfeinde abzuwehren oder auf veränderte Umweltbedingungen zu reagieren. Ein interdisziplinäres Forschungsteam der Universität Leipzig, des Leibniz-Instituts für Troposphärenforschung (TROPOS) und des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) hat in einer Studie untersucht, wie die Artenvielfalt den Ausstoß dieser Stoffe beeinflusst. Erstmals konnte so gezeigt werden, dass artenreiche Wälder weniger von diesen Gasen in die Atmosphäre abgeben als Monokulturen. Bisher wurde angenommen, dass artenreiche Wälder mehr Emissionen abgeben. Diese Annahme konnte das Leipziger Team jetzt experimentell widerlegen. Ihre Ergebnisse wurden in der Fachzeitschrift Communications Earth & Environment veröffentlicht.
Mehr07.12.2023 | iDiv, Medienmitteilung, TOP NEWS
Empfehlungen für eine Forschungsagenda zu Biodiversität und Pandemien
Mehr06.12.2023 | Experimentelle Interaktionsökologie, Forschung, iDiv, Medienmitteilung, TOP NEWS
Das Klimaschild der Natur entschlüsseln: Pflanzenvielfalt stabilisiert die Bodentemperatur
Basiert auf einer Medienmitteilung der Universität Leipzig Eine neue Studie zeigt eine natürliche Lösung zur Abschwächung von Auswirkungen des Klimawandels wie extremen Wetterereignissen auf. Forschende der Universität Leipzig, der Friedrich- Schiller-Universität Jena, des Deutschen Zentrums für integrative Biodiversitätsforschung Halle-Jena-Leipzig (iDiv) und anderer Forschungseinrichtungen fanden heraus, dass eine vielfältige Pflanzenwelt als Puffer gegen Schwankungen der Bodentemperatur wirkt. Dieser Puffer wiederum kann einen entscheidenden Einfluss auf wichtige Ökosystemprozesse haben. Ihre neuen Erkenntnisse haben sie gerade im Fachjournal Nature Geoscience veröffentlicht.
Mehr04.12.2023 | iDiv, Medienmitteilung, TOP NEWS
Ökologie: „iDiv-Universitäten“ klettern in die Spitzengruppe des internationalen Shanghai-Rankings 2023
Mehr13.11.2023 | Biodiversitätsökonomik, iDiv, Medienmitteilung, TOP NEWS
DFG-Zuschlag für neues Graduiertenkolleg
Basiert auf einer Medienmitteilung der Universität Leipzig Großer Erfolg für die wissenschaftliche Nachwuchsförderung in Leipzig: Wie die Deutsche Forschungsgemeinschaft (DFG) mitteilte, wird ab April 2024 ein neues Graduiertenkolleg mit rund 7 Millionen Euro gefördert. Über 40 Promovierende der Wirtschafts- und Natur- oder Lebenswissenschaften erforschen darin unter der Leitung von Prof. Dr. Martin Quaas vom Deutschen Zentrum für integrative Biodiversitätsforschung (iDiv) und der Universität Leipzig nachhaltige Nutzungskonzepte natürlicher Gemeinschaftsgüter.
Mehr13.11.2023 | iDiv, Medienmitteilung, TOP NEWS
Wenn Schriftstellerinnen und Schriftsteller über Biodiversität schreiben
Basiert auf einer Medienmitteilung der Universität Leipzig Viele Romane oder Gedichte beinhalten Beschreibungen von Pflanzen oder Tieren – mal mehr, mal weniger detailreich. Wie intensiv Flora und Fauna in einem literarischen Werk thematisiert werden, hängt auch damit zusammen, wer es unter welchen Lebensumständen verfasst hat. So verwenden weibliche Autorinnen beispielsweise mehr Artnamen in ihren Texten. Das hat ein Forschungsteam von der Universität Leipzig, dem Deutschen Zentrum für integrative Biodiversitätsforschung iDiv und der Goethe-Universität Frankfurt herausgefunden, indem es rund 13.500 literarische Werke von rund 2.900 Autorinnen und Autoren untersuchte. Die Studie in People and Nature ist ein Beispiel dafür, wie Methoden aus den Natur- und den Geisteswissenschaften mittels digitaler Techniken miteinander kombiniert werden können.
Mehr30.10.2023 | Biodiversitätstheorie, Experimentelle Interaktionsökologie, Medienmitteilung, TOP NEWS
Bereits wenig künstliches Licht gefährdet Ökosysteme
Leipzig, Jena. Eine neue Sammlung von Studien über künstliches Licht bei Nacht zeigt, dass die Auswirkungen der Lichtverschmutzung weitreichender sind als gedacht. Selbst geringe Mengen künstlichen Lichts können Artengemeinschaften und ganze Ökosysteme stören. Die in der Fachzeitschrift Philosophical Transactions of the Royal Society B veröffentlichte Sonderausgabe mit 16 wissenschaftlichen Studien befasst sich mit den Auswirkungen der Lichtverschmutzung auf komplexe Ökosysteme, darunter Boden-, Grasland- und Insektengemeinschaften. Wissenschaftlerinnen und Wissenschaftler des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) und der Friedrich-Schiller-Universität Jena betonen in der Sonderausgabe den Dominoeffekt, den Lichtverschmutzung auf Funktionen und Stabilität von Ökosystemen haben kann.
Mehr27.10.2023 | Biodiversität und Mensch, Forschung, iDiv, Medienmitteilung, TOP NEWS
Wie Soziale Medien zum Artenschutz beitragen können
Leipzig. Fotos von Tier- und Pflanzenarten, die in den Sozialen Medien geteilt werden, können einen wichtigen Beitrag zum Schutz der Biodiversität leisten – vor allem in tropischen Gebieten. Zu diesem Schluss kommt ein Forschungsteam unter Leitung des Deutschen Zentrums für Biodiversitätsforschung (iDiv), des Helmholtz-Zentrums für Umweltforschung (UFZ), der Friedrich-Schiller-Universität Jena und der Universität von Queensland (UQ). In drei Studien, die in den Fachmagazinen BioScience, One Earth und Conservation Biology veröffentlicht wurden, zeigen sie am Beispiel Bangladeschs, dass Facebook-Daten einen wichtigen Beitrag zum Biodiversitätsmonitoring und zur Bewertung potenzieller Schutzgebiete leisten können.
Mehr10.10.2023 | Experimentelle Interaktionsökologie, Medienmitteilung, TOP NEWS
Förderung neuer Forschung im Jena Experiment – Fokus auf Ökosystem-Stabilität
Gemeinsame Medienmitteilung von iDiv, der Universität Leipzig und der Friedrich-Schiller-Universität Jena Jena, Leipzig. Die Deutsche Forschungsgemeinschaft (DFG) fördert eine Forschungsgruppe im Jena Experiment für weitere vier Jahre mit insgesamt etwa fünf Millionen Euro. Die Wissenschaftlerinnen und Wissenschaftler unter Führung des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv), der Universität Leipzig und der Friedrich-Schiller-Universität Jena werden insbesondere die stabilisierende Wirkung von Biodiversität gegen extreme Klimaereignisse wie Trockenheit, Hitze oder Frost untersuchen.
Mehr09.10.2023 | Experimentelle Interaktionsökologie, iDiv-Mitglieder, Medienmitteilung, TOP NEWS
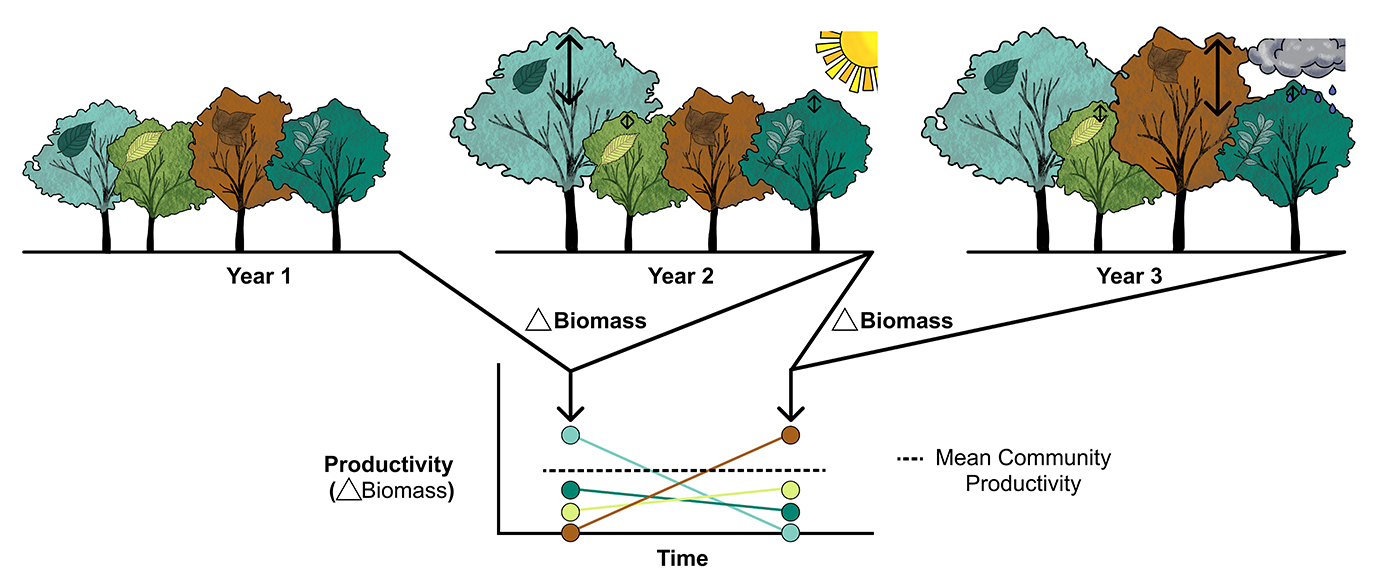
Mischwälder sind produktiver, wenn sie strukturell komplex sind
Dresden, Halle, Leipzig. Baumartenreiche Wälder sind besonders produktiv aufgrund ihrer erhöhten oberirdischen Strukturkomplexität. Das zeigt eine gemeinsame Studie der TU Dresden, Leuphana Universität Lüneburg, Martin-Luther-Universität Halle-Wittenberg, Universität Leipzig, Universität Montpellier und des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv). Die Ergebnisse sind im Journal Science Advances erschienen.
Mehr26.09.2023 | Experimentelle Interaktionsökologie, Forschung, iDiv, Medienmitteilung, TOP NEWS
Rückgang von Wirbellosen wirkt sich negativ auf Schädlingsbekämpfung und Zersetzungsprozesse aus
Leipzig. Der Rückgang wirbelloser Tierarten beeinträchtigt die Funktionsweise von Ökosystemen, darunter zwei wichtige Ökosystemleistungen: Die natürliche Schädlingsbekämpfung und die Zersetzung organischer Stoffe. Das zeigt eine Studie unter Leitung von Wissenschaftlerinnen und Wissenschaftlern des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) sowie der Universität Leipzig, die im Fachmagazin Current Biology veröffentlicht wurde. Die Studie beweist, dass der Verlust von Wirbellosen zu einem Rückgang wichtiger Ökosystemleistungen und zu einer Entkopplung von Ökosystemprozessen führt und daher sofortige Schutzmaßnahmen ergriffen werden müssen.
Mehr08.09.2023 | iDiv, Medienmitteilung, TOP NEWS
iDiv-Wissenschaftler*innen reagieren auf die prekären Arbeitsbedingungen an Universitäten und Forschungsinstituten in Deutschland
iDiv’s Forscher*innen1 sind besorgt über die bereits prekären Arbeitsbedingungen in Deutschland und alarmiert, dass diese mit Inkrafttreten eines neuen WissZeitVG noch verschärft werden.
Mehr04.09.2023 | Biodiversität und Naturschutz, Biodiversitätssynthese, Medienmitteilung, TOP NEWS
Die meisten Arten sind selten. Aber nicht sehr selten
Halle/Saale, Fort Lauderdale. Über 100 Jahre Naturbeobachtungen haben ein potenziell universelles Muster der Artenhäufigkeit enthüllt: Die meisten Arten sind selten, aber nicht sehr selten, und nur wenige Arten sind sehr häufig. Diese sogenannte „globale Artenhäufigkeitsverteilung“ ist für intensiv untersuchte Artengruppen wie die Vögel mittlerweile lückenlos erfasst. Für andere Artengruppen wie die Insekten ist das Muster noch unvollständig. Zu diesem Ergebnis kommt ein internationales Forscherteam unter Leitung des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv), der Martin-Luther-Universität Halle-Wittenberg (MLU) und der University of Florida (UF). Die Studie wurde in der Fachzeitschrift Nature Ecology and Evolution veröffentlicht. Sie zeigt, wie wichtig das Monitoring der Biodiversität ist, um die globale Artenhäufigkeit zu bestimmen und ihren Wandel zu verstehen.
Mehr25.08.2023 | iDiv, Medienmitteilung, TOP NEWS
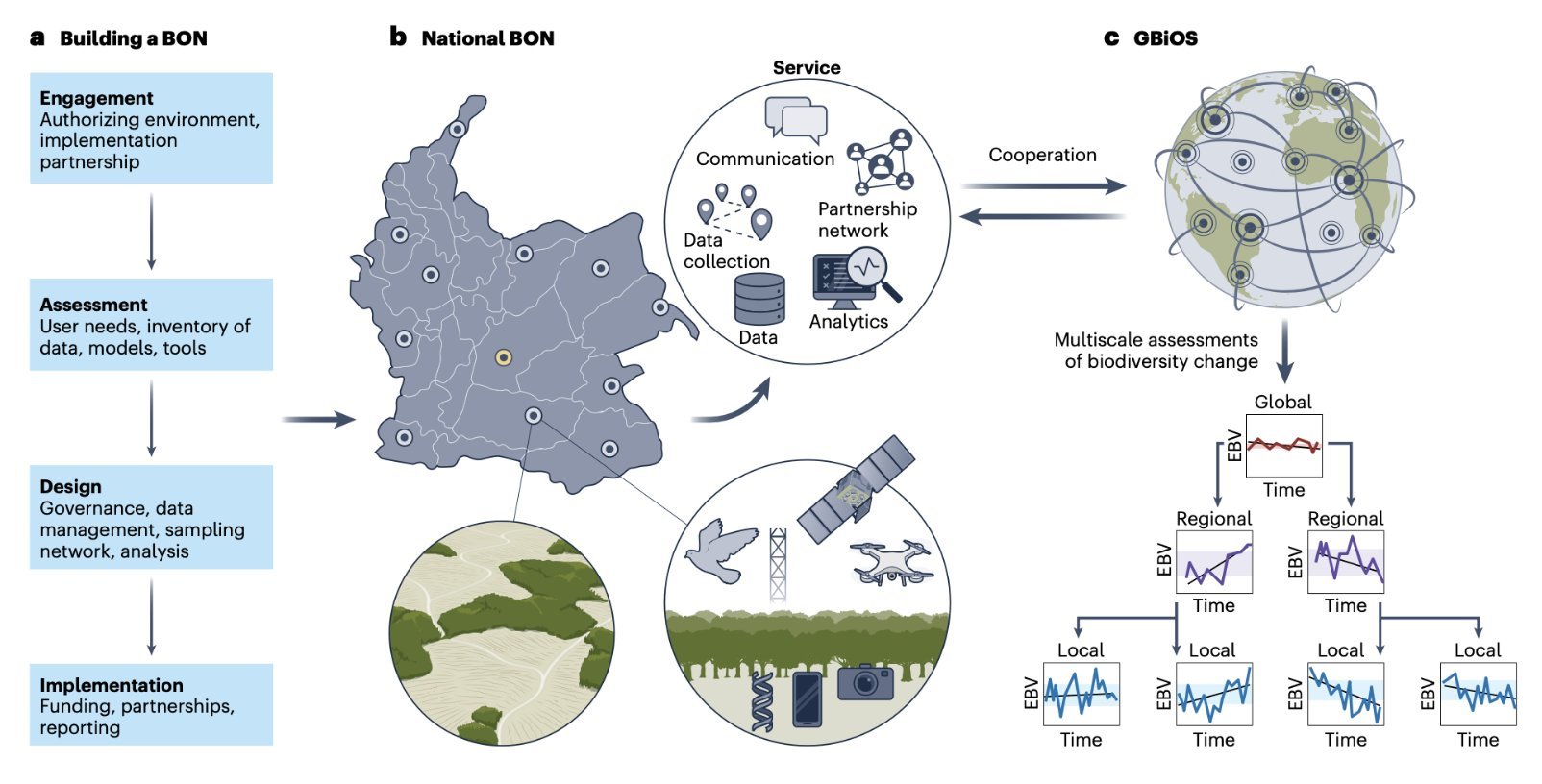
Eine globale Beobachtungsstelle für die Biodiversität
Mehr23.08.2023 | Forschung, iDiv, iDiv-Mitglieder, Medienmitteilung, TOP NEWS
1000 neue Arten für Nigeria
Leipzig/Katsina. Derzeit könnten mehr als 1000 Gefäßpflanzen in Nigeria noch unbeschrieben sein – was es wiederum unmöglich macht zu wissen, ob diese Pflanzen gefährdet sind und besondere Schutzmaßnahmen benötigen. Das ist eines der Hauptergebnisse einer neuen Studie, die unter Leitung des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) und der Universität Leipzig erstellt und im Fachjournal Annals of Botany veröffentlicht wurde. Um die Ziele des Übereinkommens für biologische Vielfalt (CBD) zu erreichen, sind dringende Maßnahmen erforderlich, die lokale taxonomische Aktivitäten fördern.
Mehr15.08.2023 | Medienmitteilung, TOP NEWS
Einige Pflanzen behalten ihre abgestorbenen Blätter im Herbst, aus guten Gründen
Bericht von Dr. Gerrit Angst, wissenschaftlicher Mitarbeiter in der Experimentellen Interaktionsökologie am iDiv, Universität Leipzig, und an der Tschechischen Akademie der Wissenschaften, Co-Autor der Studie: Leipzig/Budweis/Prag. Der Verbleib von abgestorbener Biomasse an Gräsern und Kräutern in der gemäßigten Klimazone ist weitverbreitet und korreliert mit bestimmten Pflanzeneigenschaften, welches den potentiellen Einfluss dieses Phänomens auf Ökosystemfunktionen impliziert. Dies sind die Hauptaussagen einer experimentellen Studie von über 100 Pflanzenarten, die zusammen von Wissenschaftlern des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv), Universität Leipzig, der Tschechischen Akademie der Wissenschaften, und der Karls-Universität Prag durchgeführt wurde. Die Studie wurde kürzlich in der wissenschaftlichen Zeitschrift Journal of Ecology publiziert.
Mehr08.08.2023 | Medienmitteilung, sDiv, TOP NEWS
Satelliten dokumentieren Auswirkungen von Hitzewellen auf Pflanzen
Basiert auf einer Medienmitteilung der Universität Leipzig Wie sich Dürreperioden auf das Photosynthese-Verhalten von Pflanzen im Tagesverlauf auswirken, zeigt eine neue wissenschaftliche Studie. Demnach verschieben Pflanzen in ohnehin trockenen Gebieten ihre CO2-Aufnahme während einer Hitzewelle zunehmend in die Morgenstunden und verringern die Photosynthese am Mittag und Nachmittag. Die Forschenden werteten für die Studie Daten von neuartigen geostationären Satelliten aus, die unter anderem während einer Hitzewelle in den USA im Jahr 2020 aufgenommen wurden. Dr. Benjamin Dechant vom Deutschen Zentrum für integrative Biodiversitätsforschung (iDiv) und der Universität Leipzig war an der Publikation der südkoreanischen Forschungsgruppe beteiligt und erklärt im Interview die wichtigsten Ergebnisse.
Mehr12.07.2023 | iDiv, Medienmitteilung, TOP NEWS
Entlegene Pflanzenwelt
Basiert auf einer Medienmitteilung der Universität Göttingen Ozeanische Inseln sind beliebte Modellsysteme in der Ökologie, Biogeografie und Evolutionsforschung. Viele bahnbrechende Erkenntnisse entstammen dem Studium von Arten auf Inseln und deren Wechselspiel mit ihrer belebten und unbelebten Umwelt – auch Darwins Evolutionstheorie. Nun hat ein internationales Forschungsteam unter der Leitung der Universität Göttingen und mit Beiteilung von Forschenden des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) in einer großen Feldstudie die Pflanzenwelt der Kanarischen Insel Teneriffa untersucht. Die Ergebnisse sind anders als erwartet: Die Flora der Insel weist eine bemerkenswerte Vielfalt an funktionellen Merkmalen auf. Die Pflanzen weichen aber in funktioneller Hinsicht wenig von Pflanzen des Festlands ab. Doch anders als die Flora des Festlands wird die Flora Teneriffas von langsam wachsenden, verholzten Sträuchern mit einer konservativen Lebensstrategie dominiert. Die Ergebnisse sind in der Fachzeitschrift Nature erschienen.
Mehr15.06.2023 | Experimentelle Interaktionsökologie, Medienmitteilung, TOP NEWS
Ganzheitliches Management essentiell um Kohlenstoffspeicherung im Boden zu erhöhen
Bericht von Dr. Gerrit Angst, Postdoktorand in der Forschungsgruppe Experimentelle Interaktionsökologie bei iDiv und der Universität Leipzig: Leipzig/Budweis/Kopenhagen. Wenn mehr Kohlenstoff im Boden gespeichert wird, kann das den Klimawandel abschwächen. Funktionieren kann dies allerdings nur, wenn Böden ganzheitlicher bewirtschaftet werden. Dies ist die Hauptaussage unserer Studie, die kürzlich in der Fachzeitschrift Nature Communications veröffentlicht wurde. Zusammen mit Kollegen des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv), der Tschechischen Akademie der Wissenschaften und der Universität Kopenhagen, präsentieren wir einen konzeptionellen Rahmen, der es ermöglicht, Böden effektiv als Kohlenstoffsenken zu etablieren.
Mehr26.04.2023 | Biodiversitätstheorie, Forschung, iDiv, Medienmitteilung, TOP NEWS
Vielfältige Landschaften helfen Insekten gegen Hitzestress
Leipzig/Jena/Bad Lauchstädt. Die globale Erwärmung hat auch Auswirkungen auf landlebende Insekten. Als Reaktion auf immer häufigere Hitzewellen müssen diese entweder ihre Aktivität verringern oder Schutz in geeigneteren Mikrohabitaten suchen. Eine neue Studie unter Leitung von Wissenschaftlerinnen des Deutschen Zentrum für integrative Biodiversitätsforschung (iDiv) und der Friedrich-Schiller-Universität Jena zeigt: Je vielfältiger diese kleinen Lebensräume sind, umso besser für die Insekten. Für ihre Studie, die im Fachjournal Global Change Biology veröffentlicht wurde, entwickelten die Forschenden einen neuartigen Ansatz, um die Bewegung und Aktivität von Insekten genau zu tracken.
Mehr20.04.2023 | iDiv, Medienmitteilung, TOP NEWS
iDiv feiert 10-jähriges Bestehen
Das Deutsche Zentrum für integrative Biodiversitätsforschung (iDiv) feierte heute sein 10-jähriges Bestehen mit einem Festakt im Paulinum der Universität Leipzig. Über 300 Gäste aus Politik, Wissenschaft und Gesellschaft nahmen teil, darunter die Ministerpräsidenten Sachsens, Sachsen-Anhalts und Thüringens, Michael Kretschmer, Dr. Reiner Haseloff und Bodo Ramelow sowie der Beauftragte der Bundesregierung für Ostdeutschland, Staatsminister Carsten Schneider. Sie würdigten die wichtigen Beiträge des Forschungszentrums für den Schutz der biologischen Vielfalt. Bundeskanzler Olaf Scholz betonte in einer Video-Grußbotschaft die Bedeutung der „Grundlagenforschung von Weltrang“ für die internationale Biodiversitätspolitik.
Mehr19.04.2023 | Biodiversitätstheorie, Forschung, iDiv, Medienmitteilung, TOP NEWS
Große Tiere gehen es langsamer an um nicht zu überhitzen
Leipzig. Ob sich ein Tier nun fliegend, laufend oder schwimmen fortbewegt – das jeweils optimale Tempo ist immer davon abhängig, wie effektiv das Tier sich der überschüssigen Wärme entledigt, die von seinen Muskeln erzeugt wird. Das ist das Ergebnis einer Studie, die nun unter Leitung von Forschenden des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) und der Friedrich-Schiller-Universität Jena im Fachmagazin PLOS Biology veröffentlich wurde.
Mehr30.03.2023 | Biodiversitätssynthese, iDiv, Medienmitteilung, TOP NEWS
Neuen Ideen für Forschung zur Artenvielfalt: Ökologe Jonathan Chase erhält ERC Advanced Grant
Gemeinsame Medienmitteilung des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) und der Martin-Luther-Universität Halle-Wittenberg Der Europäische Forschungsrat (ERC) fördert Prof. Dr. Jonathan Chase mit einem der begehrten ERC Advanced Grants. Dem Wissenschaftler stehen damit in den kommenden fünf Jahren knapp 2,5 Millionen für sein Forschungsprojekt „MetaChange“ zur Verfügung. Im Rahmen des Projekts will er neue Konzepte und Methoden für ein besseres Verständnis der Artenvielfalt und deren Wandel entwickeln. Chase forscht und lehrt seit 2014 am Deutschen Zentrum für integrative Biodiversitätsforschung (iDiv) und an der Martin-Luther-Universität Halle-Wittenberg (MLU).
Mehr20.03.2023 | Biodiversitätssynthese, Forschung, iDiv, Medienmitteilung, TOP NEWS
Weitverbreitete Arten auf dem Vormarsch
Leipzig/Halle. Das menschliche Handeln treibt den Wandel der Biodiversität und Veränderungen in der Zusammensetzung der Arten rapide voran. Ein Forschungsteam unter Leitung des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) und der Martin-Luther-Universität Halle-Wittenberg konnte nun zeigen, dass weiterverbreitete Arten eher von anthropogenen Veränderungen profitieren und sich weiter ausbreiten, wohingegen viele Arten mit einem kleinen Verbreitungsgebiet sich noch weiter zurückziehen. Die Ergebnisse, die im Fachmagazin Nature Communications veröffentlicht wurden, basieren auf Daten aus über 200 Studien und beweisen, dass Schutzgebiete einige Auswirkungen des Biodiversitätswandels abmildern und den systematischen Rückgang wenig verbreiteter Arten ausbremsen können.
Mehr16.03.2023 | Biodiversitätsökonomik, Forschung, iDiv, Medienmitteilung, TOP NEWS
Was der Fischer davon hat, die Evolution des Kabeljaus zurückzudrehen
Leipzig. Überfischung und Übernutzung der Meere haben bei Fischbeständen wie dem Kabeljau zu evolutionären Veränderungen geführt, die die Produktivität und den Marktwert der Fischebestände schmälern. Ein nachhaltigeres und vorausschauendes Management der Fischereien könnte diese Veränderungen rückgängig machen. Eine neue Studie des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv), der Universität Leipzig und des Instituts für Meeresforschung in Tromsø, die im Fachmagazin Nature Sustainability veröffentlicht wurde, zeigt, dass diese Umkehr der evolutionären Veränderungen sich nur geringfügig auf den Gewinn der Fischereien auswirken, aber zum Erhalt der natürlichen genetischen Vielfalt beitragen würde.
Mehr09.03.2023 | Biodiversitätssynthese, iDiv, Medienmitteilung, TOP NEWS
Zwerge und Riesen auf Inseln sterben besonders leicht aus
Leipzig/Halle. Inseln gelten als “Labore der Evolution“ und sind Lebensraum für viele Tierarten mit einzigartigen Eigenschaften. Darunter finden sich sogenannte Zwerge, die im Vergleich zu ihren Verwandten auf dem Festland eine sehr geringe Größe erreichen, sowie Riesen, die wiederum vergleichsweise groß werden. Ein Team von Forschenden unter Leitung des Zentrums für integrative Biodiversitätsforschung (iDiv) und der Martin-Luther-Universität Halle-Wittenberg (MLU) fand nun heraus, dass Arten, deren Körpergröße sich besonders stark von der ihrer Festlandsverwandten unterscheidet, mit größerer Wahrscheinlichkeit aussterben. Ihre Studie, die im Fachmagazin Science veröffentlicht wurde, zeigt außerdem, dass die Aussterberate von Säugetieren auf Inseln weltweit durch die Ankunft des Menschen deutlich angestiegen ist.
Mehr09.03.2023 | Forschung, iDiv-Mitglieder, Medienmitteilung, MLU News, TOP NEWS
Globale Klimadaten erklären lokale Pflanzenzusammensetzung nur unzureichend
Basiert auf einer Medienmitteilung der Martin-Luther-Universität Halle-Wittenberg Das globale Klima beeinflusst das regionale Pflanzenwachstum – allerdings nicht in allen Lebensräumen gleichermaßen. Das haben Forschende der Martin-Luther-Universität Halle-Wittenberg (MLU) und des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) in einer Analyse von über 300.000 europäischen Vegetationsbeobachtungen herausgefunden. Ihr Fazit: Die Effekte des Klimawandels auf die Vegetation der Erde lassen sich nicht generell vorhersagen, sondern sind in hohem Maße von den untersuchten Habitaten und den lokalen Bedingungen abhängig. Die Erkenntnisse wurden im renommierten Journal Nature Communications veröffentlicht.
Mehr07.03.2023 | Medienmitteilung, TOP NEWS
Pflanzenwurzeln: Der Treibstoff für tropische Bodenfauna
Basiert auf einer Medienmitteilung der Universität Göttingen Göttingen/Leipzig. Gemeinschaften von Bodentieren in den Tropen werden von Pflanzenwurzeln und den daraus hervorgehenden Ressourcen bestimmt. Dies ist das zentrale Ergebnis einer neuen Studie eines Forscherteams unter Leitung der Universität Göttingen, des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) und der Universität Leipzig. In einem einzigen Hektar Boden arbeiten Millionen kleiner Lebewesen wie Regenwürmer, Springschwänze, Milben, Insekten etc. für die Zersetzung und die Gesundheit des Bodens. Lange Zeit ging man davon aus, dass Laubstreu die wichtigste Ressource für diese Tiere ist. Die in Ecology Letters veröffentlichte Studie zeigt jedoch, dass die Wurzeln der Pflanzen für die tropische Bodenfauna eine mindestens ebenso große Rolle spielen.
Mehr01.03.2023 | Biodiversität und Naturschutz, Medienmitteilung, TOP NEWS
NaturaConnect-Stakeholder-Event in Brüssel
Brüssel, 28. Februar 2023. Über 70 führende Entscheidungsträger aus der EU-Politik und den Regierungen kamen zusammen, um auf der ersten NaturaConnect-Stakeholder-Veranstaltung in diesem Jahr den Grundstein für eine mutige neue Vision für den Naturschutz in Europa zu legen. An der Veranstaltung nahmen zahlreiche einflussreiche Interessenvertreter teil, von Ländervertretern über Delegierte der Europäischen Union bis hin zu internationalen und europäischen Naturschutzorganisationen. Das NaturaConnect-Projekt soll die Einrichtung eines transeuropäischen Naturnetzes (TEN-N) aus geschützten und miteinander verbundenen Gebieten unterstützen, die mindestens 30 Prozent der Fläche in der EU erhalten und sowohl der Natur als auch den Menschen zugute kommen. Es wird von internationalen Partnern aus Forschungs- und Umweltorganisationen unter der Leitung des International Institute for Applied Systems Analysis (IIASA), des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) und der Martin-Luther-Universität Halle-Wittenberg (MLU) durchgeführt.
Mehr10.02.2023 | Biodiversität und Naturschutz, Medienmitteilung, TOP NEWS
Wie verändert sich die biologische Vielfalt weltweit? Genaue Trends zu erfassen ist derzeit kaum möglich
Leipzig/Halle. Die verfügbaren Monitoringdaten sind wohl zu unpräzise, um verlässliche globale Durchschnittswerte aus den Trends der lokalen Artenvielfalt errechnen zu können. Zu diesem Schluss kommt ein internationales Forschungsteam unter Leitung des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) und der Martin-Luther-Universität Halle-Wittenberg (MLU). Die Autorinnen und Autoren empfehlen, den Wandel der biologischen Vielfalt vorrangig auf lokaler und regionaler Ebene zu bewerten, statt diesen global darzustellen. Darüber hinaus raten sie zu standardisierten Monitoringprogrammen, ergänzt durch Modelle, die Messfehler und räumliche Ungenauigkeiten berücksichtigen. Die Studie wurde in der Zeitschrift Ecography veröffentlicht.
Mehr09.02.2023 | Medienmitteilung, Molekulare Interaktionsökologie, Physiologische Diversität, TOP NEWS
Wie konnte der Mensch ein so großes Gehirn entwickeln?
Basiert auf einer Medienmitteilung der Universität Amsterdam Amsterdam/Leipzig/Jena. In Jäger- und Sammlergesellschaften bilden bereits Kinder geschlechtsspezifische Fähigkeiten zur Nahrungssuche aus, um besondere Nahrung verfügbar zu machen. Diese Errungenschaft sowie das Teilen von Nahrung könnte es der menschlichen Spezies ermöglicht haben, ein wesentlich größeres Gehirn zu entwickeln als unsere nächsten lebenden Verwandten. Zu diesem Schluss kommen Forschende der Universität Amsterdam (UvA), des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv), des Max-Planck-Instituts für evolutionäre Anthropologie, des Helmholtz-Zentrums für Umweltforschung (UFZ) und der Friedrich-Schiller-Universität Jena. Eine stabilere Energie- und Nährstoffversorgung könnte eine größere Investition in das Gehirn ermöglicht haben. Die Studie wurde in der Zeitschrift Frontiers in Ecology and Evolution veröffentlicht.
Mehr07.02.2023 | Biodiversitätssynthese, Medienmitteilung, Physiologische Diversität, TOP NEWS
Pflanzenvielfalt nach Landwirtschaft: keine vollständige Erholung ohne Hilfe
Leipzig/Minnesota. Die Landwirtschaft gilt als einer der wesentlichen Störfaktoren ökologischer Systeme – und es kann lange dauern, bis sich ehemals landwirtschaftlich genutzte Flächen wieder erholen. Ohne aktive Renaturierungsmaßnahmen kann sich diese Erholung noch weiter herauszögern und ist zudem häufig unvollständig; das zeigt ein Team unter der Leitung des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv), der Universität Leipzig (UL), der Martin-Luther-Universität Halle-Wittenberg (MLU) und des Helmholtz-Zentrums für Umweltforschung (UFZ). In ihrer Studie im Journal of Ecology beleuchten sie, wie sich ehemals landwirtschaftlich genutzte Flächen auf verschiedenen Ebenen erholen, und zeigen konkrete Renaturierungsmaßnahmen auf, die der Biodiversität helfen können, sich zu regenerieren.
Mehr01.02.2023 | Biodiversität und Mensch, Medienmitteilung, TOP NEWS
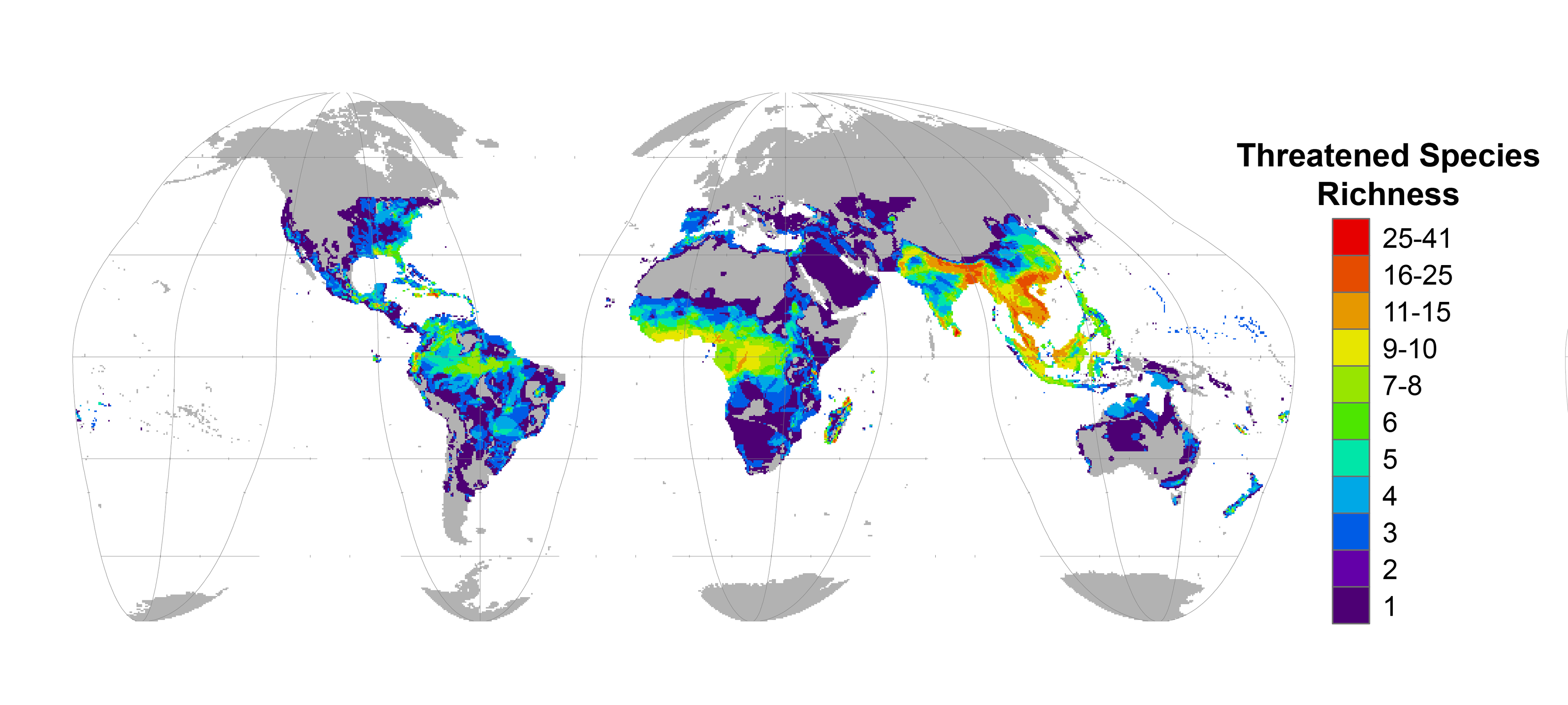
76 Prozent der erfassten Insektenarten nicht ausreichend von Schutzgebieten abgedeckt
Leipzig/Jena. Die Zahl der Insekten geht in den letzten Jahrzehnten in vielen Teilen der Welt zurück. Schutzgebiete könnten einen wesentlichen Beitrag zur Erhaltung bedrohter Insektenarten leisten, doch Forschende unter Leitung des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv), des Helmholtz-Zentrums für Umweltforschung (UFZ), der Friedrich-Schiller-Universität Jena und der Universität Queensland fanden jetzt heraus, dass 76 Prozent der erfassten Insektenarten weltweit nicht ausreichend durch Schutzgebiete abgedeckt sind. In der Zeitschrift One Earth empfehlen die Forschenden Entscheidungsträgern, die mit Abstand größte Artengruppe bei der Umsetzung der neuen Ziele der UN-Konvention zur biologischen Vielfalt angemessen zu berücksichtigen.
Mehr17.01.2023 | iDiv, Medienmitteilung, TOP NEWS
Globale Biodiversitätsziele in Deutschland umsetzen – mit Unterstützung der Forschung
Berlin. Die Umsetzung der kürzlich beschlossenen UN-Naturschutzziele gelingt nur, wenn alle Akteure – Politik und Praxis, Verbände, Wirtschaft und Wissenschaft – an einem Strang ziehen. Die Wissenschaft liefert die Wissensgrundlage für effektives Handeln und spielt damit eine Schlüsselrolle bei der Umsetzung der globalen Ziele. Dies war der Tenor beim Parlamentarischen Abend am 17. Januar in der Landesvertretung Sachsen-Anhalts in Berlin, zu dem das Deutsche Zentrum für integrative Biodiversitätsforschung (iDiv) und das Ministerium für Wissenschaft, Energie, Klimaschutz und Umwelt Sachsen-Anhalt geladen hatten. Als wesentliches Element sehen die Forschenden einen hochrangigen nationalen Biodiversitätsrat, um die Erhaltung der biologischen Vielfalt zum politischen Kernthema in allen Ministerien zu machen.
Mehr13.01.2023 | Experimentelle Interaktionsökologie, Forschung, iDiv, Medienmitteilung, TOP NEWS
Grasland-Ökosysteme mit zunehmendem Alter widerstandsfähiger
Basiert auf einer Medienmitteilung der Universität Zürich Zürich/Leipzig. Jüngste Experimente haben gezeigt, dass der Verlust von Arten in einer Pflanzengemeinschaft Ökosystemfunktionen und -leistungen wie Produktivität, Kohlenstoffspeicherung und Bodenfertilität reduziert. Mit der Verringerung der Funktionsfähigkeit gerät auch die längerfristige Stabilität und Widerstandsfähigkeit des Ökosystems in Gefahr. Da die meisten Experimente kurzfristig angelegt sind, liess sich diese Gefahr bisher jedoch nicht abschätzen.
Mehr03.01.2023 | Arten-Interaktionsökologie, Medienmitteilung, TOP NEWS, UFZ-News
Weniger Nachtfalter, mehr Fliegen
Im hohen Norden des Planeten hinterlässt der Klimawandel besonders deutliche Spuren. Eine neue Studie in Finnland zeigt nun, dass es parallel dazu dramatische Veränderungen bei den bestäubenden Insekten gegeben hat. Forscherinnen der Martin-Luther-Universität Halle-Wittenberg (MLU), des Helmholtz-Zentrums für Umweltforschung (UFZ) und des Deutschen Zentrums für integrative Biodiversitätsforschung Halle-Jena-Leipzig (iDiv) haben festgestellt, dass sich das Netzwerk von Pflanzen und ihren Bestäubern dort seit dem Ende des 19. Jahrhunderts massiv verändert hat. Möglicherweise könne das dazu führen, dass Pflanzen künftig weniger effektiv bestäubt werden und sich dadurch schlechter vermehren, warnen die Wissenschaftlerinnen im Fachjournal Nature Ecology & Evolution.
Mehr14.12.2022 | Makroökologie und Gesellschaft, Medienmitteilung, sDiv, TOP NEWS
Mensch und Natur: Der Abstand wird größer
Gemeinsame Medienmitteilung von iDiv und der Universität Leipzig Leipzig/Moulis. Die Menschen leben immer weiter von Naturräumen entfernt und beschäftigen sich tendenziell auch seltener mit der Natur. Zu diesem Ergebnis kommt eine Metastudie eines deutsch-französischen Forscherteams am Deutschen Zentrum für integrative Biodiversitätsforschung (iDiv), der Universität Leipzig und der Station für theoretische und experimentelle Ökologie (SETE – CNRS). Die Forschenden betonen, dass die Entwicklung umweltfreundlichen Verhaltens maßgeblich von diesen Naturerfahrungen abhängt – und damit die Bewältigung der globalen Umweltkrisen. Die Studie wurde in Frontiers in Ecology and the Environment veröffentlicht.
Mehr12.12.2022 | Biodiversität und Naturschutz, iDiv, Medienmitteilung, TOP NEWS
Neuartige und effiziente Methode zur Identifizierung asiatischer Otter
Mehr
08.12.2022 | Biodiversität und Mensch, Forschung, Medienmitteilung, TOP NEWS, UFZ-News
Valide Daten aus der Bürgerforschung
Basiert auf einer Medienmitteilung des Helmholtz-Zentrums für Umweltforschung (UFZ) Citizen-Science-Projekte etablieren sich mehr und mehr als wichtige Stütze für die Umweltforschung. Sie liefern Daten, öffnen die Wissenschaft für die Gesellschaft und geben Interessierten die Möglichkeit, sich für die Umwelt zu engagieren, um nur einige Vorzüge zu nennen. Allerdings gibt es auch Vorbehalte, etwa in punkto Datenqualität. Ein Forschungsteam unter Leitung des Helmholtz-Zentrums für Umweltforschung (UFZ) und des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) Halle-Jena-Leipzig hat anhand der Zustandsbewertung von Kleingewässern festgestellt, dass Citizen-Science-Daten für die weitere Verwendung in Wissenschaft und Verwaltung durchaus geeignet sind.
Mehr27.11.2022 | iDiv-Mitglieder, Medienmitteilung, TOP NEWS
Neues Senckenberg-Institut kommt nach Jena
Basiert auf einer Medienmitteilung der Senckenberg Gesellschaft für Naturforschung Jena. Die Gemeinsame Wissenschaftskonferenz (GWK) hat sich vollumfänglich für das strategische Erweiterungsvorhaben „Anthropocene Biodiversity Loss“ der Senckenberg Gesellschaft für Naturforschung ausgesprochen. Drei Schwerpunkte werden im Rahmen des Konzeptes dauerhaft etabliert: Collectomics, Biodiversity Genomics und die Solutions Labs. Die Erforschung und der Schutz der Biodiversität stehen im Zentrum des innovativen Vorhabens. Mit dem neuen Jena Senckenberg Institute of Plant Form and Function wird die sammlungsbezogene Forschung auch im Kontext von iDiv gestärkt. Sammlungen sollen genutzt werden, um Daten für die Analyse des globalen Biodiversitätswandels in noch umfangreicherer räumlicher Breite und zeitlicher Tiefe durch die Nutzung und Etablierung neuer Methoden bereit zu stellen.
Mehr10.11.2022 | iDiv-Mitglieder, Medienmitteilung, TOP NEWS
Hauptursache für den Verlust der biologischen Vielfalt ist die Umwandlung von Wäldern und Grünland
Basiert auf einer Medienmitteilung des Natural History Museum London Luxemburg/London/Halle. Die Umwandlung von naturnahen Wäldern und Grünland in landschaftliche Flächen ist hauptverantwortlich für den weltweiten Verlust der biologischen Vielfalt. Die ausbeuterische Nutzung wildlebender Tiere und Pflanzen durch Fischerei, Holzeinschlag, Handel und Jagd ist zweitwichtigste Ursache, gefolgt von Umweltverschmutzung. Der Klimawandel ist bislang nur der viertstärkste Treiber. Dies zeigt eine internationale Studie unter der Leitung der Universidad Nacional de Córdoba (UNC) in Argentinien, des Helmholtz-Zentrums für Umweltforschung (UFZ), des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) und des Natural History Museum London. Die in Science Advances veröffentlichte Studie macht deutlich, dass der Kampf gegen den Klimawandel allein nicht ausreicht, um den weiteren Verlust der biologischen Vielfalt zu verhindern.
Mehr10.11.2022 | Biodiversität und Naturschutz, Medienmitteilung, TOP NEWS
Schutz und Vernetzung der Natur in ganz Europa
Basiert auf einer Medienmitteilung des Internationalen Instituts für Angewandte Systemanalyse (IIASA) Wien/Leipzig. Europa braucht gesunde Ökosysteme, die der biologischen Vielfalt und den Menschen zugutekommen und dabei klimaresistent sind. Das Horizon Europe Projekt NaturaConnect unterstützt die Regierungen der Europäischen Union und andere öffentliche und private Institutionen dabei, ein kohärentes, widerstandsfähiges und weit verknüpftes transeuropäisches Naturnetz zu schaffen. Das neue Projekt wird von internationalen Partnern aus Forschungs- und Umweltorganisationen unter Leitung des Internationalen Instituts für Angewandte Systemanalyse (IIASA), des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) und der Martin-Luther-Universität Halle-Wittenberg (MLU) durchgeführt.
Mehr24.10.2022 | Biodiversitätssynthese, Medienmitteilung, Physiologische Diversität, TOP NEWS
Mehr Biomasse, weniger Artenvielfalt: Wie menschlich verursachte Nährstoffeinträge Pflanzengemeinschaften im Grasland beeinflussen
Leipzig. Bei verstärkten Nährstoffeinträgen im Grasland gehen über längere Zeiträume mehr Arten verloren als neu hinzukommen. Außerdem siedeln sich weniger neue Arten an als unter natürlicher Nährstoffverfügbarkeit. Diese neuen Erkenntnisse erklären, weshalb Nährstoffüberschüsse die Pflanzenvielfalt im Grasland verringern. Mit ihrem weltweiten Experiment tragen die Forschenden unter Leitung des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv), des Helmholtz-Zentrums für Umweltforschung (UFZ) und der Martin-Luther-Universität Halle-Wittenberg (MLU) wesentlich dazu bei, die Reaktion von Ökosystemen auf menschlich verursachte Nährstoffeinträge zu verstehen. Die Ergebnisse wurden in der Fachzeitschrift Ecology Letters veröffentlicht.
Mehr20.10.2022 | iDiv-Mitglieder, Medienmitteilung, TOP NEWS
Globale Vegetationskarten aus Handy-Daten
Leipzig. Infomationslücken in globalen Karten zu Pflanzenmerkmalen können mit Daten aus Naturbestimmungsapps geschlossen werden. Dies konnten Forschende der Universität Leipzig, des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) und weiterer Einrichtungen anhand von Daten der beliebten App iNaturalist zeigen. Ergänzt mit Daten zu Pflanzenmerkmalen ergeben iNaturalist-Daten wesentlich präzisere Karten als bisherige Ansätze, die auf Extrapolation kleiner Datenbanken basieren. Die neuen Karten bilden unter anderem eine verbesserte Grundlage für das Verständnis von Pflanzen-Umwelt -Interaktionen und zur Erdsystemmodellierung. Die Studie wurde in Nature Ecology and Evolution veröffentlicht.
Mehr19.10.2022 | iDiv-Mitglieder, Medienmitteilung, TOP NEWS
Ökologische Schieflage: Wie sich die Pflanzenvielfalt in Deutschland in den letzten 100 Jahren verändert hat
Basiert auf einer Medienmitteilung der Martin-Luther-Universität Halle-Wittenberg (MLU) In Deutschlands Pflanzenwelt hat es in den letzten einhundert Jahren deutlich mehr Verlierer als Gewinner gegeben. Während die Bestände vieler Arten geschrumpft sind, konnten einige ihre Vorkommen massiv ausweiten. Gewinne und Verluste sind also sehr ungleich verteilt. Das aber ist ein Indiz für einen großräumigen Verlust an Artenvielfalt, warnt ein Forschungsteam um Dr. Ute Jandt und Prof. Dr. Helge Bruelheide von der Martin-Luther-Universität Halle-Wittenberg (MLU) und dem Deutschen Zentrum für integrative Biodiversitätsforschung (iDiv) im Fachjournal Nature.
Mehr17.10.2022 | iDiv-Mitglieder, Medienmitteilung, TOP NEWS
Das koloniale Erbe Europas prägt bis heute die Pflanzenwelt
Basiert auf einer Medienmitteilung der Universität Wien Wien/Leipzig. Durch koloniale Handelspolitik wurden die Floren besetzter Gebiete geprägt, diese Veränderungen sind bis heute sichtbar und finden teils immer noch statt. Das stellte ein internationales Forschungsteam unter Leitung der Universität Wien und Beteiligung von Forschenden des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) fest. Die Pflanzenwelten in Gebieten, die ehemals von der gleichen Kolonialmacht besetzt wurden, ähneln einander heute noch stark. Diese Ähnlichkeit nimmt zudem mit der Länge der ehemaligen Besetzung zu. Die neuen Erkenntnisse wurden in der Fachzeitschrift Nature Ecology and Evolution veröffentlicht.
Mehr12.10.2022 | Experimentelle Interaktionsökologie, Medienmitteilung, TOP NEWS
Globale Studie: Wenige der ökologisch wertvollsten Böden sind geschützt
Halle, Leipzig, Sevilla. Orte mit ökologisch besonders wertvollen Böden werden nur unzureichend durch bestehende Schutzgebiete abgedeckt. Das ist die Schlussfolgerung einer Studie, die in der Fachzeitschrift Nature erschienen ist. Ein internationales Forschungsteam ermittelte hierfür verschiedene sogenannte bodenökologische Werte. Diese unterschieden sich stark zwischen den Erdteilen. So war in Ökosystemen gemäßigter Breiten die lokale Bodenbiodiversität besonders hoch, während in Böden kühlerer Klimate Ökosystemdienstleistungen wie Kohlenstoffspeicherung hohe Werte erreichten. Laut den Forschenden werden bodenökologische Werte im Naturschutz zu wenig berücksichtigt; die neue Studie zeigt, wo Schutzmaßnahmen am nötigsten ist.
Mehr01.10.2022 | Makroökologie und Gesellschaft, Medienmitteilung, TOP NEWS
Landrechte und Entwaldung sind eng verknüpft
Leipzig. Die Abholzung tropischer Wälder führt zu einem starken Rückgang der Biodiversität und der hiesigen Kohlenstoffspeicher. Forschende vom Deutschen Zentrum für integrative Biodiversitätsforschung (iDiv) und der Universität Leipzig haben nun den Zusammenhang zwischen Landrechten und der Entwaldung in Brasilien genauer untersucht. Im Fachmagazin Nature Communications zeigen sie auf, dass schlecht definierte Landrechte Hand in Hand mit einer erhöhten Abholzungsrate gehen. Eine Privatisierung dieser Gebiete, wie sie in den Tropen häufig vorangetrieben wird, kann jedoch nur dann Abhilfe schaffen, wenn sie unter strengen Umweltauflagen geschieht.
Mehr29.09.2022 | Biodiversität und Naturschutz, Forschung, Makroökologie und Gesellschaft, Medienmitteilung, TOP NEWS
Historischer Rückgang des Wolfes auf der Iberischen Halbinsel
Basiert auf einer Medienmitteilung des Consejo Superior de Investigaciones Científicas, Spanien (CSIC) Sevilla/Leipzig. Der Wolf war in der Mitte des 19. Jahrhunderts auf mindestens 65 Prozent der Iberischen Halbinsel verbreitet. Die jüngste Ausbreitung der Art hingegen bedeuten kaum mehr als eine Stabilisierung. Dies ist das Ergebnis einer Studie, die von der Biologischen Station Doñana des Consejo Superior de Investigaciones Científicas (EBD-CSIC) in Zusammenarbeit mit dem Deutschen Zentrum für integrative Biodiversitätsforschung (iDiv) und der Martin-Luther-Universität Halle-Wittenberg (MLU) durchgeführt wurde. Die Schlussfolgerungen des Forscherteams beruhen auf der Analyse historischer Informationen aus einer geografischen Erhebung aus der Mitte des 19. Die Studie, die in der Fachzeitschrift Animal Conservation veröffentlicht wurde, liefert neue Informationen über die Geschichte des Rückgangs von Wölfen aufgrund menschlicher Verfolgung.
Mehr07.09.2022 | Medienmitteilung, sDiv, TOP NEWS
Lage, Lage, Lage! Was zur Verholzung von Pflanzen auf Inseln führt
Basiert auf einer Medienmitteilung der Philipps-Universität Marburg Marburg/Leipzig/Leiden. Verstärkte Trockenheit, das Fehlen von Fressfeinden und Abgeschiedenheit führen dazu, dass Pflanzen auf Inseln zu verholzten Wuchsformen neigen. Dabei spielt auch die jeweilige Lage der Inseln, auf der die betroffenen Arten heimisch sind eine Rolle. Das ist das Ergebnis einer Studie unter der Leitung der Philipps-Universität Marburg und des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) zusammen mit dem Naturalis Biodiversitätszentrums in Leiden und weiterer Einrichtungen. Die nun in der Fachzeitschrift PNAS veröffentlicht Studie des deutsch-niederländischen Forschendenteam zeigt, wie Inseln als natürliche Laboratorien der Evolution wirken.
Mehr01.09.2022 | Forschung, iDiv-Mitglieder, Medienmitteilung, TOP NEWS
Große Pflanzenvielfalt ist oft auf kleinstem Raum zu finden
Basiert auf einer Medienmitteilung der Martin-Luther-Universität Halle-Wittenberg Halle/Leipzig. Die Steppen Osteuropas beherbergen ähnlich viele Pflanzenarten wie Regionen des Amazonasregenwaldes. Das zeigt sich aber nur, wenn Forschende die Arten nicht nur auf großen Flächen von vielen Hektar zählen. Warum sich aber das Zählen auch auf viel kleineren Flächen im Bereich von wenigen bis einigen Hundert Quadratmetern lohnt, zeigt jetzt ein internationales Forschungsteam unter Leitung der Martin-Luther-Universität Halle-Wittenberg (MLU) und des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) Halle-Jena-Leipzig im Fachjournal Nature Ecology & Evolution. Die Ergebnisse könnten für neue, passgenauere Naturschutzkonzepte nützlich sein.
Mehr15.08.2022 | Medienmitteilung, Science-Policy, TOP NEWS
Nationalparke – Inseln in einer Wüste?
Leipzig/Jena/Bonn. Wie wirksam ist der Biodiversitätsschutz europäischer und afrikanischer Nationalparke? Dies scheint stark mit den gesellschaftlichen und wirtschaftlichen Bedingungen zusammenzuhängen, in die sie eingebettet sind. Aber selbst unter den günstigsten Bedingungen können die Bedrohungen der biologischen Vielfalt in den Nationalparken nicht vollständig beseitigt werden, wenn sie nicht gleichzeitig auch außerhalb verbessert werden. Zu diesem Ergebnis kommt eine neue Studie unter Leitung des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv), des Max-Planck-Instituts für evolutionäre Anthropologie (MPI-EVA) und der Universität Bonn in Zusammenarbeit mit dem Helmholtz-Zentrum für Umweltforschung (UFZ), der Universität Leipzig, der Friedrich-Schiller-Universität Jena und vielen weiteren Institutionen. Die Studie, die in der Fachzeitschrift Nature Sustainability veröffentlicht wurde, unterstreicht die dringende Notwendigkeit besserer Nationalpark-Netzwerke.
Mehr27.07.2022 | iDiv-Mitglieder, Medienmitteilung, TOP NEWS
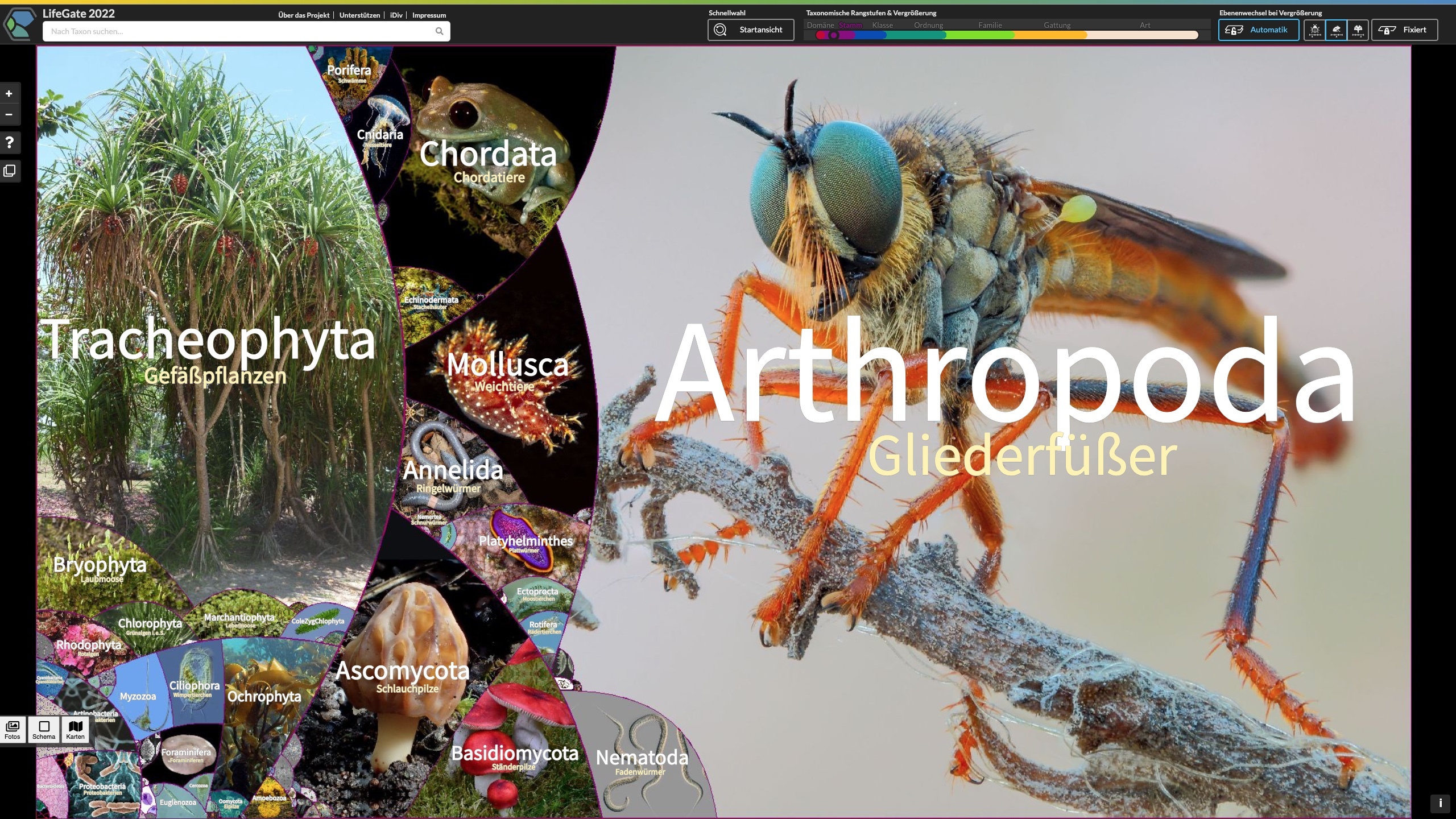
LifeGate – Neue interaktive Karte zeigt die ganze Vielfalt des Lebens
Gemeinsame Medienmitteilung der Universität Leipzig (Botanischer Garten) und des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) Leipzig. Wissenschaftler aus Leipzig haben eine riesige, digitale Karte veröffentlicht, welche die ganze Vielfalt des Lebens in Tausenden Fotos zeigt. Das sogenannte LifeGate umfasst alle 2,6 Millionen bekannten Arten des Planeten und sortiert diese nach ihrer Verwandtschaft. Die interaktive Karte ist nun für jeden kostenlos nutzbar unter lifegate.idiv.de.
Mehr19.07.2022 | Biodiversität und Naturschutz, Medienmitteilung, TOP NEWS
Künftige Prioritäten für die Erhaltung von Ökosystemen in den Tropischen Anden
Gemeinsame Presseerklärung von iDiv und NatureServe Washington D.C./Leipzig. Nur etwa fünf Prozent aller in den Tropischen Anden vorkommender Ökosysteme sind in den dort ausgewiesenen Schutzgebieten auch angemessen vertreten, nimmt man die Zielvorgaben des Übereinkommens über die biologische Vielfalt (CBD) zum Maßstab. Laut CBD sollten mindestens 30 Prozent der Land- und Wasserflächen einschließlich der gesamten dort vorkommenden Ökosystem-Vielfalt geschützt werden, um das Aussterberisiko von Arten verringern zu können. Allerdings erfüllen derzeit nur sehr wenige Orte dieser Welt dieses CBD-Ziel. In den Tropischen Anden (in den vier Ländern Bolivien, Kolumbien, Ecuador und Peru) könnte der Anteil der Ökosysteme, die das CBD-Ziel erfüllen, auf 31 Prozent erhöht werden. Das entspräche insgesamt 39 Ökosystemtypen. Dazu müssten jedoch Regierungen und die Zivilgesellschaft zusätzliche Schutzgebiete für die biologische Vielfalt (Key Biodiversity Areas, KBA) ausweisen. Diese KBAs müssten den international anerkannten Standard für Gebiete erfüllen, der wesentlich zum weltweiten Fortbestand der biologischen Vielfalt beiträgt. Dies ist das Ergebnis einer neuen Studie, die von NatureServe, dem Deutschen Zentrum für integrative Biodiversitätsforschung (iDiv), der Martin-Luther-Universität Halle-Wittenberg (MLU) sowie anderen Institutionen durchgeführt und nun in der Fachzeitschrift Remote Sensing veröffentlicht wurde. Die Studie zeigt auch, wie Schutz-Entscheidungen auf verschiedenen Ebenen durch die Verbindung „essentieller Biodiversitätsvariablen (EBVs)“ mit KBAs beeinflusst werden können.
Mehr18.07.2022 | Experimentelle Interaktionsökologie, Medienmitteilung
Mehr Arten als bisher angenommen könnten vom Aussterben bedroht sein
Basiert auf einer Medienmitteilung der Universität Minnesota Saint Paul/Leipzig. Im Mittel 30 Prozent aller Arten weltweit könnte vom Aussterben bedroht oder in den letzten 500 Jahren bereits ausgestorben sein. Dies ergaben Schätzungen von 3.331 Expertinnen und Experten, die sich mit der biologischen Vielfalt in 187 Ländern beschäftigen. Diese große und diverse Expertengruppe wurde im Rahmen einer Umfrage, geleitet von Forschenden der Universität Minnesota und unter Beteiligung von iDiv und der Universität Leipzig, gebeten, Einschätzungen zum Wandel der von ihnen beforschten Arten zu geben. Die Ergebnisse sollen Wissenslücken bestehender wissenschaftlicher Bewertungen der globalen Biodiversität verringern und so die Wissensbasis für politische Entscheidungen verbessern. Die Studie wurde in der Zeitschrift Frontiers in Ecology and the Environment veröffentlicht.
Mehr14.07.2022 | Biodiversitätssynthese, Medienmitteilung, TOP NEWS
Nordamerikanische Vögel folgen sich wandelndem Klima nur teilweise
Leipzig/Halle/Sevilla. Manche nordamerikanische Vogelarten leben zunehmend an Orten, die nicht ihren bevorzugten klimatischen Bedingungen entsprechen. Dieses Phänomen der Klima-Entkopplung ist besonders ausgeprägt bei solchen Arten, die auf bestimmte Lebensräume spezialisiert sind. Obwohl das Klima nun anderorts günstigster für sie sein mag, verharren diese Tiere teilweise in ihren angestammten Lebensräumen. Dies sind die Ergebnisse einer Studie des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv), der Universität Leipzig, der Martin-Luther-Universität Halle-Wittenberg (MLU) und der Biologischen Station Doñana, die jetzt in der Fachzeitschrift Nature Ecology & Evolution veröffentlicht worden ist. Die bei einem Viertel der untersuchten Vogelarten festgestellte Klima-Entkopplung kann diese Arten zusätzlich belasten und Bestandsrückgange verstärken.
Mehr08.07.2022 | Biodiversität und Mensch, Medienmitteilung, TOP NEWS
Schutz von Schmetterlingen in Leipzig
Mehr30.06.2022 | Biodiversität und Mensch, Medienmitteilung, TOP NEWS
Sechs Grundsätze für die EU-Agrarpolitik, um den Biodiversitätsverlust aufzuhalten
Leipzig/Rostock. Um dem Verlust der biologischen Vielfalt aufzuhalten, könnte sich die Europäische Union bei der Gestaltung ihrer künftigen Agrarpolitik an sechs Grundsätzen orientieren, begleitet von mehrjährigen Vereinbarungen und progressiven Zahlungssystemen. Dies sind die Kernpunkte der Empfehlungen von über 300 Wissenschaftlern aus 23 EU-Mitgliedstaaten, die im Auftrag der Europäischen Kommission konsultiert wurden. Koordiniert wurde der Prozess vom Deutschen Zentrum für integrative Biodiversitätsforschung (iDiv), dem Helmholtz-Zentrum für Umweltforschung (UFZ), dem Thünen-Institut für Lebensverhältnisse in ländlichen Räumen und der Universität Rostock. Eine Zusammenfassung der Ergebnisse dieses umfangreichen Konsultationsprozesses wurde jetzt in der Zeitschrift Conservation Letters veröffentlicht.
Mehr29.06.2022 | iDiv-Mitglieder, Medienmitteilung, TOP NEWS
Leben im Erdinneren so produktiv wie in manchen Meeresbereichen
Gemeinsame Medienmitteilung von iDiv und der Friedrich-Schiller-Universität Jena Jena. Mikroorganismen in Grundwasserleitern tief unter der Erdoberfläche produzieren ähnlich viel Biomasse wie solche in manchen Meeresbereichen. Zu diesem Ergebnis kommen Forschende unter Leitung der Friedrich-Schiller-Universität Jena und des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv). Mit einer einzigartigen, hochempfindlichen Messmethode mit radioaktivem Kohlenstoff konnten sie erstmals nachweisen, dass diese Lebensgemeinschaften in absoluter Dunkelheit nicht auf Sonnenenergie angewiesen sind. Stattdessen können sie ihre Energie selbständig aus der Oxidation von Gestein oder aus Stoffen gewinnen, die nach unten transportiert werden. Die Studie wurde in Nature Geoscience veröffentlicht.
Mehr24.06.2022 | iDiv, Medienmitteilung, TOP NEWS
Nachwuchsforschende ergründen Auswirkungen menschlicher Aktivitäten auf den Boden
Gemeinsame Medienmitteilung von Universität Leipzig und iDiv Leipzig. “Rätselhaft doch wunderschön” – so beschreibt Dr. Anton Potapov die Welt der Lebewesen, die unter unseren Füßen leben. Der Ökologe und Mikrobiologe baut ab dem 1. Juli 2022 eine neue Juniorforschungsgruppe am Deutschen Zentrum für integrative Biodiversitätsforschung (iDiv) und an der Universität Leipzig auf. Das Ziel: Die Rolle von Bodenorganismen im Ökosystem genauer unter die Lupe zu nehmen. Potapovs Arbeit wird in den kommenden Jahren von der Deutsche Forschungsgemeinschaft (DFG) über das Emmy Noether-Programm mit 1 Million Euro unterstützt.
Mehr09.06.2022 | Experimentelle Interaktionsökologie, iDiv-Mitglieder, Medienmitteilung, TOP NEWS
Was dich nicht umbringt, macht dich stärker
Basiert auf einer Medienmitteilung der Universität Zürich Zürich, Leipzig. Trockenstresserfahrungen von Pflanzengemeinschaften im artenreichen Grünland erhöhen die Trockenresistenz der Folgegenerationen. Diesen generationenübergreifenden Effekt hat ein internationales Forscherteam unter der Leitung der Universität Zürich mit Beteiligung des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) und der Universität Leipzig an rund 1000 experimentellen Pflanzengemeinschaften in Töpfen nachgewiesen und in der Zeitschrift Nature Communications veröffentlicht. Die Ergebnisse deuten darauf hin, dass extreme Klimaereignisse, wenn sie Arten nicht vollständig verdrängen, die Beständigkeit der biologischen Vielfalt und das Funktionieren von Ökosystemen in einer Zukunft mit häufigeren Extremereignissen verbessern könnten.
Mehr06.06.2022 | Evolution von Symbiosen, iDiv, Medienmitteilung, TOP NEWS
Evolution: Neue Emmy Noether-Gruppe untersucht Zusammenspiel von Bakterien und Insekten
Gemeinsame Pressemitteilung von der Martin-Luther Universität Halle-Wittenberg und iDiv Halle/Leipzig. Die Deutsche Forschungsgemeinschaft (DFG) nimmt den Biologen Dr. Michael Gerth in das Emmy Noether-Programm auf und unterstützt seine Arbeit in den kommenden Jahren mit bis zu 1,4 Millionen Euro. Mit der Förderung wird Gerth aus Großbritannien an die Martin-Luther-Universität Halle-Wittenberg (MLU) wechseln und seine eigene Arbeitsgruppe am Deutschen Zentrum für integrative Biodiversitätsforschung (iDiv) etablieren. Im Fokus seiner Forschung steht die Evolution von speziellen Bakterien, die in Fliegen, Bienen und anderen Insekten leben.
Mehr03.06.2022 | Biodiversität und Mensch, Medienmitteilung, TOP NEWS
Wohl dem, der Wärme liebt – Insekten im Klimawandel
Basiert auf einer Medienmitteilung der Technischen Universität München (TUM) München/Leipzig. Wärmeliebende Insektenarten profitieren in Deutschland von der Klimaerwärmung. Dabei variieren die Trends verschiedener Insektengruppen deutlich. Während die Bestände von Schmetterlingen und Heuschrecken häufiger ab- als zunahmen, zeigten Libellen überwiegend positive Trends. Zu diesem Schluss kommt eine neue Studie unter Leitung der Technischen Universität München (TUM), des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) und der Friedrich-Schiller-Universität Jena. Um erhebliche Datenlücken zu schließen, wertete das Forschungsteam eine umfangreiche Sammlung bislang kaum genutzter Daten zu über 200 Insektenarten in Bayern seit 1980 aus. Die Studie wurde in Global Change Biology veröffentlicht.
Mehr02.06.2022 | Medienmitteilung, TOP NEWS
Größte Erbguterfassung wildlebender Schimpansen
Basiert auf einer Medienmitteilung des Instituts für Evolutionsbiologie (IBE) in Barcelona Barcelona/Leipzig. Den größten genetischen Katalog wildlebender Schimpansenpopulationen in Afrika hat ein internationales Forschungsteam unter der Leitung des Instituts für Evolutionsbiologie (IBE), des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv), des Max-Planck-Instituts für evolutionäre Anthropologie (MPI-EVA) und der Universität Leipzig erstellt. Erstmals wurden die genetischen Informationen aus Hunderten von Kotproben aus dem gesamten Verbreitungsgebiet der Tiere sequenziert. Dieser Katalog, der in der Fachzeitschrift Cell Genomics veröffentlicht wurde, trägt maßgeblich zur Klärung der Evolutionsgeschichte dieser Menschenaffen bei. Darüber hinaus kann er helfen, Routen und Quellen des illegalen Handels zu kartieren, die zum Schutz dieser bedrohten Art genutzt werden können.
Mehr01.06.2022 | Biodiversitätstheorie, Medienmitteilung, TOP NEWS
Fotos von Amazonastieren liefern umfangreiche Daten zur Artenvielfalt
Manaus/São Paulo/Jena/Leipzig. Ein internationales Forschendenteam hat die größte Datensammlung aus Kamerafallen über Tiere des Amazonas-Regenwaldes veröffentlicht. Die Sammlung umfasst derzeit über 120.000 Datensätze mit Zeit- und Ortinformationen. Sie wird die Forschung über den Bestand, die Vielfalt und die Lebensraumbedingungen von Jaguaren, Tukanen, Harpyien und vielen anderen gefährdeten Regenwaldarten verbessern und zu deren Schutz beitragen. 147 Wissenschaftler aus 122 Forschungseinrichtungen und Naturschutzorganisationen arbeiteten unter der Leitung des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) und der Friedrich-Schiller-Universität Jena zusammen, um diese neue Datenbank aufzubauen, die auf Kamerafallenfotos basiert. Sie wurde jetzt in der Zeitschrift Ecology veröffentlicht.
Mehr31.05.2022 | iDiv-Mitglieder, Medienmitteilung, TOP NEWS
Gesunde Entwicklung dank älterer Geschwister
Basiert auf einer Medienmitteilung des Max-Planck-Instituts für evolutionäre Anthropologie (MPI-EVA) Leipzig. Selbst milde Formen von Stress bei schwangeren Frauen können noch Jahre nach der Geburt negative Auswirkungen auf das Verhalten ihrer Kindern haben. Ältere Geschwister können diesen Effekt jedoch mildern. Das haben Forschende des Helmholtz Zentrums für Umweltforschung (UFZ), der Universität Leipzig (UL), des Max-Planck-Instituts für evolutionäre Anthropologie (MPI-EVA) und des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) herausgefunden. Die Studie wurde in der Fachzeitschrift BMC Public Health veröffentlicht.
Mehr18.05.2022 | Biodiversität und Naturschutz, Medienmitteilung, TOP NEWS
Gärtnern mit heimischen Pflanzen für den Arterhalt
Halle/Leipzig. Auf urbanen Grünflächen könnten vermehrt rückläufige heimische Arten gepflanzt werden. Wie dieses große Potenzial für den Artenschutz genutzt werden kann, beschreiben Forschende des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv), der Martin-Luther-Universität Halle-Wittenberg (MLU), der Universität Leipzig und anderer Einrichtungen. In ihrer jüngsten Studie, die in der Zeitschrift Nature Sustainability veröffentlicht worden ist, empfehlen sie konkrete Maßnahmen des Conservation Gardenings für eine Trendwende im Gartenbau.
Mehr09.05.2022 | iDiv, iDiv-Mitglieder, Medienmitteilung, TOP NEWS
Über vier Millionen Euro für die Forschung an Bäumen und Sträuchern
Halle/Leipzig/Jena/Beijing. Das internationale Graduiertenkolleg TreeDì kann seine Arbeit fortsetzen. Der Senat der Deutschen Forschungsgemeinschaft (DFG) hat am Freitag seine Weiterförderung mit über vier Millionen Euro bis 2027 beschlossen. Das Programm wird als Kooperation der Martin-Luther-Universität Halle-Wittenberg (MLU), der Friedrich-Schiller-Universität Jena und der Universität Leipzig sowie der Universität der Chinesischen Akademie der Wissenschaften (UCAS) betrieben. Ziel der Forschung ist ein besseres Verständnis der Interaktionen von Bäumen und Sträuchern in Wäldern. Viele Promovierenden auf deutscher Seite arbeiten beim Deutschen Zentrum für integrative Biodiversitätsforschung (iDiv). Zahlreiche iDiv-Wissenschaftlerinnen und -Wissenschaftler sind bei TreeDì beteiligt, beispielsweise in der Lehre.
Mehr29.04.2022 | Evolution und Adaptation, Medienmitteilung, TOP NEWS
Aussterben der Dinosaurier veränderte Pflanzenevolution
Leipzig, Amsterdam, Zürich. Das Fehlen großer Pflanzenfresser nach dem Aussterben der Dinosaurier hat die Pflanzenevolution verändert. Die 25 Millionen Jahre lange Abwesenheit großer Pflanzenfresser verlangsamte die Entwicklung neuer Pflanzenarten. Verteidigungsmerkmale wie Stacheln bildeten sich zurück und die Früchte wurden größer. Dies hat ein Forschendenteam unter Leitung des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) und der Universität Leipzig am Beispiel von Palmen nachgewiesen. Sie konnten auch zeigen, wie tiefgreifend die Veränderungen waren: Selbst das Wiederauftreten großer Pflanzenfresser Millionen Jahre später konnte die bereits eingetretenen Veränderungen nur teilweise überschreiben. Die Studie wurde in der Fachzeitschrift Proceedings of the Royal Society B veröffentlicht. Sie ermöglicht einen Blick in die erdgeschichtliche Vergangenheit und trägt gleichzeitig zu einem besseren Verständnis der Folgen heutiger Aussterbeprozesse bei.
Mehr27.04.2022 | Biodiversität und Naturschutz, Medienmitteilung, TOP NEWS
Jede fünfte Reptilienart ist weltweit vom Aussterben bedroht
Mehr26.04.2022 | Biodiversität und Mensch, Medienmitteilung, TOP NEWS
Gemeinsam Wissen schaffen – Die Citizen-Science-Strategie 2030
Basiert auf einer Medienmitteilung des Helmholtz-Zentrums für Umweltforschung (UFZ) Berlin/Leipzig. Gemeinsam Wissen schaffen – das ist das Ziel von Citizen Science. Am 29. April 2022 stellen Wissenschaftlerinnen und -wissenschaftler der Helmholtz- und der Leibniz-Gemeinschaft sowie vom Deutschen Zentrum für integrative Biodiversitätsforschung (iDiv) die Citizen-Science-Strategie 2030 für Deutschland der Öffentlichkeit vor. In einem Citizen-Science-Festival werden zudem eine Reihe aktueller Projekte vorgestellt. Die Strategie setzt sich mit den größten Herausforderungen und Potenzialen von Citizen Science in den nächsten zehn Jahren auseinander. Sie beinhaltet 94 konkrete Handlungsempfehlungen, um Bürgerforschung in Deutschland weiterzuentwickeln und dauerhaft in Wissenschaft, Gesellschaft und Politik zu verankern. Die Citizen-Science-Strategie 2030 Deutschland wurde in einem zweijährigen partizipativen Prozess mit mehr als 200 Akteurinnen und Akteuren aus 136 Organisationen erarbeitet. Der Prozess wurde zu großen Teilen durch die Deutsche Bundesstiftung Umwelt (DBU) und das Bundesministerium für Bildung und Forschung (BMBF) gefördert.
Mehr12.04.2022 | Biodiversität und Mensch, Medienmitteilung, TOP NEWS
Wie gesund sind unsere Bäche?
Basierend auf einer Medienmitteilung des Bund für Umwelt und Naturschutz Deutschland (BUND) Von April bis Juli 2022 erforschen Bürger:innen quer durch Deutschland, wie gesund unsere Bäche sind. Das Citizen-Science-Projekt von Bund für Umwelt und Naturschutz Deutschland (BUND), Helmholtz-Zentrum für Umweltforschung (UFZ) und Deutschem Zentrum für integrative Biodiversitätsforschung (iDiv) untersucht langfristig den ökologischen Zustand kleiner Fließgewässer, darunter deren Pestizidbelastung. 2021 wurde die Citizen-Science-Methode in Mitteldeutschland systematisch getestet. Jetzt startet die erste Messkampagne mit deutschlandweit etwa 650 Teilnehmenden, die in Kleingruppen Bäche unter die Lupe nehmen.
Mehr07.04.2022 | iDiv, iDiv-Mitglieder, Medienmitteilung, TOP NEWS
Christian Wirth erhält Leipziger Wissenschaftspreis 2022
Basiert auf einer Medienmitteilung der Stadt Leipzig, der Universität Leipzig, der Sächsischen Akademie der Wissenschaften zu Leipzig Leipzig. Christian Wirth, Professor für spezielle Botanik und funktionelle Biodiversität an der Universität Leipzig, Fellow am Max-Planck-Institut für Biogeochemie in Jena und Sprecher des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv), ist heute mit dem Leipziger Wissenschaftspreis ausgezeichnet worden. Mit diesem würdigen die Stadt Leipzig, die Universität Leipzig und die Sächsische Akademie der Wissenschaften zu Leipzig Forschende, die auf höchstem wissenschaftlichen Niveau arbeiten und maßgeblich dazu beitragen, Leipzigs Ruf als Stadt der Wissenschaften und Bildung national und international zu festigen.
Mehr30.03.2022 | Experimentelle Interaktionsökologie, Medienmitteilung, TOP NEWS
Europäische Regenwürmer verringern Insektenbestände in Wäldern Nordamerikas
Leipzig/Calgary. Nach Nordamerika eingeschleppte Regenwürmer beeinträchtigen die oberirdisch lebende Insektenfauna. Diese Beobachtung beschreiben Bodenökologinnen und -ökologen unter Leitung des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) und der Universität Leipzig in der Fachzeitschrift Biology Letters. Dies gilt sowohl für die Häufigkeit und Biomasse als auch die Artenzahl der Insekten. Die Ergebnisse zeigen, dass Veränderungen von Artengemeinschaften wie etwa Insekten bisher noch wenig beachtete Ursachen haben können. Diese sollten zum Schutz und Management der Insektengemeinschaften stärker berücksichtigt werden.
Mehr23.02.2022 | Biodiversitätssynthese, Medienmitteilung, TOP NEWS
Während manche Insekten zurückgehen, können andere häufiger werden
Leipzig/Halle/Jena. Bestandsveränderungen einer Insektengruppe, z. B. Heuschrecken, sagen wenig darüber aus, wie es anderen Insekten im selben Lebensraum ergeht, z. B. Fliegen. Denn während sich Insektengruppen an manchen Orten ähnlich entwickeln, können die Trends an anderen Orten ganz unterschiedlich sein. Diese Ergebnisse einer Metastudie haben Wissenschaftlerinnen und Wissenschaftler in der Fachzeitschrift Biology Letters veröffentlicht. Das Forschungsteam unter Leitung des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv), der Martin-Luther-Universität Halle-Wittenberg (MLU), der Friedrich-Schiller-Universität Jena und des Helmholtz-Zentrums für Umweltforschung (UFZ) untersuchte Insekten-Langzeitdaten von mehr als 900 Orten weltweit. Die Ergebnisse unterstreichen, wie wichtig es ist, mehrere Artengruppen gleichzeitig zu monitoren, um die Natur zielgerichtet schützen zu können.
Mehr07.02.2022 | Biodiversität und Naturschutz, Medienmitteilung, TOP NEWS
7 bis 9 Prozent aller europäischen Gefäßpflanzen im weltweiten Fortbestand gefährdet
Halle, Leipzig. Sieben bis neun Prozent aller in Europa vorkommenden Gefäßpflanzenarten sind in ihrem weltweiten Fortbestand gefährdet. Das ist das Ergebnis einer Studie unter Leitung des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv), der Martin-Luther-Universität Halle-Wittenberg und der Universität Leipzig. Die Forschenden kombinierten Rote Listen gefährdeter Pflanzenarten in Europa mit Daten ihrer weltweiten Verbreitung. Die Studie ist in der Fachzeitschrift Plants, People, Planet veröffentlicht worden. Die Arbeit hilft, das Gesamt-Gefährdungsrisiko von Pflanzenarten einzuschätzen und unterstützt so die Grundlage internationaler Naturschutzaktivitäten.
Mehr03.02.2022 | Biodiversität und Mensch, Medienmitteilung, TOP NEWS
Die Liebe zur Natur ist teilweise erblich
Basiert auf einer Medienmitteilung von PLoS BiologySingapur/Exeter/Brisbane/Leipzig. Die Wertschätzung von Natur und die damit verbundene Neigung, sich in der Natur aufzuhalten, sind vererbbare Eigenschaften des Menschen. Das ist das Ergebnis einer groß angelegten Studie mit britischen Zwillingen, die von der National University of Singapore, der University of Exeter, der University of Queensland, dem Helmholtz-Zentrum für Umweltforschung (UFZ) und dem Deutschen Zentrum für integrative Biodiversitätsforschung (iDiv) gemeinschaftlich durchgeführt wurde. Die Studie wurde nun in der Zeitschrift PLoS Biology veröffentlicht.
Mehr18.01.2022 | Medienmitteilung, Molekulare Interaktionsökologie, TOP NEWS
Bäume rufen Vögel und räuberische Insekten um Hilfe
Leipzig/Jena. Waldbäume senden bei Befall durch Raupen und andere Pflanzenfresser Duftstoffe aus. Damit locken sie räuberische Insekten und sogar Vögel an und befreien sich so von ihren Plagegeistern. Was bislang nur in Labor- oder Gartenexperimenten nachgewiesen worden war, konnten Forschende unter Leitung des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv), der Friedrich-Schiller-Universität Jena und der Universität Leipzig nun erstmals in einem natürlichen Lebensraum zeigen – im 40 Meter hohen Kronendach des Leipziger Auwaldes. Die chemischen Hilferufe sind so wirksam, dass sie die Zusammensetzung der Insektengemeinschaft im Blätterdach maßgeblich bestimmen. Dieses Wissen könnte künftig für die natürliche Schädlingsbekämpfung in Land- und Forstwirtschaft genutzt werden, schreiben die Forschenden im Fachmagazin Ecology Letters.
Mehr17.01.2022 | Biodiversität und Naturschutz, iDiv-Mitglieder, Medienmitteilung, TOP NEWS, UFZ-News
Kann „Rewilding“ die Erhaltung der Biodiversität mit nachhaltiger Regionalentwicklung verbinden?
Basiert auf einer Medienmitteilung von Rewilding Oder Delta e.V. und dem UFZ Im November 2021 startete das vom Bundesministerium für Bildung und Forschung (BMBF) geförderte Forschungsprojekt „REWILD_DE – Erhaltung von Biodiversität und Inwertsetzung von Ökosystemleistungen durch Rewilding – Vom Oderdelta lernen“. Akteure aus Wissenschaft und Praxis befassen sich im Rahmen des dreijährigen Projekts gemeinsam mit den Potenzialen von „Rewilding“ für die Wiederherstellung der biologischen Vielfalt und die Förderung einer naturbasierten ökonomischen Entwicklung des Modellgebiets Oderdelta in Vorpommern. Darüber hinaus werden sie untersuchen, inwieweit die gewonnenen Erfahrungen und Ergebnisse auf den überregionalen Biodiversitätsschutz übertragbar sind. Koordiniert wird das Projekt am Helmholtz-Zentrum für Umweltforschung (UFZ), Projektpartner sind das Deutsche Zentrum für integrative Biodiversitätsforschung (iDiv) und die Martin-Luther-Universität Halle-Wittenberg (MLU), die Hochschule für nachhaltige Entwicklung Eberswalde (HNEE) sowie der Verein Rewilding Oder Delta e. V. (ROD) als Praxispartner im Untersuchungsgebiet.
Mehr14.01.2022 | iDiv, Medienmitteilung, TOP NEWS
Globale Biodiversitätsziele in Mitteldeutschland umsetzen
Leipzig. Die Umweltministerin und -minister der mitteldeutschen Länder sowie Vertreterinnen und Vertreter aus Naturschutzorganisationen und -behörden haben sich heute über die Umsetzung der internationalen Biodiversitätsziele auf Länderebene ausgetauscht. Das virtuelle Treffen fand auf Initiative des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) in Leipzig statt und ist Teil eines langfristigen Dialogs.
Mehr23.12.2021 | iDiv-Mitglieder, Medienmitteilung, TOP NEWS
Klima und Boden entscheiden über die Ausprägung von Pflanzenmerkmalen
Basiert auf einer Medienmitteilung des Max-Planck-Instituts für Biogeochemie Zürich/Jena/Leipzig. Ein internationales Forschungsteam hat global wirkende Faktoren identifiziert, die für die verfältigen Formen und Funktionen von Pflanzen verantwortlich sind. Die Forschenden unter der Leitung der Universität Zürich und des Max-Planck-Instituts für Biogeochemie (MPI BGC) in Jena, der Universität Leipzig und des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) analysierten dazu Pflanzendaten aus aller Welt. Die nun in der Zeitschrift Nature Ecology and Evolution veröffentlichte Studie zeigt, wie stark Pflanzenmerkmale wie Größe, Aufbau und Lebensspanne von Klima- und Bodeneigenschaften bestimmt werden. Die daraus abgeleiteten Erkenntnisse könnten Erdsystemmodelle entscheidend verbessern.
Mehr20.12.2021 | iDiv-Mitglieder, Medienmitteilung, TOP NEWS
Extreme Dürren setzen auch Leipziger Auwald zu
Leipzig. Gegen zwei aufeinanderfolgende heiße Dürrejahre war der Leipziger Auwald nicht gewappnet. Das Dürrejahr 2018 konnten die Bäume noch teilweise verkraften. Allerdings häuften sie die andauernden Schäden durch den Trockenstress an und ihr Wachstum brach im zweiten Dürrejahr 2019 je nach Baumart um 9 bis 42 % im Vergleich zu klimatisch normalen Jahren ein. Dies ist das Ergebnis einer Studie, die ein Team unter der Leitung des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) in der Fachzeitschrift Global Change Biology veröffentlicht hat. Die Studie könnte helfen, die Reaktion von Wäldern auf den Klimawandel besser zu verstehen und vorherzusagen.
Mehr17.12.2021 | iDiv-Mitglieder, Medienmitteilung, TOP NEWS
Gut versichert: Wälder mit vielen Baumarten wachsen gleichmäßiger
Leipzig/Beijing. Das jährliche Wachstum von Wäldern schwankt aufgrund von Witterungsextremen wie Dürren und Starkregen. Diese Schwankungen fallen bei artenreichen Wäldern geringer aus als bei artenarmen. Zudem produzieren Wälder mit vielen Baumarten mehr Holz. Dabei kommt es nicht nur auf die Vielfalt der Baumarten an, sondern auch auf die Vielfalt ihrer Eigenschaften. Das konnte ein internationales Forschungsteam unter Leitung des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) und der Chinesischen Akademie der Wissenschaften Beijing (CAS) nachweisen. Die Studienergebnisse sind in der Fachzeitschrift Science Advances erschienen. Sie liefern wichtige Impulse, wie die Forstwirtschaft Wälder mit stabiler Produktivität fördern kann.
Mehr13.12.2021 | iDiv, iDiv-Mitglieder, Medienmitteilung, TOP NEWS
Sensationeller Fund im Leipziger Auwald
Basiert auf einer Medienmitteilung der Universität Leipzig Leipzig. Forschende und Biologiestudierende der Universität Leipzig haben bei einer zoologischen Freilandexkursion im Leipziger Auwald ein extrem seltenes Insekt entdeckt, den Mückenhaft (Bittacus hageni). Gleich mehrere Exemplare gingen ihnen im Blätterdach des Leipziger Auwalds ins Netz. Diese Art von Schnabelfliegen ist in Europa nur an wenigen Stellen zu finden. In Deutschland galt sie bis 2003 als ausgestorben. Der Fund, den die Forschenden in der Zeitschrift Entomologische Nachrichten und Berichte beschreiben, unterstreicht die Bedeutung des Leipziger Auwaldes als einzigartigen aber bedrohten Lebensraum. Er zeigt aber auch, welche wertvollen Entdeckungen durch Studentenexkursionen möglich werden.
Mehr10.12.2021 | Biodiversität und Mensch, Medienmitteilung, TOP NEWS
Spaß am Naturschutz und Gutes tun
Basierend auf einer Medienmitteilung des Thünen-Instituts für Biodiversität
Mehr09.12.2021 | Biodiversitätsökonomik, Medienmitteilung, sDiv, TOP NEWS
Tropische Wälder wieder wachsen lassen
Basierend auf einer Medienmitteilung der Universität Wageningen Wageningen/Leipzig. Tropenwälder verschwinden in alarmierendem Tempo durch Abholzung. Aber sie haben auch das Potenzial, auf verlassenen Flächen natürlich nachzuwachsen. Eine Studie, die diese Woche in Science veröffentlicht wurde, zeigt, dass sich nachwachsende Tropenwälder erstaunlich schnell erholen. Nach 20 Jahren haben sie im Durchschnitt fast 80 % der für Primärwälder charakteristischen Merkmale wiedererlangt. Dies gilt etwa für die Fruchtbarkeit und Kohlenstoffbindung des Bodens, die Baumvielfalt und die Waldstruktur. Die von der Universität Wageningen mit Unterstützung des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) durchgeführte Studie kommt zu dem Schluss, dass natürliche Regeneration eine kostengünstige, naturbasierte Lösung für den Klimaschutz, die Erhaltung der biologischen Vielfalt und die Wiederherstellung von Ökosystemen darstellt.
Mehr09.12.2021 | Biodiversität und Naturschutz, Medienmitteilung, sDiv, TOP NEWS
Allerweltspflanzen verdrängen seltenere Arten
Basiert auf einer Medienmitteilung der Österreichischen Akademie der Wissenschaften (ÖAW) Leipzig/Wien. In mehreren Ökosystemen Europas sind „Allerweltsarten“ auf dem Vormarsch und verdrängen seltenere Pflanzenarten. Dadurch werden die Pflanzengemeinschaften immer ähnlicher. Diese Entwicklung hat ein internationales Team unter Leitung des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) und der Martin-Luther-Universität Halle-Wittenberg (MLU) unter Beteiligung der Österreichischen Akademie der Wissenschaften (ÖAW) erstmals sowohl im Hochgebirge als auch in Wäldern und Wiesen des Tieflands nachgewiesen. Einer der Hauptgründe für diese Artenverschiebung könnten erhöhte Stickstoffmengen in den Böden aus Landwirtschaft und Luftverunreinigung sein. Die Ergebnisse der Studie wurden kürzlich im Fachjournal Ecology Letters veröffentlicht.
Mehr01.12.2021 | Biodiversitätsökonomik, Medienmitteilung, TOP NEWS
Klimaveränderungen und Überfischung dezimierten Ostseehering lange vor der Industrialisierung
Gemeinsame Medienmitteilung mit der Universität Kiel Kiel/Leipzig. Der Zusammenbruch der Sundfischerei in der westlichen Ostsee Ende des 16. Jahrhunderts war die Folge von Überfischung und einer rapiden Veränderung des Klimas – ähnliche Bedingungen wie sie auch heute vorherrschen. Ein Team aus Historikern sowie Fischereiökonomen und Biologen der Christian-Albrechts-Universität zu Kiel (CAU), des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) und der Universität Leipzig hat die Entwicklung der Heringsfischerei in der Ostsee zwischen 1200 und 1650 rekonstruiert. Demnach kollabierte die damals wichtigste Fischerei auf den herbstlaichenden Hering in den 1580er Jahren innerhalb kürzester Zeit, ohne sich bis heute erholen zu können. Die Forscher erkennen darin Parallelen zur aktuellen Entwicklung kommerziell genutzter Fischbestände in der westlichen Ostsee. Die Studie, für die sie verschiedene historische Quellen ausgewertet haben, ist in der Fachzeitschrift Hansische Geschichtsblätter erschienen.
Mehr23.11.2021 | Biodiversität und Mensch, Biodiversität und Naturschutz, iDiv, iDiv-Mitglieder, Medienmitteilung, TOP NEWS
Biologische Vielfalt: Zeit, endlich zu handeln
Leipzig. Um die globalen Ziele zum Erhalt der biologischen Vielfalt zu erreichen, muss die Umsetzung auf nationaler Ebene deutlich verbessert werden. Verbindliche Maßnahmen und verantwortliche Akteure müssen klar definiert und die Umsetzung durch systematisches Monitoring überwacht werden. Diese Empfehlungen stehen im Zentrum eines dreistufigen Rahmenplans, den ein internationales Team von Wissenschaftlerinnen und Wissenschaftlern unter Leitung des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) in der Fachzeitschrift Conservation Letters veröffentlicht hat. Ein erneutes Scheitern der internationalen Vereinbarungen müsse dringend vermieden werden. Vor allem dürfe ein Fehler dieses Mal nicht mehr passieren.
Mehr03.11.2021 | Biodiversitätstheorie, Forschung, Medienmitteilung, TOP NEWS
Wo der Bär läuft
Leipzig/Jena/Oxford. Mithilfe einer neuen Software lassen sich die Bewegungen großer Wildtiere berechnen und damit Konflikte mit Menschen verringern. Die Software ist einfacher als Messungen mithilfe von Funksendern und kann dort eingesetzt werden, wo herkömmliche Methoden versagen. Ein internationales Team unter Leitung des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv), der Friedrich-Schiller-Universität Jena, der Universität Aarhus und der Universität Oxford hat die Beschreibung der neuen Software in der Fachzeitschrift Methods in Ecology and Evolution veröffentlicht.
Mehr14.10.2021 | Arten-Interaktionsökologie, Medienmitteilung, TOP NEWS
Rückgang von Pflanzenbestäubern bedroht Artenvielfalt
Gemeinsame Medienmitteilung mit der Universität Konstanz, basierend auf einer Medienmitteilung der Universität Stellenbosch, Südafrika. Stellenbosch, Konstanz, Leipzig. Etwa 175.000 Pflanzenarten – die Hälfte aller Blütenpflanzen – sind für die Samenbildung und damit für ihre Fortpflanzung überwiegend oder vollständig auf tierische Bestäuber angewiesen. Dies ist das Ergebnis einer aktuellen Studie, die am 13. Oktober 2021 von einem globalen Forschungsnetzwerk mit Beteiligung des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) und der Universität Konstanz in der Zeitschrift Science Advances veröffentlicht wurde. Ein Rückgang in der Zahl dieser Bestäuber könnte daher zu erheblichen Störungen der natürlichen Ökosysteme führen – einschließlich eines Verlustes der biologischen Vielfalt
Mehr13.10.2021 | Evolution und Adaptation, Medienmitteilung, TOP NEWS
Geologisch lebendige Kontinente erzeugen höhere Artenvielfalt
Basiert auf einer Medienmitteilung der ETH Zürich Leipzig, Zürich. Dank eines neuen Computermodells können Forschende des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv)und der ETH Zürich nun besser erklären, weshalb die Regenwälder Afrikas weniger Arten beherbergen als die Tropenwälder Südamerikas und Südostasien. Der Schlüssel zu einer hohen Artenvielfalt ist, wie dynamisch sich die Kontinente über die Zeit entwickelt haben
Mehr06.10.2021 | Biodiversität und Naturschutz, Medienmitteilung, TOP NEWS
Immer mehr Straßen aber kaum Wissen über deren Auswirkungen auf Wildtiere
Basiert auf einer Medienmitteilung der Complutense-Universität Madrid (UCM) Madrid/Leipzig/Halle. Gerade in Regionen mit sehr dichtem Straßennetz wie Deutschland gehören Fahrzeuge vermutlich zu den wesentlichen Lebensbedrohungen aller Arten von Wildtieren. Wie stark sich dieser Faktor jedoch auf die Populationen auswirkt, lässt sich mangels Daten leider nicht darstellen. Dies hat nun ein Wissenschaftlerteam unter Leitung der Complutense-Universität Madrid (UCM), dem deutschen Zentrum für integrative Biodiversitätsforschung (iDiv) sowie der Martin-Luther-Universität Halle-Wittenberg (MLU) in der Zeitschrift Perspectives in Ecology and Conservation gezeigt. Die Analyse einschlägiger Literatur ergab, dass Studien zu stark auf wenige Regionen und Arten beschränkt sind. Die Wissenschaftler sehen in der systematischen Erfassung von tierischen Verkehrsopfern ein großes Potenzial zur Bewertung des Aussterberisikos von Tierarten.
Mehr22.09.2021 | iDiv-Mitglieder, Medienmitteilung, TOP NEWS
Der Zustand terrestrischer Ökosysteme lässt sich mit drei Schlüsselindikatoren erfassen
Basiert auf einer Medienmitteilung des Max-Planck-Instituts für Biogeochemie (MPI BGC) Jena. Ökosysteme erbringen vielfältige Dienstleistungen für den Menschen. Diese hängen von grundlegenden Ökosystemfunktionen ab, die sowohl durch das vorherrschende Klima und Artenvorkommen als auch durch menschliche Eingriffe beeinflusst werden. Ein großes internationales Forschungsteam unter der Leitung des Max-Planck-Instituts für Biogeochemie (MPI-BGC) in Jena und des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) hat drei Schlüsselindikatoren ermittelt, die die Funktionsweise terrestrischer Ökosysteme beschreiben: 1) die Fähigkeit, die Primärproduktivität zu maximieren, 2) die Effizienz der Wassernutzung und 3) der Wirkungsgrad der Kohlenstoffnutzung. Das Monitoring dieser drei Kennzeichen ermöglicht es, einzuschätzen, wie anpassungsfähig ein Ökosystem gegenüber Klima- und Umweltveränderungen ist und wie es sich unter bestimmten Bedingungen weiterentwickeln kann. Die Studie wurde im Fachmagazin Nature veröffentlicht.
Mehr17.09.2021 | Forschung, iDiv, Medienmitteilung, TOP NEWS
Artensterben auch in der Literatur
Leipzig/Frankfurt a.M. Die biologische Vielfalt nimmt in der westlich geprägten Literatur seit den 1830er Jahren kontinuierlich ab. Das ist das Ergebnis einer umfangreichen, interdisziplinären Studie, die von Leipziger Forschern geleitet wurde. Die Forscher haben dafür knapp 16.000 Werke untersucht, die zwischen 1705 und 1969 erschienen sind. Die Studie wurden in der Fachzeitschrift People and Nature veröffentlicht. Die Ergebnisse deuten die Forscher als Hinweis auf eine zunehmende Entfremdung des Menschen von der Natur.
Mehr15.09.2021 | iDiv, Medienmitteilung, TOP NEWS
Neubau des Forschungszentrums iDiv eingeweiht
Leipzig. Michael Kretschmer, Bodo Ramelow und Dr. Reiner Haseloff haben am Mittwoch gemeinsam mit der DFG-Generalsekretärin Heide Ahrens den Forschungsneubau des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) feierlich eröffnet. Über 100 Gäste nahmen an der Veranstaltung teil, die unter strengen Hygieneschutzmaßnahmen stattfand. Sie erfuhren, welchen Beitrag iDiv zur Lösung der globalen Biodiversitätskrise leistet und künftig leisten will. Bundeskanzlerin Dr. Angela Merkel schickte eine Grußbotschaft. Der Neubau an Leipzigs Alter Messe ist als Ort des Ideenaustauschs und der integrativen Forschung für Wissenschaftlerinnen und Wissenschaftler aus aller Welt konzipiert. Ab 2024 wollen die drei Länder gemeinsam mit weiteren Förderern die Finanzierung des Forschungszentrums übernehmen.
Mehr13.09.2021 | Biodiversität und Naturschutz, Medienmitteilung, TOP NEWS
Bahnbrechende Methode zur Bewertung des Effektes von Renaturierung
Basiert auf der Pressemitteilung von Rewilding Europe Wissenschaftler des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv), der Martin-Luther-Universität Halle-Wittenberg (MLU) und von Rewilding Europe haben eine neue Methode zur Bewertung von Fortschritten bei der Wiederherstellung von Naturlandschaften entwickelt. Seine bahnbrechende Anwendung in sieben Einsatzgebieten von Rewilding Europe zeigte sowohl positive Auswirkungen als auch Herausforderungen bei der Ausweitung des Projekts auf. Das praktische Instrument kann dazu beitragen, die Entscheidungsfindung zu unterstützen und die Renaturierung weiter voranzutreiben. Die Studie wurde kürzlich in der Fachzeitschrift Ecography veröffentlicht.
Mehr06.09.2021 | Biodiversität und Mensch, Medienmitteilung, TOP NEWS
Beweidung als kostengünstige Maßnahme gegen Feuer
Leipzig. Der Einsatz großer Pflanzenfresser kann ein wirksames Mittel zur Verhütung und Eindämmung von Waldbränden sein, insbesondere an Orten, an denen die Landnutzung aufgegeben wurde. Viel kostspieligere Lösungen wie die Brandbekämpfung oder die mechanische Entfernung der Vegetation könnten durch Beweidung ersetzt werden. Das ist das Ergebnis einer systematischen Literaturauswertung, die von Forschern des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) durchgeführt und im Journal of Applied Ecology veröffentlicht wurde. Die Studie gibt Anregungen für die Feuer- und Agrarpolitik in Europa und weltweit.
Mehr31.08.2021 | Evolution und Adaptation, iDiv-Mitglieder, Medienmitteilung, TOP NEWS
Den zukünftigen Lebensraumbedarf von Schimpansen zeigt die Vergangenheit
Basiert auf einer Medienmitteilung der Wildlife Conservation Society Leipzig. Eine neue Studie gibt Aufschluss darüber, an welche Orte sich Schimpansen zum Schutz vor der Klimainstabilität während der Eis- und Zwischeneiszeiten in Afrika in den letzten 120.000 Jahren zurückzogen. Unter Verwendung bioklimatischer Variablen identifizierte das internationale Forscherteam unter Leitung des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv), dem Max-Planck-Institut für evolutionäre Anthropologie (MPI-EVA) und der Universität Leipzig (UL) bisher unbekannte Lebensräume, in denen Schimpansen die Veränderungen seit der letzten Zwischeneiszeit überstanden haben. Die Ergebnisse, die im American Journal of Primatology veröffentlicht wurden, tragen dazu bei, das Verständnis dafür zu verbessern, wie sich der Klimawandel auf die Biodiversität auswirkt und wie der prognostizierte Verlust der Biodiversität in der Zukunft abgemildert werden kann.
Mehr05.08.2021 | iDiv-Mitglieder, Medienmitteilung, Molekulare Interaktionsökologie, TOP NEWS
Überlebensstrategie hungernder Bäume: die maßgebliche Rolle der Energievorräte
Basiert auf einer Medienmitteilung des Max-Planck-Instituts für Biogeochemie (BGC) Junge Fichten bilden auch während langer Hungerphasen Nährstoffreserven. Das haben Wissenschaftler vom Max-Planck-Institut für Biogeochemie (BGC), dem Deutschen Zentrum für integrative Biodiversitätsforschung (iDiv), der Friedrich- Schiller-Universität Jena (FSU) und anderen Einrichtungen herausgefunden. Dies gelingt ihnen selbst, wenn die Energiezufuhr durch Photosynthese wie bei Klimaextremen langfristig lahmgelegt ist, etwa indem sie ihr Wachstum stoppen und sogar Energie durch Selbstverdauung gewinnen. Bisher ging man davon aus, dass dies nur möglich sei, wenn genug Photosyntheseprodukte vorhanden und Wachstumsvorgänge abgedeckt sind. Die Studie wurde jetzt im Journal PNAS veröffentlicht. Mit dem Wissen können Modelle verbessert werden, die das Schicksal der Wälder vor dem Hintergrund des Klimawandels vorhersagen.
Mehr13.07.2021 | iDiv-Mitglieder, Medienmitteilung, TOP NEWS
Besondere Ehre für Biodiversitätsforscher Josef Settele
Basiert auf einer Medienmitteilung des Helmholtz-Zentrums für Umweltforschung (UFZ) Neue Arten im Tier- und Pflanzenreich werden oft nach Persönlichkeiten des öffentlichen Lebens benannt. Prof. Dr. Josef Settele ist nun diese besondere Ehre zu Teil geworden: Nach dem Biodiversitätsforscher und Schmetterlingsexperten, der am Helmholtz-Zentrum für Umweltforschung (UFZ) und am Deutschen Zentrum für integrative Biodiversitätsforschung (iDiv) forscht, wurde gleich eine neue Gattung benannt: Setteleia. Sie besteht aus vier Nachtfalterarten, die zu den Flechtenbären gehören und auf den Philippinen vorkommen.
Mehr09.07.2021 | Biodiversitätsökonomik, iDiv-Mitglieder, Medienmitteilung, TOP NEWS
Küstenökosysteme weltweit: Millardenschwere CO2-Speicher
Basiert auf einer Medienmitteilung des Kieler Instituts für Weltwirtschaft (IfW Kiel) Kiel/Leipzig. Küstenökosysteme wie Seegraswiesen, Salzmarschen und Mangrovenwälder sind in vieler Hinsicht für Menschen wertvoll. Insbesondere speichern sie Kohlenstoff – und das mit deutlich höherer Flächendichte als beispielsweise Wälder. Damit tragen sie einen wichtigen Teil dazu bei, den Klimawandel abzumildern. Allein die Küstenökosysteme Australiens, die besonders viel CO2 aus der Atmosphäre aufnehmen, ersparen dem Rest der Welt Klimafolgekosten in Höhe von rund 23 Mrd. US Dollar jährlich. Dies geht aus Berechnungen von Forscherinnen und Forschern am Kieler Institut für Weltwirtschaft (IfW Kiel), dem GEOMAR Helmholtz-Zentrum für Ozeanforschung Kiel, der Christian-Albrechts-Universität Kiel (CAU), der Universität Leipzig (UL) und dem Deutschen Zentrum für Integrative Biodiversitätsforschung (iDiv) hervor, die gerade der Fachzeitschrift Nature Climate Change veröffentlicht wurden.
Mehr07.07.2021 | iDiv-Mitglieder, Medienmitteilung, TOP NEWS
Besorgniserregender Zustand unserer Bäche und Flüsse
Basiert auf einer Medienmitteilung des Helmholtz-Zentrums für Umweltforschung (UFZ) Berlin/Leipzig. Der Bund für Umwelt und Naturschutz Deutschland (BUND), das Helmholtz-Zentrum für Umweltforschung (UFZ) und das Deutsche Zentrum für integrative Biodiversitätsforschung (iDiv) Halle-Jena-Leipzig starten ein umfassendes Monitoring von deutschen Fließgewässern. Ziel ist es, die Belastung kleiner Fließgewässer durch Pestizide zu erforschen und die Auswirkungen auf aquatische Insektengemeinschaften zu erfassen. So soll langfristig der Zustand deutscher Kleingewässer untersucht, und auf dieser Grundlage die Artenvielfalt gefördert werden. Bürgerwissenschaftlerinnen und -wissenschaftler helfen dabei mit.
Mehr07.07.2021 | iDiv, Medienmitteilung, TOP NEWS
Mit Wachstumsschub in die dritte Förderphase
Bonn. Das Deutsche Zentrum für integrative Biodiversitätsforschung (iDiv) Halle-Jena-Leipzig hat sich mit Erfolg um eine weitere Förderung durch die Deutsche Forschungsgemeinschaft (DFG) beworben. Der Hauptausschuss der DFG beschloss am Dienstag, iDiv in der dritten Förderphase ohne Kürzung mit jährlich rund 11,5 Mio. Euro zu unterstützen. Das Finanzvolumen steigt damit gegenüber der zweiten Förderphase um 26 Prozent. Auch nach Auslaufen der DFG-Förderung, voraussichtlich 2024, soll iDiv von den Trägereinrichtungen sowie mit Unterstützung der drei Sitzländer und weiterer Geldgeber wie dem Bund als multipolares universitäres Zentrum der Biodiversitätsforschung mit mitteldeutscher Verankerung und globaler Ausstrahlung fortgeführt werden.
Mehr07.07.2021 | iDiv, Medienmitteilung, TOP NEWS
Kunst der biologischen Vielfalt
Leipzig. Vor dem Deutschen Zentrum für integrative Biodiversitätsforschung (iDiv) in Leipzig ist ein neuer, öffentlicher Platz entstanden. Er liegt im Eingangsbereich der Alten Messe und wurde im Rahmen des Wettbewerbs Kunst am Bau geschaffen, den der Staatsbetrieb Sächsisches Immobilien- und Baumanagement (SIB) für diese Fläche ausgerufen hatte. Die Künstlergruppe nachbars garten und das Landschaftsarchitekturbüro Station C23 erhielten für ihr gemeinsam erarbeitetes Konzept chorus den Zuschlag. Der Platz empfängt seine Besucherinnen und Besucher mit verschlungenen Wegen, bunten Wiesen und rundlichen Figurengruppen. Er lädt zum Erkunden, Staunen und Verweilen ein und weckt Interesse für das Forschungszentrum.
Mehr
22.06.2021 | iDiv-Mitglieder, Medienmitteilung, MLU News, sDiv, TOP NEWS
Pflanzen: Einmalige Datenbank zur Vegetation der Erde ist frei verfügbar
Es ist ein Datenschatz: Die globale Vegetationsdatenbank „sPlotOpen“ ist ab sofort frei zugänglich. Darin versammelt sind Vegetationsaufnahmen von Pflanzen aus 114 Ländern, von allen Klimazonen der Erde. Erarbeitet wurde die Datenbank von einem internationalen Forschungsteam unter Leitung der Martin-Luther-Universität Halle-Wittenberg (MLU), des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) und des französischen Centre national de la recherche scientifique (CNRS). Erstmals steht so Forschenden weltweit ein ausbalancierter, repräsentativer Datensatz zur Vegetation der Erde zur Verfügung, wie das Team in der Fachzeitschrift Global Ecology & Biogeography berichtet.
Mehr18.06.2021 | Biodiversität und Mensch, Forschung, iDiv, Medienmitteilung, TOP NEWS
Libellen: Gewinner und Verlierer in Deutschland
Leipzig/Jena. In den letzten 35 Jahres hat sich bei der Verteilung der Libellenarten in Deutschland viel getan. So wurden Rückgänge vor allem bei Arten an stehenden Gewässern verzeichnet. Zuwächse gab es hingegen bei Libellen, die an Fließgewässern leben und wärmere Temperaturen bevorzugen. Zu diesen Ergebnissen kommt eine Studie unter Leitung des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv), der Friedrich-Schiller-Universität Jena (FSU) und des Helmholtz-Zentrums für Umweltforschung (UFZ). Die Studie, die im Fachmagazin Diversity and Distributions veröffentlich wurde, unterstreicht die Bedeutung von Bürgerwissenschaften und Naturkundegesellschaften für die Datenerhebung sowie von Naturschutzmaßnahmen zur Verbesserung der Biodiversität.
Mehr11.06.2021 | Arten-Interaktionsökologie, iDiv, Medienmitteilung, TOP NEWS
Im Botanischen Garten summt und brummt es wieder
Leipzig. Ab dem Wochenende beherbergt der Botanische Garten der Universität Leipzig bereits zum zweiten Mal eine Ausstellung, die die Welt der Pflanzen und ihrer Bestäuber genauer unter die Lupe nimmt. Anschaulich zeigen junge Wissenschaftler und Künstler aus Leipzig, dass es dabei um mehr geht als nur die Geschichte von der Biene und der Blüte.
Mehr10.06.2021 | iDiv, Medienmitteilung, sDiv, TOP NEWS
Wie sich das Klima auf die Pflanzenwurzeln auswirkt
Leipzig/Wyoming/Wageningen. Die Eigenschaften der Wurzeln einer Pflanze sind entscheidend dafür, unter welchen klimatischen Bedingungen diese Pflanze überleben kann. Eine neue Studie unter Leitung der Universität von Wyoming (UW), des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv), der Universität Leipzig (UL) und der Universität Wageningen (WUR), die in Nature Ecology and Evolution veröffentlich wurde, beleuchtet diese Beziehung und stellt die Natur ökologischer Trade-offs in Frage.
Mehr10.06.2021 | Experimentelle Interaktionsökologie, iDiv-Mitglieder, Medienmitteilung, TOP NEWS
Klimaschutz, Erhaltung der Biodiversität und soziale Gerechtigkeit – diese Aufgaben lassen sich nur im Dreiklang lösen
Basiert auf einer Medienmitteilung des Alfred-Wegener Institut für Polar- und Meeresforschung (AWI) und des Helmholtz-Zentrums für Umweltforschung (UFZ) Kiel/Leipzig. Der Kampf gegen die Erderwärmung und für eine nachhaltige Entwicklung kann nur gelingen, wenn die Menschheit die Themen Klimaschutz, Biodiversität und soziale Gerechtigkeit gemeinsam denkt. Diese müssten bei allen politischen Entscheidungen – global, national und regional – in ihren Wechselwirkungen gleichrangig berücksichtigt werden. Dieses sind nach Ansicht beteiligter deutscher Autoren die Kernbotschaften eines neuen wissenschaftlichen Berichtes zu „Artenvielfalt, Ökosystemen und Klimawandel“, den Experten des Weltbiodiversitätsrates IPBES und des Weltklimarates IPCC erstmals gemeinsam erarbeitet haben. Die Wissenschaftler vom AWI, UFZ, dem Deutschen Zentrum für integrative Biodiversitätsforschung (iDiv) und anderen Einrichtungen zeigen darin, warum vor allem der Verzicht auf fossile Brennstoffe für Klima- und Naturschutz wichtig ist, und wie gesunde Ökosysteme langfristig einen Beitrag zum Klimaschutz leisten können.
Mehr01.06.2021 | Forschung, iDiv, Medienmitteilung, TOP NEWS
Dimensionen des Invasionserfolgs von Pflanzen
Basiert auf einer Medienmitteilung der Universität Konstanz Invasive Pflanzen sind Pflanzenarten, die in einer Umgebung außerhalb ihres ursprünglichen Lebensraums wachsen. Sofern sie sich dort erfolgreich etablieren, können sie erhebliche negative Auswirkungen auf lokale Ökosysteme sowie Wirtschaft und Gesellschaft haben. Nicht alle Pflanzenarten sind jedoch gleich effektiv bei der Eroberung neuer Lebensräume. Ein internationales Team von Forschenden unter der Leitung des Konstanzer Biologen Professor Mark van Kleunen und unter Beteiligung von iDiv-Mitgliedern untersuchte nun auf kontinentaler Ebene verschiedene Arten von „Invasivität“ sowie mögliche Faktoren, die den Invasionserfolg nichtheimischer Pflanzen in Europa bestimmen.
Mehr31.05.2021 | Biodiversität und Naturschutz, iDiv-Mitglieder, Medienmitteilung, TOP NEWS
Nur wenige Schmetterlinge mögen das Stadtleben
Halle/Jena/Leipzig. Die sich stark ausbreitenden städtischen Lebensräume dürften auf lange Sicht einen Großteil von Schmetterlingsarten gefährden. Das vermelden Forschende vom Deutschen Zentrum für integrative Biodiversitätsforschung (iDiv), der Martin-Luther-Universität Halle-Wittenberg (MLU) und der Friedrich-Schiller-Universität Jena (FSU) in der Fachzeitschrift Global Change Biology. Nur Generalisten, die große Temperaturschwankungen tolerieren und sich von vielen verschiedenen Pflanzen ernähren, profitieren voraussichtlich von den menschlich geprägten Lebensräumen. Die Autoren empfehlen, zur Erhaltung der Artenvielfalt die Bedürfnisse von spezialisierten Schmetterlingsarten in der Städte- und Raumplanung zu berücksichtigen.
Mehr19.05.2021 | iDiv-Mitglieder, Medienmitteilung, TOP NEWS
Palmölplantagen verändern das Sozialverhalten von Makaken
Basiert auf einer Medienmitteilung der Universität Leipzig Regenwald wird in vielen Teilen Südostasiens durch Palmölplantagen ersetzt. Durch die massive Rodung ihres Lebensraums weichen Primaten zur Nahrungssuche teilweise auf die Plantagen aus. Dies führt häufig zu Konflikten mit Farmern, auch wenn die Affen diese kaum schädigen sondern, im Gegenteil, dabei helfen, Schädlinge wie Ratten, gering zu halten. Der regelmäßige Aufenthalt auf den Plantagen beeinflusst allerdings massiv das Sozialverhalten der Makaken. Dies zeigt eine neue Studie, die Wissenschaftler am Max-Planck-Institut für evolutionäre Anthropologie (MPI EVA), an der Universität Leipzig (UL), der Universiti Sains Malaysia (USM) und am Deutschen Zentrum für integrative Biodiversitätsforschung (iDiv) kürzlich in Scientific Reports veröffentlicht haben. Der Aufenthalt in der menschlich geprägten Umgebung könnte sich negativ auf die Entwicklung der Nachkommen auswirken und damit auf Dauer das Überleben der Makakenpopulationen gefährden. Die neuen Erkenntnisse können dabei helfen, geeignete Maßnahmen zum Schutz der laut IUCN gefährdeten Primatenart zu entwickeln und die friedliche Koexistenz zwischen Menschen und Wildtieren zu fördern.
Mehr18.05.2021 | Biodiversität und Mensch, iDiv-Mitglieder, Medienmitteilung, TOP NEWS
Der Schutz der biologischen Vielfalt durch die Gemeinsame Agrarpolitik ist machbar
Leipzig/Braunschweig/Rostock. Ein Team aus 300 europäischen Wissenschaftlern hat in Abstimmung mit der EU-Kommission Empfehlungen erarbeitet, wie die künftige Gemeinsame Agrarpolitik (GAP) der Europäischen Union mit den bereits beschlossenen Instrumenten einen substantiellen Beitrag zum Schutz der Artenvielfalt leisten kann. Der Bericht, verfasst von Forschenden des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv), des Helmholtz-Zentrums für Umweltforschung (UFZ), des Thünen-Instituts und der Universität Rostock, wird der EU-Kommission am 19. Mai in einem öffentlichen Online-Symposium vorgestellt.
Mehr11.05.2021 | Forschung, iDiv, Medienmitteilung, TOP NEWS
Mit Smartphones den ökologischen Wandel erfassen
Leipzig/Jena/Ilmenau. Smartphone-Apps zur Pflanzenbestimmung wie „Flora Incognita“ können nicht nur Pflanzenarten erkennen, sie erfassen auch großräumige ökologische Muster. Diese Muster stimmen mit Langzeit-Kartierungen der deutschen Flora erstaunlich gut überein, obwohl sie in kürzester Zeit gewonnen wurden und stark vom Verhalten der Nutzer der App beeinflusst werden. Damit eröffnen sich neue Perspektiven für die schnelle Erfassung von Veränderungen der Biodiversität. Das sind die wesentlichen Erkenntnisse einer Studie, die von einem Forscherteam aus Mitteldeutschland durchgeführt und in der Zeitschrift Ecography veröffentlicht wurde.
Mehr03.05.2021 | Arten-Interaktionsökologie, Biodiversitätssynthese, iDiv-Mitglieder, Physiologische Diversität, TOP NEWS, UFZ-News
Weniger Niederschläge, weniger Pflanzenvielfalt
Basiert auf einer Medienmitteilung des Helmholtz-Zentrums für Umweltforschung (UFZ) Leipzig/Halle. Wasser ist in vielen Ökosystemen der Erde ein knappes Gut. Dieser Mangel dürfte sich im Zuge des Klimawandels weiter verschärfen und zu einem deutlichen Rückgang der Pflanzenvielfalt führen. Mit einer Synthese von experimentellen Daten aus der ganzen Welt haben Wissenschaftler*innen des Helmholtz-Zentrums für Umweltforschung (UFZ), des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) und der Martin-Luther-Universität Halle-Wittenberg (MLU) zum ersten Mal nachgewiesen, dass gerade Trockengebiete besonders empfindlich auf veränderte Niederschlagsmengen reagieren. Das aber kann auch für die Menschen in den betroffenen Regionen Konsequenzen haben, warnt das Team im Fachjournal Nature Communications.
Mehr27.04.2021 | iDiv, Medienmitteilung, TOP NEWS
Baumplantagen tragen nur bedingt zum Schutz der Biodiversität bei
Leipzig/Jena/Halle. Künstlich angelegte Baumplantagen sollen helfen, den Verlust naturbelassener Wälder auszugleichen, tragen aber nur bedingt zum Schutz der Biodiversität bei. So beherbergen Plantagen weniger Käferarten als naturbelassene Altbestände und auch die Zahl der Tiere ist deutlich geringer. Das zeigt eine globale Analyse unter Leitung des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv), der Friedrich-Schiller-Universität Jena (FSU) und der Martin-Luther-Universität Halle-Wittenberg (MLU), die im Fachmagazin Forest Ecology and Management veröffentlicht wurde.
Mehr12.04.2021 | Experimentelle Interaktionsökologie, iDiv, Medienmitteilung, TOP NEWS
Nadia Soudzilovskaia erhält Friedrich Wilhelm Bessel-Forschungspreis
Basiert auf einer Medienmitteilung der Universiteit Leiden. Die Umweltwissenschaftlerin Nadia Soudzilovskaia wurde mit dem angesehenen Friedrich Wilhelm Bessel-Forschungspreis der Alexander von Humboldt-Stiftung ausgezeichnet. Die Auszeichnung würdigt die außerordentlichen Forschungsleistungen internationaler Wissenschaftler und Wissenschaftlerinnen, die mit deutschen Forschenden zusammenarbeiten. „Die Kombination verschiedener Fertigkeiten und Ansätze macht ihre Forschung hochrelevant und innovativ!“
Mehr08.04.2021 | Biodiversität und Naturschutz, Forschung, iDiv, Medienmitteilung, TOP NEWS
Nachhaltige Landwirtschaft und Holzproduktion können Aussterbe-Risiko bedrohter Arten um 40 % reduzieren
Basiert auf einer Medienmitteilung der Weltnaturschutzorganisation IUCN. Gland (Schweiz) – Eine weltweite Umstellung auf nachhaltige Landwirtschaft und Holzproduktion würde die wichtigsten Faktoren für das Aussterben landbasierter Tier- und Pflanzenarten um 40 % reduzieren. Das zeigt eine in Nature Ecology & Evolution veröffentlichte Studie unter Leitung der Post-2020 Taskforce der IUCN Species Survival Commission mit Sitz an der University Newcastle. An der Studie waren Forschende von 54 Institutionen aus 21 Ländern beteiligt, darunter auch das Deutsche Zentrum für integrative Biodiversitätsforschung (iDiv) und die Martin-Luther-Universität Halle-Wittenberg. Für die Untersuchungen kam eine neue Metrik zum Einsatz, die es Unternehmen, Regierungen sowie den Bürgern ermöglicht, ihren potentiellen Beitrag zum globalen Artenverlust zu bewerten.
Mehr07.04.2021 | Arten-Interaktionsökologie, iDiv-Mitglieder, Medienmitteilung, sDiv, TOP NEWS
Die Auswirkungen des Klimawandels auf Säugetiere sind kaum vorhersehbar
Basierend auf einer Pressemeldung der British Ecological Society Zürich/Leipzig. Unser Wissen darüber, wie Säugetierpopulationen auf den Klimawandel reagieren, ist äußerst lückenhaft – besonders in den Regionen, die als am empfindlichsten betrachtet werden. Dies ergab eine internationale Studie, die von sDiv, dem Synthesezentrum des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv), initiiert wurde. Beteiligt waren Forscher der Universität Zürich, der Martin-Luther-Universität Halle-Wittenberg (MLU), des Helmholtz-Zentrums für Umweltforschung (UFZ) und andere. Die Ergebnisse sind im Journal of Animal Ecology veröffentlicht.
Mehr31.03.2021 | Forschung, iDiv, Medienmitteilung, TOP NEWS, yDiv
Biodiversität kann sich positiv auf mentale Gesundheit auswirken
Leipzig/Frankfurt/Kiel. In Regionen mit einer höheren Vielfalt an Pflanzen- und Vogelarten geht es den Menschen, die dort leben, besser. So lassen sich die Ergebnisse einer Studie unter Leitung des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv), des Senckenberg Biodiversität und Klima Forschungszentrums (SBiK-F) und der Christian-Albrechts-Universität zu Kiel zusammenfassen, die im Fachmagazin Landscape and Urban Planning veröffentlicht wurde. Den Forschenden zufolge profitiert insbesondere die mentale Gesundheit von einem größeren Artenreichtum, ein direkter Einfluss auf die physische Gesundheit lässt sich hingegen nicht nachweisen.
Mehr23.03.2021 | Arten-Interaktionsökologie, iDiv-Mitglieder, Medienmitteilung, sDiv, TOP NEWS
Kurzlebige Pflanzenarten reagieren empfindlicher auf Klimawandel
Pflanzenarten mit kurzer Generationsdauer sind durch die Folgen des Klimawandels vermutlich stärker bedroht als langlebige Arten. Dies ist eines der Ergebnisse einer Studie von Forschern des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv), der Martin-Luther-Universität Halle-Wittenberg (MLU) und des Helmholtz-Zentrums für Umweltforschung (UFZ). Das internationale Team erfasste erstmals weltweit verfügbare Daten, vornehmlich aus Europa und Nordamerika, zur Frage, wie Pflanzenpopulationen auf Klimaänderungen reagieren. Die in Nature Communications veröffentlichte Studie zeigt, dass Pflanzenmerkmale wie die Generationsdauer Vorhersagen zu Klimaanfälligkeit ermöglichen. Diese Erkenntnis kann helfen zu bewerten, welche Pflanzenarten vorrangig geschützt werden sollten.
Mehr17.03.2021 | iDiv-Mitglieder, Medienmitteilung, TOP NEWS
Neue Methode zur Genom-Assemblierung bei Gerste bringt hervorragende Ergebnisse
Basierend auf einer Presemitteilung des IPK Leibniz-Institut Gatersleben. Die Genome der Individuen einer Art unterscheiden sich von einander, sodass wir viel über genetische Diversität unserer Kulturpflanzen lernen können, wenn wir ihre Genome vergleichen. Forscher, die viele Genome untersuchen, benötigen allerdings eine schnelle und zuverlässige Methode für die Sequenzassemblierung. Ein internationales Forschungsteam unter Führung des IPK Leibniz-Institutes und des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) hat nun eine neue Methode der DNA-Sequenzierung untersucht. Die Ergebnisse, die jetzt im Magazin The Plant Cell veröffentlicht wurden, sind dabei sehr vielversprechend. Die Wissenschaftler hoffen nun, die Methode künftig auch für die Assemblierung weiterer Gersten-Genome nutzen zu können.
Mehr05.03.2021 | iDiv-Mitglieder, Medienmitteilung, Nachhaltigkeit und Komplexität der Lebensräume von Menschenaffen, TOP NEWS
Schimpansen ohne Grenzen
Basiert auf einer Pressemitteilung des Max-Planck-Instituts für evolutionäre Anthropologie (MPI-EVA) Schimpansen werden in vier Unterarten unterteilt, die durch geografische Barrieren wie Flüsse getrennt sind. Frühere Studien, die versuchten, die Populationsgeschichte der Schimpansen zu verstehen, haben ein widersprüchliches Bild gezeichnet: Einige haben klare Trennungen zwischen den Unterarten der Schimpansen gezeigt, während andere einen genetischen Gradienten über die Spezies wie beim Menschen nahelegen. Um diese Dichotomie aufzulösen, hat ein internationales Forscherteam unter Leitung des Pan African Programme: The Cultured Chimpanzee (PanAf), des Max-Planck-Instituts für evolutionäre Anthropologie und des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) über 5000 Kotproben von 55 Standorten in 18 Ländern im gesamten Verbreitungsgebiet der Schimpansen über einen Zeitraum von acht Jahren gesammelt – die bisher vollständigste Probenahme dieser Tierart. Die Auswertung wurde in Communications Biology veröffentlicht.
Mehr05.03.2021 | Biodiversität und Naturschutz, iDiv-Mitglieder, Medienmitteilung, TOP NEWS
Arten sind unsere Lebensgrundlage
Bewertungen von Ökosystemen hinsichtlich ihrer Leistungen für den Menschen sollten stärker die Artenvielfalt berücksichtigen. Das fordern Wissenschaftler des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv), der Martin-Luther-Universität Halle-Wittenberg (MLU) in der Fachzeitschrift Ecosystem Services. Tier- und Pflanzenarten liefern viele Leistungen für das menschliche Wohlergehen, gehen jedoch seit Jahrzehnten kontinuierlich zurück. Großräumige Bewertungen erfassen nur einen Teil dieser Leistungen wie Wasserreinigung, Kohlenstoffspeicherung oder Erosionsschutz. Ökosystemleistungen, die direkt an Arten gekoppelt sind, spielen hingegen kaum einen Rolle. So würden Chancen eines effektiven Natur- und Artenschutzes verspielt, kritisieren die Forscher.
Mehr24.02.2021 | Experimentelle Interaktionsökologie, iDiv-Mitglieder, Medienmitteilung, TOP NEWS
Unterirdische Biodiversität im Wandel
Basierend auf einer Medienmitteilung des Max-Planck-Instituts für Mathematik in den Naturwissenschaften Durch den globalen Wandel wird die Vielfalt der Bakterien auf lokaler Ebene voraussichtlich zunehmen, während deren Zusammensetzung sich auf globaler Ebene immer ähnlicher wird. Dies ist das Ergebnis eines Forscherteams unter Leitung des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv), der Martin-Luther-Universität Halle-Wittenberg (MLU), der Universität Leipzig (UL) und des Max-Planck-Instituts für Mathematik in den Naturwissenschaften (MiS). Die Forscher haben erstmals ganzheitlich bewertet, wie sich Klima- und Landnutzungsänderungen auf Bakteriengemeinschaften im Boden auswirken. Die in Global Ecology and Biogeography veröffentlichte Studie kann dabei helfen, zuverlässige Vorhersagen über Veränderungen in der globalen Verteilung dieser unterirdischen Gemeinschaften zu treffen.
Mehr22.02.2021 | Arten-Interaktionsökologie, iDiv, Medienmitteilung, TOP NEWS
Auswirkungen des Klimas auf Pflanzen mitunter erst nach Jahren sichtbar
Leipzig. Die Auswirkungen von Klimaelementen wie Temperatur und Niederschlag auf die Pflanzenwelt werden möglicherweise erst Jahre später sichtbar. Dies ist ein zentrales Ergebnis einer Studie unter Leitung des Deutschen Zentrums für Biodiversitätsforschung (iDiv), der Martin-Luther-Universität Halle-Wittenberg (MLU) und des Helmholtz-Zentrums für Umweltforschung (UFZ), die im Fachmagazin Global Change Biology veröffentlicht wurde. Demnach könnten klimatische Elemente langfristig einen stärkeren Einfluss auf das Überleben, das Wachstum und die Vermehrung von Pflanzen haben als frühere Studien nahelegen.
Mehr26.01.2021 | iDiv-Mitglieder, Medienmitteilung, TOP NEWS
Herbst und Frühjahr sind eng verbunden
Basiert auf einer Medienmitteilung der Friedrich-Schiller-Universität Jena Dass Pflanzen infolge des Klimawandels immer früher beginnen zu blühen, darüber haben unter anderem Jenaer Wissenschaftlerinnen und Wissenschaftler bereits vor einiger Zeit berichtet. Doch wie wirken sich die klimatischen Veränderungen eigentlich auf das andere Ende der Vegetationsperiode aus? Um Antworten darauf zu finden, haben sich die Biologinnen Dr. Solveig Franziska Bucher der Friedrich-Schiller-Universität Jena und Prof. Dr. Christine Römermann der Friedrich-Schiller-Universität Jena und des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) intensiv mit der sogenannten Blattseneszenz, also dem Alterungsprozess von Pflanzen, der sich etwa durch die herbstliche Färbung oder das Abwerfen der Blätter zeigt, auseinandergesetzt. Dabei haben sie herausgefunden, dass die Blattseneszenz bei niedrigeren Temperaturen früher einsetzt als bei höheren Temperaturen. Der Beginn dieses Prozesses kann zwar zwischen einzelnen Arten differieren, je kälter jedoch das Umfeld ist, umso schneller läuft dieser ab. Die Studie erschien im Forschungsmagazin Journal of Ecology.
Mehr26.01.2021 | Biodiversität und Naturschutz, iDiv-Mitglieder, Medienmitteilung, TOP NEWS
Nicht die gleichen Fehler machen
Leipzig/Halle. Die globalen Ziele zum Schutz der biologischen Vielfalt müssten künftig als Mindestanforderungen in nationales Recht aller Mitgliedstaaten der UN-Biodiversitätskonvention (CBD) übernommen werden. Das ist einer von vier Vorschlägen zur Verbesserung der globalen Strategie zum Biodiversitätsschutz eines Forscherteams unter gemeinsamer Leitung des des Nanjing Instituts für Umweltforschung in China, des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv), der Martin-Luther-Universität Halle-Wittenberg (MLU) und NatureServe. Diese Strategie wird derzeit neu ausgehandelt. Außerdem müssten die Finanzierung, die Wissensgrundlage und die Methoden zur Erfolgsmessung des Naturschutzes aufgebessert werden. Die bisherigen Ziele sind weitgehend verfehlt worden. In der Fachzeitschrift Nature Ecology & Evolution nennen die Forscher Gründe für das Scheitern und zeigen konkrete Politikoptionen auf.
Mehr25.01.2021 | Biodiversität und Mensch, iDiv-Mitglieder, Medienmitteilung, TOP NEWS
Straßenbäume als Mittel gegen Depressionen
Leipzig. Straßenbäume im direkten Lebensumfeld könnten das Risiko für Depressionen und den Bedarf an Antidepressiva in der Stadtbevölkerung reduzieren. Das ist das Ergebnis einer Studie von Forschern des Helmholtz-Zentrums für Umweltforschung (UFZ), des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv), der Universität Leipzig (UL) und der Friedrich-Schiller-Universität Jena (FSU). Straßenbäume in städtischen Wohngebieten zu pflanzen könnte demnach eine effektive und preiswerte naturbasierte Lösung sein, um psychische Krankheiten, den lokalen Klimawandel und den Verlust biologischer Vielfalt zu bekämpfen. Laut den Wissenschaftlern sollten Stadtplaner, Gesundheitsexperten und Naturschützern diese Maßnahme öfter in Betracht ziehen. Die Studie ist in der Zeitschrift Scientific Reports erschienen.
Mehr14.01.2021 | Experimentelle Interaktionsökologie, iDiv-Mitglieder, Medienmitteilung, TOP NEWS
Die Vermessung der unterirdischen Welt
Leipzig/Halle/Fort Collins. Ein Viertel aller bekannten Arten lebt im Boden. Das Leben über der Erde hängt vom Boden und seinen unzähligen Bewohnern ab. Doch globale Strategien zum Schutz der Biodiversität schenken diesem Lebensraum bisher wenig Beachtung. Ein internationales Team von Forschern unter der Leitung des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv), der Martin-Luther-Universität Halle-Wittenberg (MLU), der Universität Leipzig (UL) und der Colorado State University ruft in der Fachzeitschrift Science dazu auf, die Böden in den Neuverhandlungen internationaler Biodiversitätsstrategien stärker zu berücksichtigen. Ihre Bedeutung müsse weit über die Landwirtschaft hinaus honoriert werden. Um Zustand und Leistungen der Böden besser sichtbar zu machen, erläutern die Forscher ihren Plan zur systematischen Erfassung auf Basis weltweit einheitlicher Standards.
Mehr14.12.2020 | iDiv-Mitglieder, Medienmitteilung, sDiv, TOP NEWS
Pflanzenvielfalt in Deutschland auf dem Rückzug
Bonn/Halle/Jena/Leipzig: Deutschlands Pflanzenvielfalt ist auf dem Rückzug: Bei über 70 Prozent von mehr als 2000 untersuchten Arten sind in den letzten 60 Jahren deutschlandweit Rückgänge zu beobachten – im Durchschnitt um 15 Prozent pro Art. Das ist das Ergebnis der bislang umfassendsten Auswertungen von Pflanzendaten aus Deutschland, die nun die Fachzeitschrift Global Change Biology veröffentlicht hat. 29 Millionen Daten zur Verbreitung von Gefäßpflanzen flossen in die Analysen ein, die im Rahmen des Vorhabens „sMon – Biodiversitätstrends in Deutschland“ des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) erfolgten. Beteiligt waren Forschende von iDiv, der Universitäten Jena, Halle und Rostock, des Helmholtz-Zentrums für Umweltforschung (UFZ) sowie des Bundesamtes für Naturschutz (BfN) unter enger Beteiligung der oberen Naturschutzbehörden aller 16 Bundesländer.
Mehr10.12.2020 | Experimentelle Interaktionsökologie, Medienmitteilung, TOP NEWS
Leibniz-Preis 2021 für Leipziger Biodiversitätsforscher Nico Eisenhauer
Der Hauptausschuss der Deutschen Forschungsgemeinschaft (DFG) hat heute vier Wissenschaftlerinnen und sechs Wissenschaftlern den Gottfried Wilhelm Leibniz-Preis 2021 zuerkannt. Einer von ihnen ist Prof. Nico Eisenhauer, seit 2014 Forschungsgruppenleiter am Deutschen Zentrum für integrative Biodiversitätsforschung (iDiv) und an der Universität Leipzig. Die Auszeichnungen sind mit jeweils 2,5 Millionen Euro dotiert.
Mehr03.12.2020 | Biodiversität und Mensch, iDiv-Mitglieder, Medienmitteilung, TOP NEWS, yDiv
Macht biologische Vielfalt glücklich?
Basiert auf einer Medienmitteilung von Senckenberg Frankfurt, Leipzig, Kiel: Eine hohe biologische Vielfalt in der näheren Umgebung ist für die Lebenszufriedenheit genauso wichtig wie das Einkommen. Das berichten Wissenschaftler*innen von Senckenberg, des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) und der Universität Kiel aktuell in Ecological Economics. Sie haben erstmals europaweit gezeigt, dass die individuelle Lebenszufriedenheit mit der Vielfalt der Vogelarten im Umfeld korreliert. Zehn Prozent mehr Vogelarten im Umfeld steigern die Lebenszufriedenheit der Europäer*innen demnach mindestens genauso stark wie ein vergleichbarer Einkommenszuwachs. Naturschutz sei daher eine Investition in menschliches Wohlbefinden, so die Forscher.
Mehr26.11.2020 | iDiv-Mitglieder, Medienmitteilung, TOP NEWS
Leipziger Forscher erstellen größtes Inventar aller bekannten Pflanzenarten der Erde
Leipzig. Forscher der Universität Leipzig (UL) und des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) haben die weltweit umfassendste Liste aller bekannten Pflanzenarten aufgestellt. Sie enthält 1.315.562 Namen von Gefäßpflanzen und erweitert so die Anzahl anerkannter Pflanzenarten und Unterarten um 70.000, was ca. 20 % entspricht. Darüber hinaus konnten die Forscher 181.000 ungeklärte Artnamen aufklären. Der Datensatz wurde nun im Fachblatt Scientific Data veröffentlicht. Er ist das Ergebnis einer über zehn Jahre langen intensiven Recherchearbeit und könnte dazu beitragen, Leipzig zu einem der weltweit wichtigsten Zentren der Pflanzenforschung zu machen.
Mehr26.11.2020 | Biodiversität und Naturschutz, Medienmitteilung, TOP NEWS
EuropaBON: MLU und iDiv leiten neues europaweites Projekt für gemeinsames Monitoring
Basiert auf einer Medienmitteilung der Martin-Luther-Universität Halle-Wittenberg (MLU) Ein neues Forschungsprojekt soll ein länderübergreifendes System für die Überwachung der Artenvielfalt und Ökosysteme in Europa entwickeln. Koordiniert wird es von der Martin-Luther-Universität Halle-Wittenberg (MLU) gemeinsam mit dem Deutschen Zentrum für integrative Biodiversitätsforschung (iDiv) Halle-Jena-Leipzig. Die Ergebnisse des Projekts sollen die Grundlage für politische Entscheidungen der Europäischen Kommission und anderer Entscheidungsträger bilden. Die EU fördert das Projekt mit drei Millionen Euro. Vom 1. bis 3. Dezember findet ein virtuelles Kickoff-Meeting der Projektpartner statt.
Mehr23.11.2020 | iDiv-Mitglieder, Medienmitteilung, TOP NEWS
Plan zur Rettung des Leipziger Auwalds
Leipzig. Seit Jahrzehnten ist bekannt, dass das Auensystem entlang der Weißen Elster, Pleiße und Luppe von seinem wichtigsten Element abgeschnitten ist: dem Wasser. Der Wald trocknet buchstäblich aus, verliert seine charakteristischen Baumarten und deren Bewohner. Der Grund sind historische Umbauten zum Hochwasserschutz und die Klimaerwärmung. Eine Revitalisierung der Flusslandschaft ist deshalb unumgänglich, sagen Wissenschaftler des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv), des Helmholtz-Zentrums für Umweltforschung (UFZ) und der Universität Leipzig (UL). In enger Zusammenarbeit mit den zuständigen Naturschutzbehörden und -verbänden haben sie jetzt eine Vision für das Leipziger Auensystem entwickelt und eine Karte mit Bewertungen von über 70 konkreten Maßnahmen erstellt. Sachsens Umweltminister Günther würdigte das Papier als fundierte Grundlage und kündigte weitere Schritte an.
Mehr29.10.2020 | Evolutionsökologie, Medienmitteilung, TOP NEWS
Der verlockende Duft süßer Früchte
Das Deutsche Zentrum für integrative Biodiversitätsforschung (iDiv) erweitert sein Portfolio um einen neuen Forschungsbereich. Ab November 2020 leitet der Biologe Dr. Omer Nevo die neue Nachwuchsgruppe „Evolutionsökologie“ am iDiv und an der Friedrich-Schiller-Universität Jena (FSU). Der 35-jährige Wissenschaftler untersucht die chemische Kommunikation zwischen Pflanzen und Tieren – genauer gesagt, wie Pflanzen durch den Duft ihrer Früchte Tiere anlocken, die Frucht und Samen weitertragen und ausbreiten. Das Wissen über Signalwirkungen von Gerüchen soll auch zu neuen Ansätzen im Naturschutz verhelfen. Nevo und sein Team werden für sechs Jahre mit rund 1,3 Millionen Euro durch das Emmy-Noether-Programm der Deutschen Forschungsgemeinschaft (DFG) gefördert.
Mehr28.10.2020 | iDiv-Mitglieder, Medienmitteilung, sDiv, TOP NEWS
Studie: Klimawandel verursacht Artensterben im Schwarzwald
Basiert auf einer Medienmitteilung der Martin-Luther-Universität Halle-Wittenberg (MLU) Schon heute hinterlässt der Klimawandel in den Mooren im Schwarzwald seine Spuren. Durch steigende Temperaturen und längere Trockenperioden sind dort in den vergangenen 40 Jahren bereits zwei typische Pflanzenarten ausgestorben. Gleichzeitig ging der Bestand vieler weiterer Arten um ein Drittel zurück. Zehn weitere typische Moorarten könnten in den nächsten Jahren aussterben, schreiben Forscher der Martin-Luther-Universität Halle-Wittenberg (MLU) und des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) Halle-Jena-Leipzig im Fachmagazin Diversity and Distributions.
Mehr27.10.2020 | Biodiversität und Mensch, Medienmitteilung, Nachhaltigkeit und Komplexität der Lebensräume von Menschenaffen, sDiv, TOP NEWS
Monitoringprogramme zur Biodiversität brauchen eine Kultur des Miteinanders
Der Verlust der Artenvielfalt schreitet weltweit unaufhaltsam voran. Um wirkungsvoller dagegen zu steuern, braucht es Monitoringprogramme, die den Zustand der Tier- und Pflanzenarten sowie deren Gefährdungszustand präzise abbilden. Doch daran mangelt es noch zu oft – zu lückenhaft, zu wenig aufeinander abgestimmt und zu begrenzt ist das zu untersuchende Artenspektrum. Ein vom Deutschen Zentrum für integrative Biodiversitätsforschung (iDiv) geführtes Team von Forschern beschreibt in einem Beitrag für das Fachjournal OneEarth, wie verschiedene Interessengruppen mit viel Expertise zusammenarbeiten können, um Monitoring zu stärken und damit einem weiteren Artenrückgang entgegenzuwirken.
Mehr26.10.2020 | Biodiversität und Mensch, Medienmitteilung, TOP NEWS
Intensive Landnutzung stört Wechselwirkungen in Ökosystemen
Basiert auf einer Medienmitteilung der Universität Bern Eine hohe Intensität in der Land- und Forstwirtschaft untergräbt die biologische Vielfalt und den Nutzen, den Menschen aus Ökosystemen ziehen können. Eine internationale Studie unter Leitung des Helmholtz-Zentrums für Umweltforschung (UFZ), des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) und der Universität Bern zeigt erstmals, wie die Intensität der Landnutzung die Wechselwirkungen zwischen drei Ökosystem-Eigenschaften beeinflusst: Biodiversität, Funktionen von Ökosystemen sowie deren Leistungen für die Menschen. Die Studie wurde in PNAS veröffentlicht.
Mehr26.10.2020 | Experimentelle Interaktionsökologie, Forschung, iDiv, iDiv-Mitglieder, Medienmitteilung, TOP NEWS
Veränderte Blühphasen von Pflanzen durch geringere Insektendichte
Basiert auf einer Medienmitteilung der Friedrich-Schiller-Universität Jena Leipzig/Jena. Die Blumen auf der Wiese blühen in voller Pracht – aber weit und breit ist keine einzige Biene zu sehen. Was heute noch unwahrscheinlich klingt, könnte in Zukunft durchaus häufig vorkommen. Denn, so hat eine Forschungsgruppe der Universität Jena und des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) herausgefunden, Insekten haben einen entscheidenden Einfluss auf die Biodiversität und Blühphasen von Pflanzen. Fehlen Insekten im Umfeld der Pflanzen, verändert sich deren Blühverhalten. Dies kann dazu führen, dass die Lebenszyklen der Insekten und die Blütezeit der Pflanzen nicht mehr übereinstimmen. Gehen die Insekten aber zur falschen Zeit auf Nektarsuche, werden manche Pflanzen nicht mehr bestäubt.
Mehr23.10.2020 | Biodiversität und Naturschutz, Medienmitteilung, TOP NEWS
Wir brauchen ein Sicherheitsnetz für die Biodiversität
Basiert auf einer Medienmitteilung der Nationalen Universität Córdoba und des Leibniz-Instituts für Gewässerökologie und Binnenfischerei (IGB) Córdoba, Leipzig, Halle. Um dem alarmierenden Rückgang der biologischen Vielfalt entgegenzuwirken, braucht es ein „Sicherheitsnetz“ aus miteinander verbundenen ehrgeizigen Zielen. Denn kein einzelnes Ziel kann dem breiten Spektrum der Anforderungen gerecht werden, so das Fazit eines großen internationalen Teams mit dem Deutschen Zentrum für integrative Biodiversitätsforschung (iDiv), der Martin-Luther-Universität Halle-Wittenberg (MLU) und dem Leibniz-Institut für Gewässerökologie und Binnenfischerei (IGB). Die in der Fachzeitschrift Science erschienene Studie skizziert die wissenschaftliche Grundlage für die Neugestaltung der Ziele der UN-Konvention über die Biologische Vielfalt (CBD).
Mehr19.10.2020 | iDiv-Mitglieder, Medienmitteilung, TOP NEWS
Akademien fordern schnelles Handeln zum Schutz der Artenvielfalt in der Agrarlandschaft
Basierend auf einer Pressemitteilung der Nationalen Akademie der Wissenschaften Leopoldina, acatech – Deutsche Akademie der Technikwissenschaften und der Union der deutschen Akademien der Wissenschaften Halle/Saale. Die biologische Vielfalt in der Agrarlandschaft ist in Deutschland in den letzten Jahren, selbst in Naturschutzgebieten, stark zurückgegangen. In ihrer gemeinsamen Stellungnahme „Biodiversität und Management von Agrarlandschaften” geben die Nationale Akademie der Wissenschaften Leopoldina, acatech – Deutsche Akademie der Technikwissenschaften und die Union der deutschen Akademien der Wissenschaften Empfehlungen in acht Handlungsfeldern. Zu den Autorinnen und Autoren gehören u. a. die iDiv-Mitglieder Prof. Katrin Böhning-Gaese (Sprecherin; Senckenberg Biodiversität und Klima Forschungszentrum), Prof. Helge Bruelheide (Martin-Luther-Universität Halle-Wittenberg) und Prof. Ralf Seppelt (Helmholtz-Zentrum für Umweltforschung – UFZ).
Mehr07.10.2020 | Experimentelle Interaktionsökologie, iDiv-Mitglieder, Medienmitteilung, TOP NEWS
Langfristige Folgen des globalen Wandels für Ökosysteme schwer vorhersehbar
Basiert auf einer Medienmitteilung der Universität Leipzig Ein internationales Forscherteam unter Leitung der Universität Leipzig (UL) und des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) hat in einem Langzeitexperiment die Auswirkungen von Veränderungen in der Artenvielfalt von Pflanzen für die Funktionen von Ökosystemen untersucht. Die Wissenschaftler stellten fest, dass die Pflanzenmerkmale, die die Funktionen eines Ökosystems bestimmen, sich von Jahr zu Jahr ändern. Die langfristigen Folgen des Wandels der biologischen Vielfalt vorherzusagen sei daher äußerst schwierig, schreiben sie in einem Beitrag für das Fachjournal Nature Ecology & Evolution.
Mehr06.10.2020 | Medienmitteilung, TOP NEWS
Turbo für die Bestimmung von Blütenpollen
Basiert auf einer Medienmitteilung des Helmholtz-Zentrums für Umweltforschung (UFZ) Zur Pollenflugvorhersage, Honiganalyse oder um klimabedingter Veränderungen von Pflanzen-Bestäuber-Interaktionen – die Analyse von Blütenpollen spielt in vielen Forschungsbereichen eine wichtige Rolle. Goldstandard ist dabei nach wie vor die Mikroskopie, die jedoch viel Zeit und Expertise erfordert. Wissenschaftlerinnen und Wissenschaftler des Helmholtz-Zentrums für Umweltforschung (UFZ) und des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) haben in Kooperation mit der Technischen Universität (TU) Ilmenau nun ein Verfahren entwickelt, mit dem sie die Pollenanalyse automatisieren können. Ihre Studie ist im Fachmagazin New Phytologist veröffentlicht.
Mehr29.09.2020 | Biodiversitätssynthese, Forschung, iDiv, Medienmitteilung, TOP NEWS
Erhebungen an ‚coolen‘ Standorten möglicherweise irreführend
Leipzig/Halle. Die Daten, die von Citizen-Science-Initiativen, Museen und Nationalparks gesammelt werden, sind eine wichtige Basis für die Erforschung des Biodiversitätswandels. Doch die gewählten Standorte sind oftmals nicht repräsentativ und können zu falschen Schlüssen über den Wandel der Biodiversität führen. Zu diesem Ergebnis kommen Forscher des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) und der Martin-Luther-Universität Halle Wittenberg (MLU). In ihrer Studie, die im Fachmagazin Conservation Biology veröffentlicht wurde, fordern sie eine objektivere Auswahl von Standorten und bessere Schulungsangebote für Bürgerwissenschaftler.
Mehr28.09.2020 | Arten-Interaktionsökologie, Evolution und Adaptation, iDiv, Medienmitteilung, sDiv, TOP NEWS
Wie künstliche Intelligenz zum Schutz von Orchideen und anderen Arten beiträgt
Leipzig/Halle. Orchideen erfreuen sich als Zimmerpflanzen großer Beliebtheit, in freier Natur sind viele Arten allerdings stark bedroht durch Landnutzung und illegale Ernte. Doch nur ein Bruchteil von ihnen steht auf der internationalen Roten Liste bedrohter Arten, denn die nötigen Fachgutachten sind enorm aufwendig. Ein neues und deutlich schnelleres automatisiertes Verfahren, entwickelt unter der Leitung von Biodiversitätsforschern aus Mitteldeutschland, zeigt, dass 30 % aller Orchideenarten potentiell gefährdet sind. Im Fachmagazin Conservation Biology beschreiben die Forscher, wie ihr neuer Ansatz die naturschutzfachliche Prüfung für alle Arten weltweit beschleunigen könnte.
Mehr15.09.2020 | Forschung, Medienmitteilung, TOP NEWS
Wie retten wir Europas letzte Urwälder?
Halle/Berlin. Nur um 1 % müssten die Waldschutzgebiete Europas ausgeweitet werden, um die meisten verbliebenen europäischen Urwälder zu schützen. Dies hat ein internationales Forscherteam unter Leitung des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv), der Martin-Luther-Universität Halle-Wittenberg (MLU) und der Humboldt-Universität zu Berlin (HU) errechnet. Die in Diversity and Distribution veröffentlichte Studie erfasst erstmals europaweit die Verbreitung und den Schutzstatus der letzten weitestgehend unberührten Wälder. Sie zeigt, wo dringender Handlungsbedarf zur Erhaltung besteht und liefert wertvolle Informationen zur Umsetzung der neuen EU-Biodiversitätsstrategie.
Mehr14.09.2020 | Medienmitteilung, Nachhaltigkeit und Komplexität der Lebensräume von Menschenaffen, TOP NEWS
Schimpansenverhalten und -kultur sind in variabler Umwelt am vielfältigsten
Basiert auf einer Medienmitteilung des Max-Planck-Instituts für evolutionäre Anthropologie (MPI EVA) Die kulturelle und Verhaltensvielfalt bei Schimpansen ist für das gesamte äquatoriale Afrika gut dokumentiert, doch bisher war größtenteils ungeklärt, welche ökologisch-evolutionären Mechanismen dieser Vielfalt zugrunde liegen. Ein internationales Forschungsteam unter der Leitung des Max-Planck-Instituts für evolutionäre Anthropologie und dem Deutschen Zentrum für integrative Biodiversitätsforschung (iDiv) hat den Einfluss der Umweltvariabilität auf das Verhaltensrepertoire von 144 sozialen Gruppen untersucht. Die in Nature Communications veröffentlichte Studie zeigt, dass die Verhaltensvielfalt bei jenen Schimpansen größer ist, die weiter entfernt von historischen Waldrefugien leben, die unter saisonalen Bedingungen leben, und die eher in Savannenwäldern als in dicht bewaldeten Lebensräumen beheimatet sind.
Mehr09.09.2020 | Makroökologie und Gesellschaft, Medienmitteilung, TOP NEWS
Der Abwärtstrend der biologischen Vielfalt ist umkehrbar
Basiert auf einer Pressemitteilung des Internationalen Instituts für angewandte Systemanalyse (IIASA) Laxenburg/Leipzig. Die Politik muss in den kommenden Jahren und Jahrzehnten alles daran setzen, die noch bestehenden natürlichen Lebensräume zu schützen, viele bereits verloren gegangene wiederherzustellen und vor allem die Ernährungsgewohnheiten und Nahrungsproduktion auf nachhaltig umzustellen. Nur so sei der Verlust der biologischen Vielfalt bis 2050 oder früher zu stoppen. Dieses Rezept haben Wissenschaftler unter Leitung des Internationalen Instituts für angewandte Systemanalyse (IIASA) unter Beteiligung von Forschern des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) in einer aktuellen Studie errechnet. Anhand neuer Modelle und Szenarien untersuchte das Team, ob und auf welchem Wege es möglich wäre, Naturschutzziele zu erreichen, ohne andere UN-Nachhaltigkeitsziele wie etwa die Welternährung zu behindern. Die in Nature veröffentlichte Studie ist Teil des jüngsten WWF-Berichts „Living Planet Report“.
Mehr03.09.2020 | iDiv, iDiv-Mitglieder, Medienmitteilung, TOP NEWS
ERC Starting Grant für iDiv Nachwuchswissenschaftler Dr. Martin Mascher
Basiert auf einer Medienmitteilung des Leibniz-Instituts für Pflanzengenetik und Kulturpflanzenforschung (IPK) Gatersleben: Großer Erfolg für den iDiv-Juniorforschungsgruppenleiter Dr. Martin Mascher. Der 34-jährige Wissenschaftler, der am Leibniz-Institut für Pflanzengenetik und Kulturpflanzenforschung (IPK) arbeitet, erhält einen Starting Grant vom European Research Council (ERC). Damit wird sein aktuelles Forschungsprojekt TRANSFER in den kommenden fünf Jahren mit 1,5 Millionen Euro gefördert.
Mehr01.09.2020 | Biodiversität und Mensch, Medienmitteilung, TOP NEWS, UFZ-News
Bildung alleine reicht nicht
Basiert auf einer Medienmitteilung des Helmholtz-Zentrums für Umweltforschung (UFZ) Es ist ein bekanntes Problem: Zu selten führt das, was Politikerinnen und Politiker an Initiativen, Empfehlungen oder Strategien auf dem Gebiet des Naturschutzes verkünden, dazu, dass die Menschen ihr Alltagsverhalten wirklich ändern. Ein deutsch-israelisches Forscherteam unter Führung des Helmholtz-Zentrums für Umweltforschung (UFZ) und des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) hat sich mit den Gründen befasst. Demnach nutzen die von der Politik vorgeschlagenen Maßnahmen die Bandbreite der möglichen Verhaltenseingriffe nicht genügend aus und benennen zu selten die eigentlichen Zielgruppen, schreiben sie im Fachmagazin Conservation Biology.
Mehr28.08.2020 | iDiv, Medienmitteilung, TOP NEWS
Leipziger Aue chronisch krank
Leipzig. Der Leipziger Auwald gehört zu den größten erhaltenen Auwaldbeständen in Mitteleuropa. Doch die Aue ist gefährdet – nicht nur Trockenheit und Klimawandel, sondern auch das menschliche Eingriffe machen ihr zu schaffen. Diese Belastungen sowie Möglichkeiten zur Revitalisierung dieses Waldgebiets waren die Themen eines gemeinsamen Besuches am Leipziger Auwaldkran, an dem Prof. Beate Jessel, Präsidentin des Bundesamtes für Naturschutz (BfN), Wolfram Günther vom Sächsischen Umweltministerium, Rüdiger Dittmar vom Amt für Stadtgrün und Gewässer der Stadt Leipzig und Prof. Dr. Christian Wirth vom Deutschen Zentrum für integrative Biodiversitätsforschung (iDiv) und der Universität Leipzig (UL) teilnahmen.
Mehr26.08.2020 | Biodiversität und Naturschutz, Medienmitteilung, Nachhaltigkeit und Komplexität der Lebensräume von Menschenaffen, TOP NEWS
Wirksamkeit von Schutzmaßnahmen für Primaten meist völlig ungesichert
Leipzig/Halle/Cambridge. Weniger als ein Prozent der wissenschaftlichen Literatur über Primaten bewerten die Wirksamkeit von Maßnahmen zu ihrem Schutz. Dies hat ein internationales Team unter Leitung von Forschern des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv), der Martin-Luther-Universität Halle-Wittenberg (MLU), des Max-Planck-Instituts für evolutionäre Anthropologie (MPI-EVA) und der Universität Cambridge ermittelt. Trotz großer Schutzbemühungen sei dies einer der Hauptgründe für den anhaltenden dramatischen Rückgang von Primaten. Die in der Zeitschrift BioScience veröffentlichte Studie stellt mehrere Maßnahmen vor, um den Primatenschutz auf eine bessere wissenschaftliche Basis zu stellen.
Mehr24.08.2020 | Experimentelle Interaktionsökologie, Forschung, iDiv, iDiv-Mitglieder, Medienmitteilung, TOP NEWS
Biodiversitätsversuchsflächen auf dem Prüfstand
Basiert auf einer Medienmitteilung des Senckenberg Biodiversität und Klima Forschungszentrums. Leipzig/Frankfurt/Bern. Ein Großteil der Erkenntnisse darüber, wie Ökosysteme von biologischer Vielfalt profitieren, stammt aus künstlich angelegten Versuchsflächen. Kritiker bemängeln jedoch seit langem, dass dort Artengemeinschaften wachsen, die in der Natur nicht vorkommen. Doch der positive Effekt der Biodiversität ist nicht nur dem Design der Versuchsflächen geschuldet. Das konnte ein internationales Forscherteam unter Leitung des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv), der Universität Leipzig (UL), der Universität Bern und des Senckenberg Biodiversität und Klima Forschungszentrums nun nachweisen, indem sie unrealistische Versuchsflächen in ihrer Analyse aussparten. Ihre Ergebnisse, die in Nature Ecology & Evolution veröffentlicht wurden, belegen, dass die aus den Versuchsflächen erlangten Erkenntnisse zur biologischen Vielfalt valide sind.
Mehr17.08.2020 | Forschung, iDiv, iDiv-Mitglieder, Medienmitteilung, MLU News, TOP NEWS
Stadthummeln sind größer als ihre Artgenossinnen auf dem Land und bestäuben auch mehr
Basiert auf einer Medienmitteilung der Martin-Luther-Universität Halle-Wittenberg. Leipzig/Halle. Treiben Städte die Evolution von Hummeln voran? Einen ersten Hinweis dafür liefern Befunde einer neuen Studie der Martin-Luther-Universität Halle-Wittenberg (MLU) und des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv). Demnach sind die Insekten in Städten größer und dadurch sogar produktiver als Vertreterinnen derselben Art auf dem Land. Die Unterschiede in der Körpergröße könnten eine Folge der zunehmend zerstückelten Lebensräume in Städten sein, wie das Forschungsteam in der Fachzeitschrift Evolutionary Applications schreibt.
Mehr17.08.2020 | Forschung, iDiv, iDiv-Mitglieder, MLU News, Physiologische Diversität, TOP NEWS, UFZ-News
Ökosysteme: Was sagen Schwellenwerte wirklich aus?
Basiert auf einer Medienmitteilung der Carl von Ossietzky Universität Oldenburg. Oldenburg/Leipzig/Halle. Viele politische Maßnahmen, die die Folgen globaler Umweltveränderungen abmildern sollen, stützen sich auf das Konzept der sogenannten Kipppunkte. Demnach schlägt ein Ökosystem in einen anderen, oft schlechteren Zustand um, sobald eine Belastung, wie etwa der Verlust der biologischen Vielfalt, einen bestimmten Schwellenwert überschreitet. Ein Team aus Wissenschaftlern der Carl von Ossietzky Universität Oldenburg, des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) und weiterer internationaler Forschungseinrichtungen zeigt nun in Nature Ecology and Evolution, dass solche Schwellenwerte kaum zu identifizieren sind. Das Fokussieren auf solche Werte berge daher die Gefahr, die negativen Auswirkungen allmählicher Veränderungen auf Ökosysteme zu übersehen – mit möglicherweise schwerwiegenden Folgen.
Mehr10.08.2020 | Arten-Interaktionsökologie, Forschung, iDiv, Medienmitteilung, MLU News, sDiv, TOP NEWS, UFZ-News
Veränderte Landnutzung beeinträchtigt Bestäubung von Wildpflanzen
Leipzig/Halle. Die intensive Landnutzung durch den Menschen beeinträchtigt weltweit die Bestäubung von Wildpflanzen und deren Fortpflanzungserfolg. Das betrifft insbesondere Pflanzen, die in ihrer Bestäubung hochspezialisiert sind. Zu diesem Schluss kommt eine neue Studie unter Leitung des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv), der Martin-Luther-Universität Halle-Wittenberg (MLU) und des Helmholtz-Zentrums für Umweltforschung (UFZ), die in Nature Communications wurde. Mithilfe eines globalen Datensatzes ist es dem Forschungsteam gelungen, diesem Zusammenhang zu untersuchen.
Mehr04.08.2020 | Experimentelle Interaktionsökologie, Medienmitteilung, TOP NEWS
Bodenchemikalien hemmen Zersetzung von Pflanzenresten – durch Schädigung der Biodiversität
Leipzig, Namur. Die schlechtere Verrottung von Pflanzenresten unter dem Einfluss von Chemikalien ist auf die Beeinträchtigung der Biodiversität zurückzuführen. Dies sind die neuen Erkenntnisse einer Studie, die in der Open-Access-Zeitschrift eLife veröffentlicht wurde. Die Ergebnisse deuten darauf hin, dass viele menschliche Chemikalieneinträge wie Pestizide und Schwermetalle die Zahl der Arten und Individuen von Bodenorganismen verringern, was ihre Funktionen im Ökosystem – etwa die Zersetzung – signifikant verringert. Dies gilt jedoch nicht generell für Nährstoffzusätze. Die globale Meta-Analyse wurde von Forschern des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv), der Universität Leipzig und der Universität Namur in Belgien durchgeführt. Sie deckt wichtige anthropogene Einflüsse auf die biologische Vielfalt und die Funktionsweise von Ökosystemen auf und hilft so, die Entwicklungen verschiedener Ökosysteme weltweit vorherzusagen.
Mehr03.08.2020 | iDiv, Medienmitteilung, TOP NEWS, UFZ-News
Schmetterlingsvielfalt in Leipzig
Basiert auf einer Pressemitteilung des Helmholtz-Zentrums für Umweltforschung (UFZ) Über 180 Tagfalterarten kommen in Deutschland vor und rund 40 Prozent von ihnen sind bestandsgefährdet oder vom Aussterben bedroht. Ein von UFZ und iDiv koordiniertes Projektteam wird im Rahmen des vom Bundesprogramm Biologische Vielfalt geförderten Kommunikations- und Bildungsprojekts „VielFalterGarten“ nicht nur die Vielfalt der Schmetterlinge erfahrbar machen, sondern auch aufzeigen, was für deren Schutz auf privatem und städtischem Grün getan werden kann. Dazu finden offene Workshops statt, in denen interessierten Bürgerinnen und Bürgern Artenkenntnis, die Ökologie der Tagfalter sowie praktische Anleitungen für ökologische Maßnahmen vermittelt werden. Die ersten Workshops finden am 5. August (Gemeinschaftsgarten Grünau) und 7. August (Lene-Voigt-Park) statt.
Mehr03.08.2020 | Experimentelle Interaktionsökologie, Forschung, iDiv, Medienmitteilung, MLU News, TOP NEWS
Weiße Flecken in den Böden der Erde
Leipzig/Halle. Ein großer Teil der weltweiten biologischen Vielfalt befindet sich in den Böden. Doch das Wissen über die Verbreitung von Bodenlebewesen und ihrer Funktionen ist lückenhaft und nicht repräsentativ für die globalen Ökosysteme und Artengruppen. Insbesondere die tropischen und subtropischen Regionen sind hinsichtlich der Biodiversität im Boden kaum erforscht sind Zu diesem Ergebnis kommt eine Studie, die nun im Fachmagazin Nature Communications veröffentlicht worden ist und von Wissenschaftlern des Deutschen Zentrums für integrative Biodiversitätsforschung, der Martin-Luther-Universität Halle-Wittenberg sowie der Universität Leipzig geleitet wurde.
Mehr29.07.2020 | Arten-Interaktionsökologie, Biodiversitätssynthese, Forschung, iDiv, Medienmitteilung, MLU News, TOP NEWS, UFZ-News
Schlimmer als gedacht: Rückgang der Artenvielfalt durch Habitatverluste unterschätzt
Leipzig/Halle. Mittlerweile ist es auch in der Politik angekommen: Um das Aussterben von Tieren und Pflanzen zu verringern, müssen deren Lebensräume geschützt und wiederhergestellt werden. Doch die entsprechenden politischen Maßnahmen stützen sich oft auf Vorhersagen durch ein einfaches theoretisches Modell, das beschreibt, wie sich die Artenzahl im Verhältnis zum vorhandenen Lebensraum verändert. Eine neue Studie im Fachmagazine Nature zeigt nun, dass dieses Standard-Modell unterschätzt, wie viele Arten tatsächlich auf lokaler Ebene aussterben. Forscher vom Deutschen Zentrum für integrative Biodiversitätsforschung (iDiv), von der Martin-Luther-Universität Halle-Wittenberg (MLU) und vom Helmholtz-Zentrum für Umweltforschung (UFZ) haben dazu Daten aus 123 Studien ausgewertet und Ansätze entwickelt, die realistischere Biodiversitätsvorhersagen unter Berücksichtigung des Verlustes von Lebensräumen und deren Wiederherstellung ermöglichen.
Mehr28.07.2020 | Experimentelle Interaktionsökologie, iDiv-Mitglieder, TOP NEWS, UFZ-News
Das Schrumpfen der Zwerge
Basiert auf einer Pressemitteilung des Helmholtz-Zentrums für Umweltforschung (UFZ) Das Leben im Erdreich hat heutzutage gleich mit mehreren Problemen zu kämpfen. Die Biomasse der kleinen Tiere, die dort Pflanzen zersetzen und damit die Fruchtbarkeit des Bodens erhalten, nimmt sowohl durch den Klimawandel als auch durch eine zu intensive Bewirtschaftung ab. Zu ihrer Überraschung haben Wissenschaftler des Helmholtz-Zentrums für Umweltforschung (UFZ), des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) und der Universität Leipzig allerdings festgestellt, dass dieser Effekt auf zwei unterschiedlichen Wegen zustande kommt: Während das veränderte Klima die Körpergröße der Organismen reduziert, verringert die Bewirtschaftung ihre Häufigkeit. Selbst mit Biolandwirtschaft lassen sich demnach nicht alle negativen Folgen des Klimawandels abpuffern, warnen die Forscher im Fachjournal eLIFE.
Mehr17.07.2020 | Forschung, iDiv, Medienmitteilung, Nachhaltigkeit und Komplexität der Lebensräume von Menschenaffen, TOP NEWS
Handel mit Buschfleisch: Klare Strategien zur Eindämmung nötig
Leipzig. Der extensive Handel mit Wildtieren stellt nicht nur eine Bedrohung für viele Arten weltweit dar, er kann auch zur Übertragung von Krankheiten vom Tier auf den Menschen führen. Davon betroffen sind Hunderte von Tierarten, die sich hinsichtlich ihres Schutzstatus‘ und potentiell übertragbarer Krankheiten teils beträchtlich unterscheiden. Doch diese Unterschiede werden bei der Erarbeitung von Strategien zur Eindämmung des Wildtierhandels selten berücksichtigt. Ein internationales Forscherteam unter Leitung des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) und des Max-Planck-Institutes für evolutionäre Anthropologie (MPI-EVA) zeigt nun, weshalb Menschen verschiedene Wildtierarten jagen, konsumieren oder mit ihnen Handel treiben. Ihrer Forschung zufolge sind differenziertere Lösungsansätze notwendig, um den unkontrollierten Ausbruch von Krankheiten und den Rückgang gefährdeter Arten zu vermeiden.
Mehr17.07.2020 | Arten-Interaktionsökologie, iDiv, Medienmitteilung, TOP NEWS
Ausstellung „Blüten(be)sucher: Beziehungsgeschichten aus der Natur“ öffnet in Leipzig
Leipzig. Ab sofort beherbergt der Botanische Garten der Universität Leipzig eine neue Ausstellung, die einen etwas anderen Blick auf die Welt der Pflanzen und ihrer Bestäuber wirft. Anschaulich zeigen junge Wissenschaftler und Künstler aus Leipzig, dass es dabei um mehr geht als nur die Geschichte von der Biene und der Blüte.
Mehr14.07.2020 | iDiv-Mitglieder, Medienmitteilung, TOP NEWS
Wie viele invasive Arten vertragen unsere Ökosysteme?
Basiert auf einer Medienmitteilung der Universität Wien Schon 20 bis 30 Prozent mehr invasive Arten führen zu weltweiten dramatischen Biodiversitätsverlusten in der Zukunft. Zu diesem Schluss kommt die Studie eines internationalen Forscherteams unter der Leitung der Universität Wien und unter Beteiligung des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) und des Helmholtz-Zentrums für Umweltforschung UFZ. Ursachen seien vor allem der zunehmende globale Warentransport, der Klimawandel und das wirtschaftliche Wachstum. Die Studie wurde in der Fachzeitschrift Global Change Biology veröffentlicht.
Mehr29.06.2020 | iDiv-Mitglieder, TOP NEWS, UFZ-News
Wissenschaftler warnen vor zunehmenden Schäden durch gebietsfremde invasive Arten
Basiert auf einer Medienmitteilung des Helmholtz-Zentrums für Umweltforschung (UFZ) In einer eben erschienenen internationalen Studie warnen Wissenschaftlerinnen und Wissenschaftler, darunter auch Prof. Ingolf Kühn vom Helmholtz-Zentrum für Umweltforschung (UFZ), vor den zunehmenden negativen Auswirkungen gebietsfremder invasiver Tier- und Pflanzenarten auf die biologische Vielfalt und die Leistungen der Ökosysteme. Vor allem eine verbesserte internationale Zusammenarbeit sei notwendig, um die Einbringung weiterer Arten zu verhindern, neue Vorkommen zu ermitteln und vorhandene zu kontrollieren.
Mehr18.06.2020 | Biodiversitätssynthese, Forschung, iDiv, Medienmitteilung, MLU News, TOP NEWS
Waldverlust verstärkt Biodiversitätswandel
Basiert auf einer Medienmitteilung der Universität von St. Andrews Der Verlust von Waldflächen verringert nicht grundsätzlich die biologische Vielfalt – aber er kann sie stark verändern. Zu diesem Ergebnis kommt ein internationales Forscherteam unter Beteiligung des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) und der Martin-Luther-Universität Halle-Wittenberg (MLU). Die im Fachmagazin Science veröffentlichte Studie zeigt anhand von Biodiversitätsdaten der vergangenen 150 Jahre von mehr als 6000 Orten, dass der Rückgang von Wäldern auf der ganzen Welt bestehende Zunahmen oder Rückgänge bei den vorherrschenden Tier- und Pflanzenarten verstärkt. Doch diese Veränderungen werden mitunter erst nach Jahrzehnten deutlich.
Mehr04.06.2020 | Biodiversität und Mensch, iDiv, Medienmitteilung, TOP NEWS
Dialogforum widmet sich Citizen-Science-Strategie in Deutschland
Wie kann die Citizen-Science-Strategie in Deutschland weiterentwickelt werden? Dieser Frage widmet sich ein Online-Dialogforum am 26. Juni 2020, das unter maßgeblicher Beteiligung von Wissenschaftlern vom Deutschen Zentrum für integrative Biodiversitätsforschung (iDiv) und vom Helmholtz-Zentrum für Umweltforschung (UFZ) organisiert wird.
Mehr25.05.2020 | Biodiversität und Mensch, iDiv-Mitglieder, Medienmitteilung, TOP NEWS, UFZ-News
Den Blick auf Insekten lenken
Basiert auf einer Medienmitteilung des Helmholtz-Zentrums für Umweltforschung (UFZ) Paris, Halle, Leipzig. Das Netzwerk der Natura 2000-Schutzgebiete der Europäischen Union (EU) soll gefährdete Tier- und Pflanzenarten und deren Lebensräume schützen. Allerdings profitieren auch etliche Arten, die nicht im Fokus stehen. Nur sind diese Nutznießer ungleichmäßig über die großen Tiergruppen verteilt, berichtet ein internationales Forscher*innen-Team, darunter Wissenschaftler des Helmholtz-Zentrums für Umweltforschung (UFZ) sowie des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv), in der Zeitschrift Conservation Biology. So zieht fast die Hälfte der nicht in der Zielgruppe genannten Vogelarten Nutzen aus dem Natura 2000-Schutz, während bei den Tagfaltern nur ein gutes Viertel von einem solchen Mitnahmeeffekt profitiert.
Mehr20.05.2020 | Biodiversität und Naturschutz, Medienmitteilung, TOP NEWS
Internationaler Tag der Biodiversität 2020: Corona-Pandemie mahnt uns, Natur zu schützen
Leipzig, Halle. 2020 war eigentlich zum politischen „Superjahr“ ernannt worden. Im Oktober sollte die Vertragsstaatenkonferenz der UN-Konvention zur Biologischen Vielfalt (CBD), die COP-15, in China die Weichen für den internationalen Naturschutz der kommenden 10 Jahre stellen. Doch die Corona-Pandemie hat auch beim so genannten Post-2020-Prozess die Pausetaste gedrückt. COP-15 wurde bis auf weiteres verschoben. Die Pandemie macht aber auch deutlich, welch wichtige Rolle natürliche Ökosysteme für die menschliche Gesundheit spielen – als Quelle für Krankheitserreger, aber auch als Teil der Lösung. Das betont Prof. Dr. Henrique Miguel Pereira am diesjährigen Internationalen Tag der biologischen Vielfalt am 22. Mai mit dem Motto „Unsere Lösungen liegen in der Natur“. Pereira ist Leiter der Forschungsgruppe Biodiversität und Naturschutz am Deutschen Zentrum für integrative Biodiversitätsforschung (iDiv) und der Martin-Luther-Universität Halle-Wittenberg (MLU). Er ist Vorsitzender des Biodiversity Observation Network GEO BON und engagiert sich in mehreren Foren mit politischen Entscheidungsträgern, darunter der Weltbiodiversitätsrat IPBES und die CBD.
Mehr12.05.2020 | Forschung, iDiv, iDiv-Mitglieder, Medienmitteilung, TOP NEWS
Große Artenvielfalt – viele Heilpflanzen
Basiert auf einer Medienmitteilung der Universität Leipzig Heilpflanzen mit ihrem reichen Repertoire an anti-infektiven Substanzen waren seit jeher wichtige Helfer des Menschen im Überlebenskampf gegen Krankheitserreger und Parasiten. Die Suche nach pflanzlichen Wirkstoffen mit neuartigen Strukturen und Wirkprinzipien gehört daher bis heute zu den großen Herausforderungen der Naturstoffforschung. Wissenschaftler der Universität Leipzig (UL), des Leibniz-Instituts für Pflanzenbiochemie (IPB) und des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) haben nun einen Weg aufgezeigt, wie diese Suche nach natürlichen Wirkstoffen anhand von Datenanalysen zu Verwandtschaft, Verbreitung und Inhaltsstoffen von Pflanzen erheblich erleichtert werden kann. Der von ihnen entworfene Ansatz ermöglicht Vorhersagen darüber, in welchen Pflanzengruppen und geografischen Gebieten eine besonders hohe Dichte an Arten mit heilenden Wirkstoffen zu erwarten ist. In derart modellierten Hotspots könnte die Suche nach neuen Medizinalpflanzen künftig gezielter erfolgen.
Mehr11.05.2020 | Experimentelle Interaktionsökologie, Medienmitteilung, sDiv, TOP NEWS
Klimawandel fördert im Boden lebende Erreger von Pflanzenkrankheiten
Basiert auf einer Medienmitteilung der Pablo de Olavide Universität Sevilla Sevilla, Leipzig, Halle. Die Klimaerwärmung wird weltweit zu einer Zunahme von bodengebundenen Krankheitserregern für Pflanzen führen. Darunter sind auch Krankheiten wichtiger Nahrungs- und Arzneipflanzen, was langfristig die Ernährungssicherheit und Lebensqualität der Weltbevölkerung gefährden könnte. Zu diesem Ergebnis kommt eine experimentelle Studie unter Beteiligung von Wissenschaftlern des Deutschen Zentrum für integrative Biodiversitätsforschung (iDiv), der Universität Leipzig (UL) und der Martin-Luther-Universität Halle-Wittenberg (MLU), die im Fachmagazin Nature Climate Change veröffentlicht wurde.
Mehr04.05.2020 | Biodiversitätssynthese, Forschung, iDiv, Medienmitteilung, MLU News, TOP NEWS
Klimawandel verändert besonders die Meere
Basiert auf einer Medienmitteilung der Universität von St. Andrews Ändert sich die Temperatur, hat dies Auswirkungen auf die biologische Vielfalt in den Meeresgebieten: Eine Erwärmung führt in der Regel zu einer Zunahme der Zahl der Arten. Zu diesem Ergebnis kommt ein Team unter Leitung von Forschern der Universitäten in Helsinki, St. Andrews und Radboud mit Partnern vom Deutschen Zentrum für integrative Biodiversitätsforschung (iDiv) und der Martin-Luther-Universität Halle-Wittenberg (MLU). Die steigende Artenzahl ist wahrscheinlich auf klimabedingte Einwanderungen aus artenreichen wärmeren Regionen zurückzuführen. Die im Fachmagazin Nature Ecology and Evolution veröffentlichte Studie stellt Zusammenhänge zwischen Biodiversität und Temperatur her und vergleicht die Veränderungen in Ozeanen und an Land.
Mehr24.04.2020 | Biodiversitätssynthese, Medienmitteilung, sDiv, TOP NEWS
Bislang umfassendste Studie bestätigt Rückgang landlebender Insekten, zeigt aber Erholungen bei Süßwasserinsekten
Leipzig. Eine Analyse weltweiter Langzeitstudien zeigt, dass die Zahl landlebender Insekten zurückgeht. Sie sank im Schnitt um 0,92 % pro Jahr, was einem Rückgang von 24 % über 30 Jahre entspricht. Gleichzeitig stieg die Zahl der an Süßwasser gebundenen Insekten wie Libellen und Köcherfliegen um 1,08 % pro Jahr. Dies könnte die Folge von Gewässerschutzmaßnahmen sein. Diesen durchschnittlichen, globalen Trends stehen sehr unterschiedliche Entwicklungen vor Ort gegenüber. Dabei scheinen menschliche Einflüsse die Trends zu verstärken. Zu diesen Ergebnissen kommt die bislang umfassendste Meta-Analyse von Insektenbeständen an 1676 Orten weltweit. Die Studie wurde von Forschern des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv), der Universität Leipzig (UL) und der Martin-Luther-Universität Halle-Wittenberg (MLU) geleitet und ist in der jüngsten Ausgabe der Fachzeitschrift Science erschienen. Sie schließt wichtige Wissenslücken im Kontext des viel diskutierten „Insektensterbens“.
Mehr13.04.2020 | Biodiversität und Naturschutz, Forschung, iDiv, Medienmitteilung, MLU News, sDiv, TOP NEWS
Pflanzenvielfalt in Europas Wäldern nimmt ab
Leipzig/Halle. In Europas gemäßigten Wäldern werden wenig verbreitete Pflanzenarten von jenen Arten verdrängt, die stärker verbreitet sind. Ein internationales Forscherteam unter Leitung des Deutschen Zentrums für Integrative Biodiversitätsforschung (iDiv) und der Martin-Luther-Universität Halle-Wittenberg (MLU) hat nun herausgefunden, dass diese Entwicklung mit einer erhöhten Stickstoffverfügbarkeit zusammenhängt. Ihre Ergebnisse veröffentlichten sie im Fachmagazin Nature Ecology & Evolution.
Mehr09.04.2020 | Forschung, iDiv, Medienmitteilung, TOP NEWS, Waldökologie und -modellierung
Ein Blick in die Zukunft der Tropenwälder
Leipzig/Panama-Stadt. Tropische Wälder sind ein Hotspot der Artenvielfalt. Auch vor dem Hintergrund des Klimawandels spielt ihr Schutz eine besondere Rolle. Dabei ist es wichtig vorherzusagen, wie sich so artenreiche Waldbestände über Jahrzehnte oder gar Jahrhunderte verändern. Genau dies ist nun Forschern des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv), der Universität Leipzig (UL) und weiterer internationaler Forschungseinrichtungen gelungen. Die Ergebnisse haben sie im Fachmagazin Science veröffentlicht.
Mehr30.03.2020 | Biodiversität und Mensch, Medienmitteilung, sDiv, TOP NEWS, UFZ-News
Ökosystemleistungen kennen keine Grenzen
Basiert auf einer Medienmitteilung des Helmholtz-Zentrums für Umweltforschung (UFZ) Was haben Kakao, Zugvögel, Hochwasserschutz und Pandas gemeinsam? Viele Länder profitieren von Ökosystemleistungen, die zuvor in anderen Ländern erbracht wurden. Wo und wie Ökosystemleistungs-Ströme verlaufen, ist jedoch kaum bekannt. Wissenschaftler des Helmholtz-Zentrums für Umweltforschung (UFZ) und des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) konnten nun in einer im Fachjournal Global Environmental Change veröffentlichten Studie zeigen, wie interregionale Ökosystemleistungs-Ströme aufgedeckt und quantifiziert werden können.
Mehr18.03.2020 | Biodiversität und Naturschutz, Medienmitteilung, TOP NEWS
EU-Biodiversitätsstrategie: Wiederherstellung intakter Natur
Mehr13.03.2020 | Forschung, iDiv, Medienmitteilung, sDiv, TOP NEWS
Pflanzenleben unter härtesten Bedingungen
Mehr03.03.2020 | Biodiversität und Mensch, iDiv, Medienmitteilung, TOP NEWS
Steuergelder für Umwelt und Gemeinwohl
Leipzig. Schnelles und effektives Handeln erwarten Wissenschaftler aus ganz Europa von der EU im Rahmen ihrer Gemeinsamen Agrarpolitik (GAP). In einem Positionspapier, verfasst von 21 Autoren unter Koordination von Wissenschaftlern des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv), des Helmholtz-Zentrums für Umweltforschung (UFZ) und der Universität Rostock, bewerten sie die aktuellen Reformvorschläge der EU-Kommission als unzureichend. Weder die angestrebten Klima- und Naturschutzziele noch wesentliche soziale Ziele der EU Agrarpolitik würden so erreicht. Milliarden Euro von Steuergeldern würden ineffektiv eingesetzt – wider besseres Wissen. Die Forscher schlagen zehn Maßnahmen für eine nachhaltige und gerechte Landwirtschaft vor. Über 3600 Unterzeichner unterstützen die Forderungen.
Mehr26.02.2020 | Evolution und Adaptation, Forschung, iDiv, Medienmitteilung, TOP NEWS
Farbensehen bei Primaten mit dem Vorkommen farbiger Palmfrüchte verknüpft
Leipzig/Amsterdam. Die Entwicklung des Farbensehens könnte eng mit der Verfügbarkeit von Nahrung verbunden sein. Forscher vom Deutschen Zentrum für integrative Biodiversitätsforschung (iDiv), der Universität Leipzig (UL) und der Universität von Amsterdam (UvA) fanden heraus, dass das Farbensehen bei afrikanischen Primatenarten – eine Fähigkeit, die sie mit dem Menschen gemeinsam haben – mit der räumlichen Verbreitung der Farben von Palmfrüchten zusammenhängt. Die Ergebnisse ihrer Studie wurden im Fachmagazin Proceedings of the Royal Society B veröffentlicht und geben neue Einblicke in die Evolution der Primaten.
Mehr14.02.2020 | Forschung, iDiv, Medienmitteilung, sDiv, TOP NEWS
Klimawandel führt zu abrupten Veränderungen in Trockengebieten
Mehr31.01.2020 | Forschung, iDiv, Medienmitteilung, sDiv, TOP NEWS
Wissenschaftler besorgt über Ergrünen der Arktis
Mehr29.01.2020 | iDiv-Mitglieder, Medienmitteilung, TOP NEWS, yDiv
Bestäubung funktioniert in Städten besser als auf dem Land
Blütenpflanzen werden in Städten besser bestäubt als im Umland. Das zeigt das Experiment eines Wissenschaftlerteams unter Leitung des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv), der Martin-Luther-Universität Halle-Wittenberg (MLU) und des Helmholtz-Zentrums für Umweltforschung (UFZ). Die Forscher fanden zwar auf dem Land insgesamt eine größere Vielfalt an Fluginsekten – in den Städten sorgten aber mehr Bienen und Hummeln für mehr bestäubte Blüten an den Testpflanzen. Mit Abstand am fleißigsten bestäubten Hummeln, die vermutlich von einer höheren Zahl geeigneter Lebensräume in der Stadt profitieren. Um Bestäubung zu fördern, empfehlen die Forscher, die Bedürfnisse von Bienen bei der Grünflächenplanung besser zu berücksichtigen. Die Ergebnisse wurden in der Zeitschrift Nature Communications veröffentlicht.
Mehr23.01.2020 | Biodiversität und Mensch, iDiv, Medienmitteilung, TOP NEWS
Öffentlicher Vortrag „Schmetterlinge und Politik“
Wie hängen Klimawandel und Insektensterben zusammen? Was haben Insekten mit der EU-Agrarpolitik zu tun? Und was kann jeder Einzelne gegen das Insektensterben tun? Mit diesen Fragen beschäftigen sich Wissenschaftler des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) in einer gemeinsamen öffentlichen Veranstaltung mit dem BUND Leipzig (Ortsgruppe Ost) und Scientists For Future am 24.01.2020 ab 18 Uhr. Im Anschluss an den Vortrag Schmetterlinge und Politik von Dr. Guy Pe’er gibt es eine Diskussion zum Thema.
Mehr22.01.2020 | Medienmitteilung, sDiv, TOP NEWS
Auch tote Tiere sind wichtig fürs Ökosystem
Tierkadaver spielen eine wichtige Rolle für die Artenvielfalt und das Funktionieren von Ökosystemen – auch über längere Zeiträume. Diese Erkenntnisse haben Wissenschaftler des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) und der Reichsuniversität Groningen in der Zeitschrift PLOS ONE veröffentlicht. Die Kadaver bieten nicht nur vielen aasfressenden Tierarten Nahrung, ihre Nährstoffe tragen auch zu einem wesentlich stärkten Wachstum umliegender Pflanzen bei. Dies begünstigt wiederum viele pflanzenfressende Insekten und deren Räuber. Die Forscher empfehlen, rechtliche Regelungen, die die Beseitigung von Kadavern vorschreiben, für Naturschutzgebiete zu lockern.
Mehr17.01.2020 | Biodiversität und Naturschutz, iDiv, Medienmitteilung, MLU News, TOP NEWS
EU-Biodiversitätsstrategie nach 2020: Für eine Rückkehr zur Natur
Basiert auf einer Medienmitteilung von Rewilding Europe Die großflächige Wiederherstellung von Naturlandschaften kann sowohl die aktuelle Klima- als auch die Biodiversitätskrise bekämpfen. Ein heute von sechs Institutionen herausgegebenes Strategiepapier, an dem auch das Deutsche Zentrum für integrative Biodiversitätsforschung (iDiv) und die Martin-Luther-Universität Halle-Wittenberg (MLU) beteiligt sind, fordert von der Europäischen Kommission eine stärkere Priorisierung sogenannter Rewilding-Maßnahmen in der neuen EU-Biodiversitätsstrategie nach 2020. Rewilding bezeichnet die Wiederherstellung der Natur mit geringen menschlichen Eingriffen.
Mehr13.01.2020 | iDiv, Medienmitteilung, sDiv, TOP NEWS
iDiv erhält Auszeichnung der UN-Dekade Biologische Vielfalt
Das Deutsche Zentrum für integrative Biodiversitätsforschung (iDiv) ist für das Projekt sMon von der UN-Dekade Biologische Vielfalt ausgezeichnet worden. Dr. Andreas Krüß vom Bundesamt für Naturschutz übergibt am Dienstag, den 14. Januar, Urkunde und Trophäe an die Projektbeteiligten. sMon bringt Experten aus 16 Bundesländern zusammen, um gemeinsam die Frage zu beantworten: Wo verändert sich Biodiversität und in welchem Ausmaß? Die Auszeichnung „Projekt der UN-Dekade Biologische Vielfalt“ wird an Projekte verliehen, die sich in besonderer Weise für die Erhaltung der biologischen Vielfalt in Deutschland einsetzen.
Mehr13.12.2019 | iDiv-Mitglieder, TOP NEWS, UFZ-News
Den gordischen Knoten durchschlagen
Basiert auf einer Medienmitteilung des Helmholtz-Zentrums für Umweltforschung – UFZ. Seit den 1970er Jahren wächst der Einfluss der Menschheit auf die Natur rasant, berichten Wissenschaftlerinnen und Wissenschaftler aus aller Welt in der aktuellen Ausgabe der renommierten Fachzeitschrift Science. Da aber eine Reihe von eng miteinander verzahnten Einflüssen vom Klimawandel bis zu Überfischung und Landübernutzung die Umwelt in die Zange nehmen, sollten diese weltweiten Herausforderungen alle gleichzeitig an der Wurzel gepackt werden, um weitere massive globale Schäden noch zu verhindern. Und das müsste sofort geschehen, betonen die Forscher. Unter den Autoren ist auch das iDiv-Mitglied Prof. Josef Settele vom Helmholtz-Zentrum für Umweltforschung – UFZ.
Mehr09.12.2019 | Biodiversität und Naturschutz, Forschung, iDiv, Medienmitteilung, sDiv, TOP NEWS
Städtewachstum verursacht stärksten Verlust der biologischen Vielfalt außerhalb der Städte
Leipzig/Halle/Arlington. Die zunehmende Urbanisierung und die damit einhergehende Umwandlung natürlicher Lebensräume in Stadtgebiete führen in Städten zu einem deutlichen Verlust der natürlichen Vielfalt. Doch diese direkten Folgen des Städtewachstumes sind anscheinend weitaus geringer als die indirekten Auswirkungen außerhalb der Städte. Dazu gehören die Freisetzung von Treibhausgasen in den Städten, die weltweit zu einer Veränderung des Klimas führen, oder der zunehmende Bedarf an Lebensmitteln und anderen Ressourcen, der eine veränderte Landnutzung zur Folge hat. Sowohl Klima- als auch Landnutzungswandel sind wesentliche Gründe für den weltweiten Verlust der Artenvielfalt. Ein Forscherteam der Naturschutzorganisation The Nature Conservancy (TNC), des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv), der Martin-Luther-Universität Halle-Wittenberg (MLU) und anderer Forschungseinrichtungen hat die direkten und indirekten Auswirkungen des Städtewachstums auf globaler Ebene untersucht. Die Ergebnisse wurden im Fachmagazin Nature Sustainability veröffentlicht.
Mehr22.11.2019 | Forschung, iDiv, Medienmitteilung, Physiologische Diversität, sDiv, TOP NEWS
Biologische Vielfalt auf ehemaligen Nutzflächen auch nach hundert Jahren noch beeinträchtigt
Basiert auf einer Medienmitteilung der University of Minnesota. Minnesota/Leipzig. Auch Jahrzehnte nach der Stilllegung landwirtschaftlicher Flächen hat sich die Pflanzenwelt noch nicht vollständig erholt. Das zeigt eine Studie in der Fachzeitschrift Nature Ecology & Evolution. Wissenschaftler vom Deutschen Zentrum für integrative Biodiversitätsforschung (iDiv), dem Helmholtz-Zentrum für Umweltforschung (UFZ) und der University of Minnesota untersuchten die pflanzliche Vielfalt und Produktivität auf Flächen, die in der Vergangenheit als Acker genutzt wurden und deren landwirtschaftliche Nutzung eingestellt wurde. Während die pflanzliche Vielfalt auf den Wiesen mit der Zeit wieder zunimmt, bleibt die Produktivität der Pflanzen eingeschränkt.
Mehr08.11.2019 | Biodiversität und Mensch, iDiv-Mitglieder, Medienmitteilung
Mittelhäufige Pflanzenarten sind am stärksten zurückgegangen
Basiert auf einer Medienmitteilung der Universität RostockRostock/Leipzig. Arten, die früher häufig waren, zeigen die höchsten Verluste und sind durchschnittlich auf die Hälfte ihrer früheren Verbreitung zurückgegangen. Das haben Forscher der Universität Rostock und des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) anhand von Daten aus Mecklenburg-Vorpommern gezeigt. Sie haben ihre Ergebnisse im Fachjournal Conservation Letters veröffentlicht.
Mehr24.10.2019 | Experimentelle Interaktionsökologie, Medienmitteilung, sDiv, TOP NEWS
Lokale Regenwurm-Vielfalt in Europa größer als in den Tropen
Leipzig. An einem Ort der gemäßigten Breiten gibt es meist mehr Regenwürmer und mehr Regenwurmarten als an einem Ort gleicher Größe in den Tropen. Der Klimawandel könnte das Vorkommen von Regenwürmern und damit auch ihre Funktionen für Ökosysteme weltweit verändern. Dies sind die zentralen Ergebnisse einer Studie, die in der aktuellen Ausgabe der Fachzeitschrift Science veröffentlicht wurde. Für die Studie hat ein Wissenschaftlerteam unter Führung des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) und der Universität Leipzig zusammen mit 140 internationalen Wissenschaftlern den weltweit größten Regenwurmdatensatz zusammengestellt – mit Informationen von 6928 Standorten aus 57 Ländern.
Mehr21.10.2019 | Forschung, iDiv, iDiv-Mitglieder, Medienmitteilung, TOP NEWS
Makaken können durch das Jagen von Ratten Palmölproduktion nachhaltiger und effizienter machen
Leipzig/Gelugor. Der Südliche Schweinsaffe, eine Makakenart aus Südostasien, hat in Malaysia keinen sonderlich guten Ruf und gilt gemeinhin als Plantagenschädling. Doch tatsächlich ernähren sich die Affen auch von Ratten, der größten Plage im Palmölanbau, und können damit eine wichtige Ökosystemdienstleistung durch natürliche Schädlingsbekämpfung erbringen. Das fanden Wissenschaftler der Universiti Sains Malaysia (USM), des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv), der Universität Leipzig (UL) und des Max-Planck-Instituts für evolutionäre Anthropologie (MPI EVA) heraus. Gemeinsam untersuchten sie Kosten und Nutzen von Makaken in Palmölplantagen. Ihre Ergebnisse wurden nun in der Fachzeitschrift Current Biology veröffentlicht.
Mehr18.10.2019 | Biodiversitätssynthese, Forschung, iDiv, Medienmitteilung, sDiv, TOP NEWS
Veränderung der Arten-Zusammensetzung in Ökosystemen weltweit
Leipzig/Halle/St. Andrews. An vielen Orten auf der ganzen Welt finden rasante Veränderungen der Biodiversität statt. Doch während sich die jeweiligen Arten in den lokalen Gemeinschaften stark verändern, bleibt die Zahl der Arten im Durchschnitt oft gleich. Daher spiegeln die Veränderungen auf lokaler Ebene nicht immer den globalen Artenverlust wider. Dies ist das Ergebnis einer Untersuchung, die von einem Forscherteam unter Leitung des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv), der Martin-Luther-Universität Halle-Wittenberg (MLU) und der Universität St. Andrews durchgeführt wurde. Die Studie wurde im Fachmagazin Science veröffentlicht und zeigt, dass sich die Zusammensetzung der Arten in marinen Ökosystemen stärker verändert als an Land. Dabei unterliegen insbesondere die marinen Tropen extremen Veränderungen.
Mehr08.10.2019 | Biodiversität und Naturschutz, Forschung, iDiv, Medienmitteilung, TOP NEWS
Globaler Süden leidet am stärksten unter Klimawandel und Landnutzung
Basiert auf einer Medienmitteilung des Natural Capital Project Leipzig/Stanford. Bis zum Jahr 2050 könnten bis zu fünf Milliarden Menschen von Wasserverschmutzung, Küstenstürmen oder unbestäubten Nutzpflanzen bedroht sein – ein Großteil davon in Entwicklungsländern. Zu diesem Ergebnis kommt eine Studie im Fachmagazin Science, die von einem internationalen Forscherteam mit Beteiligung des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) und der Martin-Luther-Universität Halle-Wittenberg (MLU) verfasst wurde. Die Forscher erstellten eine hochauflösende globale Karte, welche die Leistungen der Natur für den Menschen darstellt. Diese sogenannten Ökosystemleistungen sind durch die vom Menschen verursachte Schädigung der Ökosysteme und der Biodiversität bedroht. Die neue Karte kann helfen, politische Entscheidungen zum Schutz der Natur zu verbessern – sowohl lokal als auch global. Durch eine nachhaltige Entwicklung können die Gefahren um ein Vielfaches gemindert werden.
Mehr30.09.2019 | Experimentelle Interaktionsökologie, Forschung, iDiv, Medienmitteilung, TOP NEWS
Neue Forschungsgruppe schlägt Brücken in Mitteldeutschland
Gemeinsame Medienmitteilung von iDiv, Universität Leipzig und Friedrich-Schiller-Universität Jena Jena/Leipzig. Die Deutsche Forschungsgemeinschaft (DFG) fördert eine neue Forschungsgruppe im Jena Experiment mit fünf Millionen Euro über einen Zeitraum von vier Jahren. Die Wissenschaftler werden unter Führung des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv), der Universität Leipzig und der Friedrich-Schiller-Universität Jena die Mechanismen untersuchen, die dem Zusammenhang zwischen Biodiversität und Ökosystemfunktionen zugrunde liegen. Dafür binden sie weitere experimentelle Plattformen ein.
Mehr26.09.2019 | Biodiversitätsökonomik, Medienmitteilung, TOP NEWS
Skepsis deutscher Fischer gegenüber EU erschwert Einhaltung der EU-Regelungen
Leipzig/Hamburg/Kiel: Ein schlechtes Image einer Regulierungsinstanz wie der EU reduziert die Ehrlichkeit der Regulierten, etwa der Fischer. Diese Schlussfolgerung ziehen Forscher des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv), der Universität Leipzig, der Universität Hamburg und des Kieler Instituts für Weltwirtschaft aus einem Glücksspiel-Experiment mit EU-kritischen Berufsfischern und Brexit-Wählern. Die Erkenntnis hilft unter anderem bei der Einschätzung, wie effektiv EU-Fischereiregelungen sind, die nicht kontrolliert werden. Die Studie, die im European Economic Review erschienen ist, zeigte aber auch: Die Berufsfischer waren ehrlicher als Studenten.
Mehr18.09.2019 | iDiv, Medienmitteilung, sDiv, TOP NEWS
Klima und Biodiversität gehören zusammen – Klimawandel zerstört unsere natürlichen Lebensgrundlagen
Leipzig. Die Klimaerwärmung verändert die Natur mit all ihrer Vielfalt. Sie gefährdet die Bedingungen, von der unsere Ernährung und elementare Dinge des menschlichen Lebens abhängen. Zunehmende Knappheit von sauberem Wasser und fruchtbaren Böden könnten zu globalen Konflikten führen. Den Zusammenhang von Klima und Biodiversität thematisieren zwei iDiv-Wissenschaftler (Dr. Roel van Klink und Prof. Nicole van Dam) in ihren Reden bei der Leipziger Fridays-for-Future-Demonstration am 20. September. Zahlreiche Mitarbeiter des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) werden an der Demonstration teilnehmen.
Mehr16.09.2019 | Arten-Interaktionsökologie, Medienmitteilung, TOP NEWS
Klimawandel: Es gibt zu wenig realistische Experimente zu den Folgen für Ökosysteme
Basierend auf einer Medienmitteilung der Martin-Luther-Universität Halle-Wittenberg (MLU) Wenn es um die Folgen des Klimawandels für Ökosysteme geht, gibt es bisher noch eine große Wissenslücke. Die meisten Experimente dazu sind unrealistisch, weil sie nicht auf gängigen Klimavorhersagen für die jeweilige Region basieren. Deshalb gibt es bisher fast keine verlässlichen Daten dazu, wie Ökosysteme in Zukunft aussehen werden. Zu diesem überraschenden Schluss kommt ein Team von mitteldeutschen Biodiversitätsforschern in der Fachzeitschrift Global Change Biology. Für die Arbeit hat es die verfügbaren Studien zu dem Thema ausgewertet. Die Forschenden fordern, gemeinsame Standards für künftige Experimente einzuführen.
Mehr05.09.2019 | iDiv, Medienmitteilung, TOP NEWS
Vielfalt erhöht die Widerstandskraft
Basiert auf einer Medienmitteilung der Universität Freiburg Leipzig/Freiburg. Wälder mit einer hohen Artenvielfalt sind produktiver und stabiler gegenüber Stress als solche, die gleichförmig zusammengesetzt sind: Diesen Befund haben Wissenschaftlerinnen und Wissenschaftler der Universität Freiburg und des Deutschen Zentrums für Integrative Biodiversitätsforschung (iDiv) anhand von Daten aus dem weltweit ältesten Freilandexperiment zur Diversität tropischer Baumarten bestätigt. Das Team um den Doktoranden Florian Schnabel hat seine Ergebnisse im Fachjournal „Global Change Biology“ veröffentlicht.
Mehr02.08.2019 | Biodiversität und Mensch, Medienmitteilung, sDiv, TOP NEWS
EU-Landwirtschaft nicht zukunftsfähig
Leipzig, Brüssel. Die aktuellen Reformvorschläge der EU-Kommission zur Gemeinsamen Agrarpolitik (GAP) lassen keine Verbesserungen beim Umweltschutz erwarten. Dies konstatiert ein Forscherteam unter Leitung des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv), des Helmholtz-Zentrums für Umweltforschung (UFZ) und der Georg-August-Universität Göttingen in der Fachzeitschrift Science. Zwar bekenne sich die EU zu mehr Nachhaltigkeit, in den GAP-Reformvorschlägen spiegele sich dies jedoch nicht wider. Die Autoren zeigen, wie der laufende Reformprozess wissenschaftlichen Erkenntnissen und öffentlichen Forderungen nach mehr Umwelt- und Klimaschutz gerecht werden könne.
Mehr29.07.2019 | Biodiversitätssynthese, Medienmitteilung, TOP NEWS
Hawaiis alte Inseln beheimaten die meisten Arten
Internationales Forscherteam untersucht Zusammenspiel von Geologie und Biodiversität Medienmitteilung der Universität Göttingen Göttingen/Halle/Leipzig/Hawaii: Das Verständnis, wie die Biodiversität durch mehrere Kräfte geformt wird, ist entscheidend für den Schutz seltener Arten und einzigartiger Ökosysteme. Ein internationales Forschungsteam unter der Leitung der Universität Göttingen, des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv), des Helmholtz-Zentrums für Umweltforschung (UFZ) und der Martin-Luther-Universität Halle-Wittenberg (MLU) sowie der University of Hawai’i in Mānoa hat festgestellt, dass die Biodiversität auf älteren Inseln höher ist als auf jüngeren. Darüber hinaus fanden sie heraus, dass eingeführte Arten die Auswirkungen des Inselalters auf die Muster der lokalen Biodiversität verwässern. Die Ergebnisse sind in der Fachzeitschrift PNAS erschienen.
Mehr09.04.2019 | iDiv-Mitglieder, Medienmitteilung, TOP NEWS
Pflanzenvielfalt erhöht Insektenvielfalt
Halle, Leipzig, Göttingen. Je mehr Pflanzenarten in Wiesen und Wäldern leben, desto mehr Insektenarten finden dort Lebensraum. Mehr Pflanzenarten erhöhen aber nicht nur die Zahl der Insektenarten, sondern auch die Zahl ihrer Individuen. Gleichzeitig wird die tierische Vielfalt nicht nur von der pflanzlichen Artenvielfalt bestimmt, sondern auch von der pflanzlichen Strukturvielfalt. Dies sind Ergebnisse einer internationalen Zusammenarbeit unter Führung des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv), die in der Fachzeitschrift Nature Communications veröffentlicht worden sind. Sie haben Konsequenzen für die insektenfreundliche Bewirtschaftung von Wiesen und Wäldern.
Mehr02.04.2019 | Biodiversitätssynthese, iDiv, Medienmitteilung, TOP NEWS
Verlust von Lebensräumen schadet der Artenvielfalt doppelt
Halle/Lunz (A). Der Verlust und die Fragmentierung von Lebensräumen zählen zu den wichtigsten Ursachen, warum an vielen Orten weltweit der Artenreichtum zurückgeht. Jetzt hat ein Forscherteam unter Beteiligung des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) und der Martin-Luther-Universität Halle-Wittenberg (MLU) nachgewiesen, dass sich die Zerstörung von Lebensräumen sogar doppelt auswirkt: Wenn Lebensräume verloren gehen, verschwinden nicht nur die dort lebenden Arten – auch in benachbarten Lebensräumen sinkt die Artenzahl. Ursache seien die zu großen räumlichen Abstände zwischen den noch verbliebenen Lebensräumen, schreiben die Forscher im Fachblatt Ecology Letters.
Mehr27.03.2019 | Biodiversität und Mensch, Medienmitteilung, TOP NEWS
Europas Agrarlandschaften gehen die insektenfressenden Vögel aus
Frankfurt am Main/Leipzig. Die Anzahl an Vögeln, die hauptsächlich Insekten fressen, ist in der Europäischen Union während der letzten 25 Jahre signifikant gesunken. Hauptgrund ist das Verschwinden dieser Insektenfresser aus der Agrarlandschaft, berichten Forschende des Senckenberg Biodiversität und Klima Forschungszentrums und des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) aktuell im Fachjournal Conservation Biology. Sie hatten als Erste europaweit untersucht, wie die Ernährung und Bestandsentwicklung von Vögeln zusammenhängen. Insektenfresser machen rund die Hälfte aller europäischen Vogelarten aus.
Mehr13.03.2019 | Biodiversität und Naturschutz, Experimentelle Interaktionsökologie, iDiv-Mitglieder, Medienmitteilung, sDiv, TOP NEWS
Artenvielfalt über- und unterirdisch nicht immer gleich
Leipzig. Ein internationales Forscherteam unter Leitung der Universität Leipzig und des Forschungszentrums iDiv hat in aufwändigen Studien wichtige neue Erkenntnisse zur Biodiversität ober- und unterhalb der Erdoberfläche erlangt: Sie fanden heraus, dass auf etwa 30 Prozent der terrestrischen Oberfläche unseres Planeten eine große Artenvielfalt an Flora, Fauna und Mikroben im Boden herrscht, jedoch über der Erde deutlich weniger Arten leben oder umgekehrt, oberirdisch herrschte im Gegensatz zum Boden Artenreichtum. Diese Unterschiede in der Biodiversität waren in den restlichen 70 Prozent der terrestrischen Erdoberfläche nicht nachweisbar. Hier gab es ober- und unterhalb der Erde entweder Artenreichtum oder weniger Diversität, sogenannte Hot- und Cold-Spots. Die Forscher haben die Ergebnisse ihrer Studie jetzt im Fachjournal Conservation Biology veröffentlicht.
Mehr04.03.2019 | Biodiversität und Naturschutz, Medienmitteilung, TOP NEWS
Biodiversitätskrise: Technische Fortschritte in der Landwirtschaft reichen als Antwort nicht aus
Leipzig, Halle. Das rasante Bevölkerungs- und Wirtschaftswachstum zerstört die biologische Vielfalt – vor allem in den Tropen. Das berichtet ein Forscherteam unter der Leitung des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) und der Martin-Luther-Universität Halle-Wittenberg (MLU) in Nature Ecology & Evolution. Schuld daran ist die wachsende Nachfrage nach Agrarprodukten, die immer neue Anbauflächen verlangt. Zwar wird die Landwirtschaft durch technische Fortschritte immer effizienter, doch die wachsende Zahl an Menschen macht diese Erfolge wett. Klar ist: Eine wirksame Naturschutzpolitik braucht Konzepte gegen Bevölkerungswachstum und für nachhaltigen Konsum.
Mehr20.02.2019 | Biodiversitätssynthese, Medienmitteilung, TOP NEWS
Lückenlose Weltkarte der Baumarten-Vielfalt
Leipzig, Halle. Die biologische Vielfalt (Biodiversität) unseres Planeten ist eine unserer wichtigsten Ressourcen. Allerdings kennen wir von den meisten Orten der Erde nur einen kleinen Ausschnitt dieser Vielfalt. Forschern des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) und der Martin-Luther-Universität Halle-Wittenberg (MLU) ist es nun gelungen, aus versprengten Daten eine Weltkarte der Biodiversität zu erstellen; auf dieser ist die Anzahl von Baumarten dargestellt. Mithilfe der neuen Karte konnten die Forscher untersuchen, welche Einflussfaktoren die globale Baumartenvielfalt bestimmen. Das Klima spielt eine zentrale Rolle; zudem hängt die Vielfalt der Arten, die man in einem bestimmten Gebiet feststellt, aber auch von der räumlichen Skala der Betrachtung ab. Dies berichten die Forscher in der Fachzeitschrift Nature Ecology and Evolution. Die neue Methode könnte unter anderem helfen, den weltweiten Artenschutz zu verbessern.
Mehr25.01.2019 | iDiv-Mitglieder, Medienmitteilung, Molekulare Interaktionsökologie, TOP NEWS
Trickreiche Methode im Nachbarschaftsstreit
Leipzig. Ihren Fraßfeinden davonrennen können Pflanzen nicht. Doch viele Arten haben ihre ganz eigene Methode, sich zu verteidigen: Sie produzieren chemische Substanzen, die hungrigen Krabbeltieren nicht gut bekommen. Auf diese Weise setzt sich auch der Wilde Tabak gegen die Raupen des Tabakschwärmers zur Wehr. Dass es sich dabei für eine Pflanze lohnen kann, die Plagegeister einige Tage lang zu ertragen bevor sie die Abwehr startet, zeigt eine neue Studie unter der Leitung von Wissenschaftlern des Forschungszentrums iDiv, der Universität Jena und des UFZ. Denn auf diese Weise wechseln die Raupen genau dann zu einer benachbarten Pflanze, wenn sie so richtig Appetit bekommen – was Pflanze Nummer eins einen Vorteil im innerartlichen Konkurrenzkampf verschafft.
Mehr21.01.2019 | Experimentelle Interaktionsökologie, Medienmitteilung, sDiv, TOP NEWS
Mut zu weniger Reinlichkeit?
Leipzig, Raleigh. Gelten auf unserem Körper und in unseren Häusern die gleichen Gesetze der biologischen Vielfalt wie draußen in der Natur? Wenn ja, wären unsere aktuellen Hygienemaßnahmen zur Bekämpfung aggressiver Keime teilweise kontraproduktiv. Das schreibt ein interdisziplinäres Forscherteam vom Deutschen Zentrum für integrative Biodiversitätsforschung (iDiv), der Universität Leipzig und der Universität North Carolina State in der Fachzeitschrift Nature Ecology & Evolution. Es schlägt vor, die Rolle der Artenvielfalt verstärkt auch bei Mikroorganismen in den Ökosystemen Körper und Haus zu untersuchen. Die Erkenntnisse daraus könnten bisherige Strategien zur Bekämpfung von Infektionskrankheiten und resistenten Keimen auf den Kopf stellen.
Mehr05.11.2018 | Medienmitteilung, Nachhaltigkeit und Komplexität der Lebensräume von Menschenaffen, TOP NEWS
Wissenschaftler widersprechen: Orang-Utan-Populationen haben nicht zugenommen
Leipzig/Brunei. Die Orang-Utan-Populationen nehmen nach wie vor rapide ab, auch wenn die indonesische Regierung behauptet, die Lage für die Menschenaffen habe sich verbessert. In der Fachzeitschrift Current Biology kritisiert ein Team von Wissenschaftlern, darunter Maria Voigt vom Deutschen Zentrum für integrative Biodiversitätsforschung (iDiv) und dem Max-Planck-Institut für Evolutionäre Anthropologie, dass ungeeignete Methoden verwendet worden seien, um die Orang-Utan-Populationen zu erfassen. Die Forscher fordern die konsequente Anwendung wissenschaftlich fundierter Methoden für ein zuverlässiges Monitoring der Menschenaffen.
Mehr27.09.2018 | iDiv, Medienmitteilung, TOP NEWS
Neuer Professor für Biodiversitätsökonomik: Martin Quaas komplettiert Forschungszentrum iDiv
Leipzig. Das Deutsche Zentrum für integrative Biodiversitätsforschung (iDiv) Halle-Jena-Leipzig und die Wirtschaftswissenschaftliche Fakultät der Universität Leipzig bekommen eine neue gemeinsame Professur: Martin Quaas beginnt am 1. Oktober seine Arbeit als Professor für Biodiversitätsökonomik. Quaas erforscht die Wechselwirkungen von Wirtschaft und Biodiversität – zum Beispiel die Auswirkung von Fangquoten auf die Einkommen von Fischern und die Bestände mariner Fischarten. Quaas komplettiert eine Gruppe von neun Professoren, die eigens für den Aufbau des 2012 gegründeten DFG-Forschungszentrums iDiv berufen wurden.
Mehr26.09.2018 | Medienmitteilung, sDiv, TOP NEWS
Neues Zuhause in der Arktis: Mit dem Klimawandel halten höherwüchsige Pflanzen in der Tundra Einzug
Frankfurt/ Leipzig, den 24.09.2018. Die Arktis ist bislang eine Domäne niedrigwüchsiger Gräser und Zwergsträucher. Um den harten Umweltbedingungen zu widerstehen, kauern sie sich dicht an den Boden und werden oft nur wenige Zentimeter hoch. Zunehmend breiten sich hier jedoch neue, größere Pflanzenarten aus. Daher sind in der arktischen Tundra in den letzten 30 Jahren deutlich höherwüchsige Pflanzengemeinschaften entstanden. Das berichtet eine Gruppe von fast 130 internationalen Biologen unter der Leitung des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) und des Senckenberg Biodiversität und Klima Forschungszentrums heute im Fachmagazin Nature.
Mehr21.08.2018 | iDiv, Medienmitteilung, TOP NEWS
Insektensterben überall … auch unter unseren Füßen?
Gibt es das Insektensterben auch im Boden und was können wir zum Schutz der Artenvielfalt tun? Ein Wissenschaftler und ein Naturschützer widmen sich diesen Fragen in zwei öffentlichen Vorträgen am 27. August um 18 Uhr in der Bio City Leipzig an der Alten Messe. Die Vorträge des iDiv-Wissenschaftlers Nico Eisenhauer und des NABU-Leipzig-Vorsitzenden René Sievert sind Startschuss für eine Wanderausstellung der UN-Dekade Biologische Vielfalt, die bis zum 5. Oktober im Forum der Biocity zu sehen sein wird.
Mehr06.08.2018 | iDiv, Medienmitteilung, TOP NEWS
„Frankfurter Erklärung“ zum Schutz der Artenvielfalt
Basierend auf einer Medienmitteilung von Senckenberg: Frankfurt. In Deutschland zeigt sich in den letzten Jahrzehnten ein dramatischer Artenverlust in einzelnen Organismengruppen. Angesichts dieser Besorgnis erregenden Entwicklung plädieren in der heute veröffentlichten „Frankfurter Erklärung“ 22 renommierte WissenschaftlerInnen aus ganz Deutschland für eine langfristige, stärker interdisziplinär ausgelegte Forschung zum Erhalt der Artenvielfalt in Deutschland. Die Erklärung ist das Ergebnis eines Symposiums im Frankfurter Senckenberg Biodiversität und Klima Forschungszentrum, das auf Initiative des Bundesministeriums für Bildung und Forschung (BMBF) stattfand. Auch mehrere iDiv-Wissenschaftler haben die „Frankfurter Erklärung“ unterzeichnet.
Mehr01.08.2018 | iDiv-Mitglieder, Medienmitteilung, TOP NEWS
Tiere und Pilze fördern Leistungen von Wäldern
Leipzig, Halle. Eine neue Studie zeigt, dass neben der Vielfalt der Baumarten auch jene der Tier- und Pilzarten entscheidenden Einfluss hat auf die Leistungen von Wäldern. Zu diesen gehören unter anderem Holzproduktion, CO2-Speicherung und Klimaregulation. Die Studie basiert auf zehn Jahren Forschung in artenreichen Wäldern der Subtropen. Ein Forscherteam unter Federführung des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) und der Martin-Luther-Universität Halle-Wittenberg hat die Ergebnisse in der neuen Ausgabe der Zeitschrift Nature Communications veröffentlicht. Sie verdeutlichen, dass Biodiversität ganzheitlich betrachtet werden muss, um die Leistungsfähigkeit von Wäldern zu erhalten.
Mehr24.07.2018 | Biodiversität und Naturschutz, Medienmitteilung, TOP NEWS
Viel Lebensraum für Bären in Europa
Leipzig/Halle. Große Chance für europäische Braunbären: Eine neue Studie unter Leitung des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) und der Martin-Luther-Universität Halle-Wittenberg (MLU) zeigt, dass es in Europa viele Gebiete gibt, in denen keine Bären mehr leben, die sich aber grundsätzlich wieder als Lebensraum eignen würden. Nachdem sich die potentiellen Lebensbedingungen für Bären in vielen europäischen Staaten verbessert haben – zum Beispiel durch weniger Bejagung – sei es wahrscheinlich, dass künftig Tiere in einige dieser Gebiete einwanderten, so der Studienleiter. Wichtig sei es nun, vorausschauend Maßnahmen zu ergreifen, um Konflikte zwischen Bären und Menschen zu vermeiden.
Mehr04.07.2018 | Experimentelle Interaktionsökologie, Medienmitteilung, TOP NEWS
Schnecken-Shuttle-Service für Milben
Leipzig. Auf der Speisekarte von Nacktschnecken stehen nicht nur Moose, Flechten und Gartengemüse, sondern auch winzig kleine Hornmilben, die sie unweigerlich mit ihrer Nahrung aufnehmen. Erstaunlicherweise überstehen die meisten der kleinen Spinnentiere die Reise durch den Schneckendarm unbeschadet und werden an einem anderen Ort im Ökosystem wieder lebend ausgeschieden. Wissenschaftler um Dr. Manfred Türke vom Deutschen Zentrum für integrative Biodiversitätsforschung (iDiv) und der Universität Leipzig haben erstmalig bei Milben diese Ausbreitungsstrategie entdeckt, die in der Fachwelt als Endozoochorie („Verdauungsausbreitung“) vor allem bei Pflanzen bekannt ist. Ihre Forschungsergebnisse haben die Forscher in der Fachzeitschrift Oecologia veröffentlicht.
Mehr04.06.2018 | Evolution und Adaptation, Medienmitteilung, TOP NEWS
Forschungszentrum iDiv wächst weiter – Niederländische Evolutionsbiologin baut neue Juniorgruppe auf
Leipzig. Das Deutsche Zentrum für integrative Biodiversitätsforschung (iDiv) wächst weiter. Die Niederländische Biologin Dr. Renske Emilie Onstein leitet ab Juni die neue Junior-Forschungsgruppe „Evolution und Adaptation“, die mit Büro und Labor in der Leipziger Bio City ansässig sein wird. Die Botanikerin wird mit ihrem Team anhand von Blütenpflanzen und fruchtfressenden Tieren untersuchen, wie sich Arten bilden und welche Faktoren dabei eine Rolle spielen. Dieses Wissen ist wichtig, um vorherzusagen, wie sich die biologische Vielfalt an den globalen Wandel anpassen kann.
Mehr15.05.2018 | Biodiversität und Naturschutz, Biodiversität und Naturschutz, Medienmitteilung, TOP NEWS
Die neue „Seidenstraße“ bringt Herausforderungen und Chancen für den Erhalt der Biodiversität
London. Die chinesische Regierung plant, ein neues weltweites Handels- und Logistiknetzwerk zu etablieren. In einem Artikel, der in dieser Woche in der renommierten Zeitschrift Nature Sustainability veröffentlicht wurde, argumentiert ein internationales Forscherteam, dass der Umweltschutz für die Initiative „Neue Seidenstraße“ Priorität haben sollte. Dieses chinesische Projekt wäre somit nicht nur eine Investition zur Förderung des internationalen Handels, sondern auch eine Chance für eine nachhaltige Entwicklung. Zum Team, das eine umfassende strategische Umwelt- und Sozialverträglichkeitsprüfung fordert, gehören Forscher des Portugiesischen Forschungszentrums für Biodiversität und Genetische Ressourcen (CIBIO-InBIO), der Martin-Luther-Universität Halle-Wittenberg (MLU) und des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv).
Mehr26.04.2018 | Medienmitteilung, Nachhaltigkeit und Komplexität der Lebensräume von Menschenaffen, TOP NEWS
Gorillas und Schimpansen: Mehr als erwartet, dennoch gefährdet
Basierend auf einer Pressemitteilung der Wildlife Conservation Society (WCS): New York/Leipzig. Einer Studie zufolge leben in Afrikas Wäldern schätzungsweise noch immer mehr als 360.000 Gorillas und knapp 130.000 Schimpansen – das sind ein Drittel bzw. ein Zehntel mehr als ursprünglich angenommen. Allerdings leben rund 80 Prozent dieser Menschenaffen außerhalb von Schutzgebieten und der Bestand an Gorillas nimmt jährlich um rund 2,7 Prozent ab. Um die Menschenaffen zu retten, müssen die Wilderei, illegale Rodungen und die Zerstörung des Lebensraumes gestoppt werden. Für die neue Studie haben Natur- und Umweltschützer verschiedener Organisationen und Regierungsbehörden Daten über Populationen des Westlichen Flachlandgorillas und des Zentralafrikanischen Schimpansen gesammelt. Es ist die größte jemals durchgeführte Studie über diese Menschenaffen, die ausschließlich im westlichen Zentralafrika leben. Insgesamt nahm die Feldarbeit 167 Personenjahre in Anspruch; die dabei von den Wissenschaftlern zu Fuß zurückgelegten Wege waren länger als die Nord-Süd-Achse Afrikas. Die Studie wurde in der Fachzeitschrift Science Advances veröffentlicht und entstand unter der Leitung der Wildlife Conservation Society (WCS). Zu den Autoren zählt Dr. Hjalmar Kühl vom Deutschen Zentrum für integrative Biodiversitätsforschung (iDiv) und dem Max-Planck-Institut für evolutionäre Anthropologie (MPI-EVA).
Mehr09.03.2018 | Biodiversität und Naturschutz, Medienmitteilung, TOP NEWS
Der Luchs ist zurück im Thüringer Wald
Leipzig/Oberschönau. Wissenschaftler des Forschungszentrums iDiv und der Martin-Luther-Universität Halle-Wittenberg (MLU) haben mit Unterstützung eines ortsansässigen Naturschützers im Thüringer Wald den Luchs nachgewiesen. Nördlich von Oberschönau wurde ein erwachsenes Tier mit Hilfe einer Kamerafalle fotografiert. Damit ist die Rückkehr des scheuen Beutegreifers in den Thüringer Wald 200 Jahre nach seinem Verschwinden erneut nachgewiesen.
Mehr05.03.2018 | iDiv-Mitglieder, Medienmitteilung, TOP NEWS
Gemeinsame Medienmitteilung von iDiv, Senckenberg und UFZ
Wissenschaftler sind sich einig: Die Zeit zum Handeln ist jetzt
Dresden. Im Rahmen einer Anhörung im Sächsischen Landtag am 2. März 2018 zu den Ursachen des Insektensterbens und möglichen Gegenmaßnahmen wurden unter anderem Wissenschaftler von iDiv, der Senckenberg Gesellschaft für Naturforschung und dem UFZ gehört. Einhellig betonten sie die Notwendigkeit, zügig zu handeln. Nach Aussage der Wissenschaftler sind sowohl Ausmaß und Tragweite des Insektenschwunds als auch dessen wesentliche Ursachen unbestritten.
Mehr21.12.2017 | Experimentelle Interaktionsökologie, Medienmitteilung, TOP NEWS
Klimawandel: Selbstverstärkender Effekt nicht durch Bodentiere erklärbar
Leipzig. Wenn sich Erdboden erwärmt, setzt er vermehrt Kohlendioxid (CO2) frei – ein Effekt, der den Klimawandel zusätzlich anheizt. Bisher hatte man angenommen, der Grund hierfür sei vor allem in kleinen Bodentieren und Mikroorganismen zu suchen, die bei wärmeren Temperaturen mehr fressen und atmen würden. Eine neue Studie in Nature Climate Change zeigt jedoch, dass dies nicht zutrifft. Im Gegenteil: Kommt zur Wärme auch noch Trockenheit hinzu, fressen die Bodentiere sogar weniger. Um die Vorhersagekraft von Klimamodellen zu verbessern, sei es nun dringend notwendig, die biologischen Vorgänge im Boden besser zu erforschen, so die Wissenschaftler.
Mehr17.11.2017 | Forschung, iDiv-Mitglieder, iDiv-Mitglieder, Medienmitteilung, Medienmitteilung, Forschung, TOP NEWS, TOP NEWS
Bedeutung von Biodiversität in Wäldern könnte mit Klimawandel zunehmen
Leipzig. Wälder erfüllen zahlreiche wichtige Funktionen dann besonders gut, wenn sie reich an unterschiedlichen Baumarten sind. Dies ist das Ergebnis einer neuen Studie. Zudem muss man sich bei der Bewirtschaftung des Waldes nicht für ausschließlich eine Leistung – wie Holzproduktion oder Naturschutz – entscheiden, wie eine zweite Studie zeigt: Mehrere Leistungen von Waldökosystemen lassen sich gleichzeitig verbessern. Beide Studien wurden unter Federführung der Universität Leipzig und des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) durchgeführt und in der renommierten Zeitschrift Ecology Letters veröffentlicht.
Mehr17.07.2017 | Biodiversitätstheorie, Medienmitteilung, Medienmitteilung, Biodiversitätstheorie, TOP NEWS, TOP NEWS
Warum Tyrannosaurus eine lahme Ente war
Ein Käfer ist langsamer als eine Maus ist langsamer als ein Kaninchen ist langsamer als ein Gepard ist… langsamer als ein Elefant? Nein! Schneller als ein Gepard ist kein anderes Tier an Land – der Elefant ist zwar größer, aber langsamer. Bei kleinen bis mittelgroßen Tieren bedeutet größer auch schneller, doch bei richtig großen Tieren geht es mit der Geschwindigkeit wieder bergab. Wie dieser parabelartige Zusammenhang zwischen Körpergröße und Geschwindigkeit zustande kommt, hat nun ein Forscherteam unter der Leitung des Deutschen Zentrums für integrative Biodiversitätsforschung (iDiv) und der Friedrich-Schiller-Universität Jena erstmals in einem mathematischen Modell beschrieben und dieses in der renommierten Fachzeitschrift „Nature Ecology and Evolution“ vorgestellt.
Mehr